| Issue |
Med Sci (Paris)
Volume 30, Number 2, Février 2014
|
|
|---|---|---|
| Page(s) | 173 - 178 | |
| Section | M/S Revues | |
| DOI | https://doi.org/10.1051/medsci/20143002015 | |
| Published online | 24 février 2014 | |
L’effet de position télomérique
Silence dans le fond !
The telomere position effect: silence in the back row!
Altérations génétiques et épigénétiques des génomes, Institut de Duve, université catholique de Louvain, avenue Hippocrate 75, 1200 Bruxelles, Belgique
*
Cette adresse e-mail est protégée contre les robots spammeurs. Vous devez activer le JavaScript pour la visualiser.
Résumé
L’hétérochromatine présente différentes marques épigénétiques dont l’effet est de réprimer la transcription. En l’absence de barrières spécialisées, ces marques répressives peuvent se propager aux nucléosomes voisins et réprimer la transcription des régions adjacentes. Ainsi, dans diverses espèces, l’insertion d’un gène rapporteur à proximité des télomères le réduit au silence. Ce phénomène de répression transcriptionnelle induite par la propagation de l’hétérochromatine télomérique a été appelé effet de position télomérique. La répression transcriptionnelle est également observée au niveau de locus endogènes, mais elle est atténuée par la présence de barrières subtélomériques naturelles. Cet article passe en revue les arguments actuels en faveur de l’effet de position télomérique, de la levure à l’homme.
Abstract
Heterochromatin displays repressive histone marks that down-regulate transcription. In the absence of specialized barriers, these repressive marks spread onto nearby nucleosomes and induce transcriptional silencing of these regions. Accordingly, in various species, transgenes that are experimentally inserted directly next to telomeric repeats are silenced. Transcriptional repression induced by the spreading of telomeric heterochromatin is known as the “telomere position effect”. Although it is attenuated by the presence of natural subtelomeric barriers acting against the spreading of telomeric heterochromatin, telomere-induced silencing is also observed at the level of endogenous loci where it was initially proposed to provide a mean to regulate gene expression during senescence. This, however, remains to be formally demonstrated. Here, I review the current evidences for a telomere position effect, from yeast to human.
© 2014 médecine/sciences – Inserm
Euchromatine, hétérochromatine et barrières contre la propagation de l’hétérochromatine
Les chromosomes comportent deux types de chromatine distincts : une chromatine dite ouverte, ou euchromatine, et une chromatine plus compacte, appelée hétérochromatine (HC) [1]. De nombreuses études ont montré que ces deux types de chromatine se distinguent par l’espacement des nucléosomes, les modifications d’histone, l’état de méthylation de l’ADN, la localisation dans le noyau et la liaison de certaines protéines spécialisées.
L’euchromatine se caractérise par une abondance des marques d’histone dites activatrices, comme l’acétylation des lysines 9 ou 14 de l’histone H3 (H3K9ac, H3K14ac) ou la triméthylation de la lysine 4 (H3K4me3). De ce fait, ce type de chromatine est classiquement considéré comme transcriptionnellement compétent [1]. À l’inverse, l’HC est qualifiée de silencieuse. Elle peut être facultative ou constitutive. L’HC constitutive se retrouve principalement au niveau des régions péricentromériques des chromosomes et des télomères. Typiquement, l’HC est enrichie en résidus lysine 9 de l’histone H3 portant trois groupements méthyl (H3K9me3) ; ces derniers servent de point d’ancrage aux protéines HP1 (heterochromatin protein 1). Par leur formation de dimères, les protéines HP1 jouent un rôle crucial dans la compaction de la chromatine en formant des ponts moléculaires entre nucléosomes voisins. H4K20me3 est une autre marque typique de l’HC. De plus, les dinucléotides CpG présents au niveau de l’ADN des régions hétérochromatiniennes sont généralement méthylés.
Les marques répressives H3K9me3 et HP1 ont la capacité de se propager de proche en proche au sein de l’HC. Cette propagation des marques répressives est expliquée par la liaison d’HP1 aux résidus H3K9me3 et la capacité des molécules d’HP1 à recruter, à leur tour, l’histone méthyltransférase (HMT) [31] capable de triméthyler H3K9, créant ainsi de nouveaux sites de liaison pour HP1 (Figure 1) [1]. Une boucle de renforcement de l’HC se met alors en place qui participe à la propagation des marques répressives aux nucléosomes voisins. Si aucune barrière à la propagation de l’HC n’existait, ce type de chromatine pourrait, en théorie, se propager à l’ensemble des chromosomes. Outre le cas particulier du chromosome X inactif des cellules femelles, ce phénomène n’est pas observé. Ceci s’explique par la liaison de protéines spécialisées agissant comme barrières aux frontières de régions chromosomiques à HC. Ces barrières recrutent des histones acétlyltransférases (HAT) capables de s’opposer à l’action des HMT (Figure 1). Une des barrières les mieux caractérisées est sans doute celle assurée par la liaison de la protéine insulatrice CTCF (CCCTC-binding factor [zinc finger protein]) [2].
 |
Figure 1. Organisation des régions à hétérochromatine et euchromatine. L’hétérochromatine se caractérise par la présence de marques répressives, telles que H3K9me3 et HP1. La liaison d’HP1 aux résidus H3K9me3 permet le recrutement, par HP1 elle-même, d’histones méthyltransférases (HMT) qui vont, à leur tour, permettre la triméthylation d’H3K9 et la propagation des marques d’hétérochromatine aux nucléosomes voisins. Cette propagation est empêchée par la présence de barrières, ou insulateurs, qui, en recrutant des histones acétyltransférases (HAT), permettent de s’opposer à l’action des HMT. Le modèle présente le cas des locus insulateurs assurés par la liaison de CTCF où les régions à hétérochromatine sont en contact avec les lamines jouxtant la membrane nucléaire. ARN Pol : ARN polymérase. |
Découverte de l’effet de position télomérique chez la mouche
Bien avant la découverte du phénomène de propagation de l’HC, des expériences de complémentation d’un défaut de la couleur des yeux chez des mutants white de Drosophila melanogaster avaient identifié un lien entre la position de l’insertion d’un transgène dans le chromosome et son niveau d’expression, un phénomène décrit sous le nom de position effect variegation (PEV). Dans ces études, les auteurs ont montré que l’ADN du locus white sauvage n’était pas toujours capable de complémenter le phénotype white- des mouches mutantes [3, 4]. Des expériences d’hybridation in situ ont alors révélé que ce défaut de complémentation pouvait résulter de l’insertion de l’ADN white à proximité immédiate de régions péricentromériques ou de répétitions télomériques. Dans ce dernier cas, le PEV a été appelé effet de position télomérique ou TPE (telomere position effect). Plus tard, le modèle qui a émergé de ces observations était que l’environnement répressif de la chromatine télomérique pouvait s’étendre au transgène et réprimer sa transcription. Ainsi, l’insertion expérimentale d’un transgène à proximité immédiate des télomères de la mouche était capable de réprimer son niveau de transcription. Les télomères de la mouche présentent toutefois une structure et une régulation distinctes de celles de la plupart des autres espèces, puisqu’ils sont maintenus par un mécanisme de transposition indépendant de la télomérase. Dès lors, sur la base de ces observations, il était difficile de généraliser le TPE à toutes les espèces eucaryotiques avant de l’avoir formellement testé.
L’effet de position télomérique chez la levure
Plusieurs années après sa découverte chez la mouche, le TPE a été démontré expérimentalement chez la levure Saccharomyces cerevisiae en positionnant un gène rapporteur à proximité d’un télomère à la suite de la fragmentation du chromosome VII-L [5]. Combinée à la puissance de la génétique de levure, l’utilisation de ces systèmes expérimentaux d’extrémités chromosomiques tronquées a permis l’identification de plus de 50 gènes impliqués dans la régulation du TPE [6]. Parmi ceux-ci, on trouve les membres du complexe SIR (silent information regulator), les protéines Ku et la protéine Rap1 (repressor activator protein 1) qui se lie directement à l’ADN télomérique. On a ainsi pu montrer que la première étape de la propagation de l’HC télomérique est le recrutement de SIR4 par Rap1. Une fois recrutée au télomère, SIR4 interagit avec SIR3. À leur tour, SIR3 et SIR4 recrutent SIR2, une histone désacétylase (HDAC). La désacétylation des extrémités amino-terminales des histones renforce la liaison de SIR3 et SIR4 à la chromatine télomérique, et permet la propagation de la chromatine répressive vers les régions subtélomériques. Très vite, il est également apparu que le pouvoir de répression des télomères augmentait avec leur longueur, un phénomène attribué à un recrutement plus important des protéines SIR [6]. Sachant que, chez les espèces ne présentant pas d’expression constitutive de la télomérase, comme l’homme, la longueur des télomères diminue avec l’âge, cette observation a suggéré que la transcription de gènes endogènes présents aux extrémités chromosomiques pouvait être régulée au cours du vieillissement. Cette hypothèse a suscité beaucoup d’enthousiasme et stimulé la recherche de preuves en faveur d’un TPE endogène.
Plusieurs années après la découverte du TPE à partir de transgènes télomériques, il est apparu que la répression induite par les extrémités chromosomiques natives de la levure était probablement régulée différemment [7, 8]. En effet, les subtélomères de S. cerevisiae comportent tous des éléments appelés X, et plus de la moitié d’entre eux possèdent également l’élément Y’. Ainsi, le TPE endogène aux extrémités présentant uniquement des éléments X est variable en intensité, allant de niveaux comparables à ceux observés aux télomères expérimentalement tronqués à des niveaux 100 fois inférieurs [7] (Figure 2A–C). Ces différences semblent s’expliquer par la présence ou non, au niveau des éléments X, d’éléments STAR (subtelomeric antisilencing region) agissant comme barrière [8]. De plus, alors que la répression de gènes rapporteurs diminue progressivement avec l’éloignement du télomère, en étant toujours faiblement présente à 5 kb de celui-ci (Figure 2A), le TPE natif, lorsqu’il est observé, diminue de façon brutale et n’est plus détecté à 4 kb du télomère [7] (Figure 2B). Lorsque le subtélomère de levure comprend également un élément Y’ (qui est, lui, toujours associé à un élément STAR), le TPE est inexistant au sein de cet élément, et ce même si Y’ est à proximité immédiate (1 kb) du télomère. Toutefois, le TPE reste possible plus loin, au niveau d’un élément X présent sur le même subtélomère, suggérant dès lors la coexistence d’éléments propagateurs et insulateurs responsables d’un TPE discontinu à certaines extrémités chromosomiques (Figure 2D) [7, 8]. Ces travaux ont donc révélé l’existence de mécanismes de protection contre le TPE aux extrémités natives des chromosomes.
 |
Figure 2. Propagation de l’hétérochromatine télomérique : systèmes expérimentaux et extrémités natives. A. Les systèmes expérimentaux d’étude du TPE font appel à des transgènes télomériques initialement portés par des plasmides comportant des répétitions télomériques. Lorsque ces constructions sont introduites dans la cellule, le subtélomère et le télomère natifs du chromosome où a lieu l’insertion sont remplacés par l’ADN plasmidique. Dans ce cas, les éléments régulateurs des subtélomères naturels sont perdus et la propagation de l’hétérochromatine télomérique est généralement exacerbée. B-D. Aux extrémités natives des chromosomes, plusieurs situations sont observées : le subtélomère comprend un ou plusieurs élément(s) propagateur(s) de l’hétérochromatine et l’expression de gènes subtélomériques peut être réprimée (B) ; un élément insulateur est présent en amont des répétitions télomériques et bloque la propagation de l’hétérochromatine télomérique (C) ; ou des éléments propagateurs et insulateurs coexistent au sein du même subtélomère, donnant lieu à un TPE discontinu (D) . |
La découverte du rôle crucial de l’HDAC SIR2 dans le TPE chez la levure S. cerevisiae a suggéré que l’acétylation des histones pourrait procurer une barrière importante contre la propagation de l’HC télomérique. Chez cette même levure, il semble que le variant d’histone H2A.Z puisse également constituer un rempart important contre la propagation de l’HC télomérique et protéger les gènes proches des télomères de la répression transcriptionnelle [9]. À l’inverse de la levure S. cerevisiae qui ne présente ni marque H3K9me3, ni protéine de la famille HP1, Schizosaccharomyces pombe possède ces deux caractéristiques. Ainsi, l’HMT Clr4 de S. pombe méthyle le résidu H3K9, permettant ainsi la liaison de Swi6, l’homologue d’HP1 requis pour le TPE chez S. pombe [10, 11]. Le recrutement de Swi6 aux télomères requiert également Taz1, une protéine de la famille des TRF (telomere repeat factor), et Rap1 [11]. Une autre caractéristique de S. pombe est l’existence d’un deuxième mécanisme de recrutement de Swi6 aux subtélomères. Ce dernier dépend de la machinerie d’ARN interférence (non opérationnelle chez S. cerevisiae) et permet la propagation de l’HC télomérique sur des distances de 45 à 75 kb [11]. Toutes ces données convergent vers une régulation du TPE par les modifications post-traductionnelles des histones et par les variants d’histones.
L’effet de position télomérique chez l’homme
L’observation faite chez la levure de l’existence d’un lien entre longueur des télomères et expression des gènes présents aux extrémités chromosomiques a mené, dès le début des années 1990, Wright et Shay à proposer un modèle dans lequel le TPE participerait, chez l’homme, à la régulation de la sénescence cellulaire induite par le raccourcissement des télomères [12]. Le raccourcissement des télomères, associé à la sénescence cellulaire, pourrait ainsi activer l’expression de gènes subtélomériques. La mise en évidence du TPE chez l’homme s’est faite initialement à l’aide de transgènes télomériques. Après des premiers essais infructueux réalisés avec un gène rapporteur se situant à 4 kb du télomère [13], un transgène télomérique placé à proximité immédiate des répétitions télomériques a permis la première mise en évidence d’un TPE humain [14]. En accord avec un rôle des modifications d’histones, la répression transcriptionnelle du transgène était sensible au traitement par la trichostatine A, un inhibiteur de l’HDAC, et augmentait avec la longueur des télomères [14]. Des résultats similaires à ceux décrits dans cette étude ont été obtenus peu de temps après, et il a de plus été proposé que les protéines HP1α et β pourraient participer à la répression du transgène télomérique [15]. En accord avec le rôle de l’acétylation des histones dans le blocage de la propagation de l’HC télomérique, une étude plus récente a montré que l’expression de la luciférase à partir d’un transgène adjacent aux télomères était régulée par SIRT6 (Sirtuin 6), une HDAC humaine de la famille de SIR2 [16]. Une autre observation intéressante a été que le recrutement expérimental, entre les télomères et un gène rapporteur, de CTF1 (CCAAT-box-binding transcription factor 1), un facteur de transcription doté d’activité de remodelage de la chromatine, était capable de protéger le transgène de la répression transcriptionnelle induite par l’HC télomérique [17]. Des observations similaires avaient été faites au préalable chez la levure [18], suggérant à nouveau une conservation des mécanismes de régulation du TPE.
La démonstration de l’existence d’un TPE sur des transgènes avait-elle la moindre signification physiologique ? Pour tenter de répondre à cette question, une analyse systématique de la transcription des gènes les plus distaux connus au début des années 2000, et situés entre 13- et 376 kb du télomère de différents chromosomes, a été réalisée dans des fibroblastes jeunes (télomères longs) ou sénescents (télomères courts) [19]. Cette étude sur 34 gènes n’a pas révélé de régulation par la longueur des télomères. Alternativement, une autre équipe a tiré profit d’une microdélétion naturelle amenant le locus ATSA à 54 kb du télomère en 22q pour étudier le TPE endogène, mais à nouveau sans succès [20]. En 2009, cependant, l’effet répressif de la longueur des télomères sur l’expression du gène ISG15, situé à environ 1 Mb du télomère 1p, a été montré mais, étonnamment, cet effet n’était associé à aucune répression des gènes situés entre ISG15 et les répétitions télomériques, suggérant l’existence d’un TPE atypique [21]. La première démonstration d’un effet TPE endogène classique n’a été possible qu’à la suite de la découverte de la transcription des télomères humains en ARN non codants, appelés TERRA (telomeric repeat-containing RNA), dont les sites de démarrage de transcription sont situés entre 50 pb et 1,5 kb des premières répétitions télomériques [22–24]. Ainsi, notre équipe a montré que l’expression des TERRA était diminuée par une augmentation de la densité des marques H3K9me3 et d’HP1α aux télomères plus longs [24]. Cette augmentation de la densité des marques H3K9me3 est restreinte aux répétitions TTAGGG des télomères allongés et ne s’étend pas aux régions subtélomériques [24], ce qui renforce l’idée de l’existence de barrières capables de s’opposer à la propagation de l’HC télomérique. Il est raisonnable de penser que les sites de liaison de CTCF (CCCTC-binding factor), un facteur de transcription doté d’activité insulatrice, détectés dans la plupart des subtélomères humains [25], puissent jouer un rôle dans ce blocage de la propagation de l’HC télomérique (Figure 3A). Comme la liaison de CTCF s’accompagne d’une augmentation de la densité locale d’H2A.Z [26], cela pourrait suggérer que, à l’instar de ce qui a été observé chez la levure [9], ce variant d’histone contribuerait également aux barrières subtélomériques humaines.
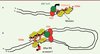 |
Figure 3. Un effet TPE en amont ou en trans ? A. La transcription des télomères humains produit des ARN non codants appelés TERRA qui sont impliqués dans l’hétérochromatinisation des télomères en recrutant des histones méthyltransférases et HP1 [30]. Chez l’homme, la propagation de l’hétérochromatine télomérique est probablement bloquée par les protéines insulatrices CTCF qui se lient directement en amont des répétitions télomériques où elles sont requises pour le recrutement de l’ARN polymérase II (ARN PolII). B. Suite au repliement de l’extrémité chromosomique, les molécules de TERRA pourraient induire l’hétérochromatinisation de régions plus internes des chromosomes (effet TPE en amont) et/ou de régions présentes sur d’autres chromosomes (effet TPE en trans). La dimérisation de molécules de CTCF pourrait être impliquée dans ce processus. |
L’importance de la présence de barrières naturelles contre la propagation de l’HC télomérique humaine a été à nouveau suggérée dans une étude récente décrivant l’existence d’un TPE endogène dans le cas particulier de la dystrophie facio-scapulo-humérale ou myopathie FSH [27]. La myopathie FSH est associée à une contraction pathologique des répétitions D4Z4 subtélomériques en 4q35, et à l’induction transcriptionnelle du locus DUX4 situé au sein de ces répétitions. Dans les cellules de ces patients, une répression transcriptionnelle sur DUX4 est observée avec l’allongement expérimental des télomères [27]. Comme les symptômes de la myopathie FSH ne se déclarent pas avant 20 ou 30 ans, cette découverte a permis de proposer que le raccourcissement des télomères lié à l’âge pourrait être un élément déclencheur de la myopathie FSH chez des personnes présentant une contraction de la région 4q35. Les raisons pour lesquelles le TPE devient possible au niveau de 4q35 chez les patients FSH ne sont pas connues, mais pourraient être liées à la perte de fonction de barrière de cette région subtélomérique altérée, à la perturbation du positionnement de 4q35 dans le noyau [28], ou à la formation de boucles de chromatine induites par le recrutement de CTCF aux motifs D4Z4 contractés [28, 29], un phénomène qui pourrait perturber l’organisation tridimensionnelle de cette extrémité chromosomique.
Conclusions : TPE or not TPE ?
La propension naturelle de l’HC à s’étendre aux régions chromosomiques voisines est limitée par la présence de barrières. L’HC télomérique n’échappe pas à la règle, et il est donc raisonnable de proposer que toutes les espèces eucaryotes aient élaboré des mécanismes de protection semblables contre la propagation de l’HC télomérique vers les régions subtélomériques. Les systèmes expérimentaux d’étude du TPE, faisant appel à des transgènes télomériques qui perturbent les barrières subtélomériques naturelles, sont donc peu physiologiques, et la répression transcriptionnelle qui en découle est sans doute exacerbée (Figure 2). Chez la levure S. cerevisiae, il semble néanmoins y avoir un rassemblement, aux subtélomères, de gènes impliqués dans la réponse au stress. Ces gènes sont normalement réprimés mais, en réponse à divers signaux, la répression transcriptionnelle peut être levée [6]. Cette répression réversible de la transcription des gènes subtélomériques peut être vue comme un moyen d’adaptation rapide à des conditions de stress. La régulation de la variation antigénique chez de nombreux pathogènes dont Trypanosoma, Leishmania, Plasmodium ou certaines levures du type Candida représente une autre situation où le TPE permet de mettre en place un programme de survie [6]. Dans ce cas, certains parasites peuvent échapper au système immunitaire en modulant l’expression de gènes subtélomériques codant pour des variants de glycoprotéines de surface.
Chez l’homme, en conditions non pathologiques, nos données suggèrent que le TPE en cis pourrait être restreint à la répression de l’expression de TERRA [24]. Les conséquences biologiques de cette modulation transcriptionnelle de TERRA par la longueur des télomères ne sont pas élucidées, mais la régulation de la transcription des télomères pourrait être importante dans le contrôle de la mobilité des télomères, de la formation de l’hétérochromatine télomérique ou de l’allongement des télomères. Toutefois, si le TPE est restreint à TERRA, comment expliquer les résultats de l’étude montrant une répression du locus IGS15 sans que les gènes situés entre ce locus et les télomères ne soient eux-mêmes réprimés [21] ? Une explication possible serait que, via l’action de boucles télomériques, comme celles initiées par la liaison de CTCF [2], l’HC télomérique puisse être capable de se propager à une région plus interne du même chromosome, ou d’un chromosome voisin, et induire un TPE en trans (Figure 3B). Si cette hypothèse est exacte, il se pourrait même que TERRA puisse en être responsable en recrutant, au locus ciblé, les enzymes de modification d’histone et les protéines HP1, comme proposé précédemment [30].
Les données très récentes de Stadler et al. [27] suggèrent néanmoins que, dans certaines conditions pathologiques de perturbation des subtélomères, comme dans la myopathie FSH, la répression transcriptionnelle dictée par le télomère puisse s’étendre sur plusieurs dizaines de kb en amont de celui-ci. Ceci souligne toute l’importance du bon fonctionnement des barrières subtélomériques naturelles contre la propagation de l’HC télomérique.
Liens d’intérêt
L’auteur déclare n’avoir aucun lien d’intérêt concernant les données publiées dans cet article.
Remerciements
Je tiens à remercier le Fonds national de la recherche scientifique (FNRS), l’Université catholique de Louvain et l’Institut de Duve pour leur soutien financier, ainsi que Nausica Arnoult pour ses commentaires pertinents sur cette revue.
Références
- Terranova R. L’hétérochromatine constitutive dans tous ses états. Med Sci (Paris) 2008 ; 24 : 720–724. [CrossRef] [EDP Sciences] [PubMed] [Google Scholar]
- Millau J-F, Gaudreau L. CTCF, cohesin, and histone variants: connecting the genome. Biochem Cell Biol 2011 ; 89 : 505–513. [CrossRef] [PubMed] [Google Scholar]
- Hazelrigg T, Levis R, Rubin GM. Transformation of white locus DNA in Drosophila: dosage compensation, zeste interaction, and position effects. Cell 1984 ; 36 : 469–481. [CrossRef] [PubMed] [Google Scholar]
- Gehring WJ, Klemenz R, Weber U, Kloter U. Functional analysis of the white gene of Drosophila by P-factor-mediated transformation. EMBO J 1984 ; 3 : 2077–2085. [PubMed] [Google Scholar]
- Gottschling DE, Aparicio OM, Billington BL, Zakian VA., Position effect at S. cerevisiae telomeres: reversible repression of Pol II transcription. Cell 1990 ; 63 : 751–762. [CrossRef] [PubMed] [Google Scholar]
- Ottaviani A, Gilson E, Magdinier F. Telomeric position effect: from the yeast paradigm to human pathologies? Biochimie 2008 ; 90 : 93–107. [CrossRef] [PubMed] [Google Scholar]
- Pryde FE, Louis EJ. Limitations of silencing at native yeast telomeres. EMBO J 1999 ; 18 : 2538–2550. [CrossRef] [PubMed] [Google Scholar]
- Fourel G, Revardel E, Koering CE, Gilson E. Cohabitation of insulators and silencing elements in yeast subtelomeric regions. EMBO J 1999 ; 18 : 2522–2537. [CrossRef] [PubMed] [Google Scholar]
- Guillemette B, Gaudreau L. H2A.Z : un variant d’histone qui orne les promoteurs des gènes. Med Sci (Paris) 2006 ; 22 : 941–946. [CrossRef] [EDP Sciences] [PubMed] [Google Scholar]
- Nakayama J, Rice JC, Strahl BD, et al. Role of histone H3 lysine 9 methylation in epigenetic control of heterochromatin assembly. Science 2001 ; 292 : 110–113. [CrossRef] [PubMed] [Google Scholar]
- Kanoh J, Sadaie M, Urano T, Ishikawa F. Telomere binding protein Taz1 establishes Swi6 heterochromatin independently of RNAi at telomeres. Curr Biol 2005 ; 15 : 1808–1819. [CrossRef] [PubMed] [Google Scholar]
- Wright WE, Shay JW. Telomere positional effects and the regulation of cellular senescence. Trends Genet 1992 ; 8 : 193–197. [CrossRef] [PubMed] [Google Scholar]
- Sprung CN, Sabatier L, Murnane JP. Effect of telomere length on telomeric gene expression. Nucleic Acids Res 1996 ; 24 : 4336–4340. [CrossRef] [PubMed] [Google Scholar]
- Baur JA, Zou Y, Shay JW, Wright WE. Telomere position effect in human cells. Science 2001 ; 292 : 2075–2077. [CrossRef] [PubMed] [Google Scholar]
- Koering CE, Pollice A, Zibella MP, et al. Human telomeric position effect is determined by chromosomal context and telomeric chromatin integrity. EMBO Rep 2002 ; 3 : 1055–1061. [CrossRef] [PubMed] [Google Scholar]
- Tennen RI, Bua DJ, Wright WE, Chua KF., SIRT6 is required for maintenance of telomere position effect in human cells. Nat Commun 2011 ; 2 : 433. [CrossRef] [PubMed] [Google Scholar]
- Esnault G, Majocchi S, Martinet D, et al. Transcription factor CTF1 acts as a chromatin domain boundary that shields human telomeric genes from silencing. Mol Cell Biol 2009 ; 29 : 2409–2418. [CrossRef] [PubMed] [Google Scholar]
- Ferrari S, Simmen KC, Dusserre Y, et al. Chromatin domain boundaries delimited by a histone-binding protein in yeast. J Biol Chem 2004 ; 279 : 55520–55530. [CrossRef] [PubMed] [Google Scholar]
- Ning Y, Xu JF, Li Y, et al. Telomere length and the expression of natural telomeric genes in human fibroblasts. Hum Mol Genet 2003 ; 12 : 1329–1336. [CrossRef] [PubMed] [Google Scholar]
- Ofir R, Wong AC, McDermid HE, et al. Position effect of human telomeric repeats on replication timing. Proc Natl Acad Sci USA 1999 ; 96 : 11434–11439. [CrossRef] [Google Scholar]
- Lou Z, Wei J, Riethman H, et al. Telomere length regulates ISG15 expression in human cells. Aging 2009 ; 1 : 608–621. [PubMed] [Google Scholar]
- Azzalin CM, Reichenbach P, Khoriauli L, et al. Telomeric repeat containing RNA and RNA surveillance factors at mammalian chromosome ends. Science 2007 ; 318 : 798–801. [CrossRef] [PubMed] [Google Scholar]
- Nergadze SG, Farnung BO, Wischnewski H, et al. CpG-island promoters drive transcription of human telomeres. RNA 2009 ; 15 : 2186–2194. [CrossRef] [PubMed] [Google Scholar]
- Arnoult N, Van Beneden A, Decottignies A. Telomere length regulates TERRA levels through increased trimethylation of telomeric H3K9 and HP1α. Nat Struct Mol Biol 2012 ; 19 : 948–956. [CrossRef] [PubMed] [Google Scholar]
- Deng Z, Wang Z, Stong N, et al. A role for CTCF and cohesin in subtelomere chromatin organization, TERRA transcription, and telomere end protection. EMBO J 2012 ; 31 : 4165–4178. [CrossRef] [PubMed] [Google Scholar]
- Fu Y, Sinha M, Peterson CL, Weng Z., The insulator binding protein CTCF positions 20 nucleosomes around its binding sites across the human genome. PLoS Genet 2008 ; 4 : e1000138. [CrossRef] [PubMed] [Google Scholar]
- Stadler G, Rahimov F, King OD, et al. Telomere position effect regulates DUX4 in human facioscapulohumeral muscular dystrophy. Nat Struct Mol Biol 2013 ; 20 : 671–678. [CrossRef] [PubMed] [Google Scholar]
- Ottaviani A, Schluth-Bolard C, Rival-Gervier S, et al. Identification of a perinuclear positioning element in human subtelomeres that requires A-type lamins and CTCF. EMBO J 2009 ; 28 : 2428–2436. [CrossRef] [PubMed] [Google Scholar]
- Ottaviani A, Rival-Gervier S, Boussouar A, et al. The D4Z4 macrosatellite repeat acts as a CTCF, A-type lamins-dependent insulator in facio-scapulo-humeral dystrophy. PLoS Genet 2009 ; 5 : e1000394. [CrossRef] [PubMed] [Google Scholar]
- Deng Z, Norseen J, Wiedmer A, et al. TERRA RNA binding to TRF2 facilitates heterochromatin formation and ORC recruitment at telomeres. Mol Cell 2009 ; 35 : 403–413. [CrossRef] [PubMed] [Google Scholar]
- Chaib H, Prébet T, Vey N, Collette Y. Histone méthyltransférases : une nouvelle classe de cibles thérapeutiques dans le traitement du cancer ? Med Sci (Paris) 2011 ; 27 : 725–732. [CrossRef] [EDP Sciences] [PubMed] [Google Scholar]
Liste des figures
 |
Figure 1. Organisation des régions à hétérochromatine et euchromatine. L’hétérochromatine se caractérise par la présence de marques répressives, telles que H3K9me3 et HP1. La liaison d’HP1 aux résidus H3K9me3 permet le recrutement, par HP1 elle-même, d’histones méthyltransférases (HMT) qui vont, à leur tour, permettre la triméthylation d’H3K9 et la propagation des marques d’hétérochromatine aux nucléosomes voisins. Cette propagation est empêchée par la présence de barrières, ou insulateurs, qui, en recrutant des histones acétyltransférases (HAT), permettent de s’opposer à l’action des HMT. Le modèle présente le cas des locus insulateurs assurés par la liaison de CTCF où les régions à hétérochromatine sont en contact avec les lamines jouxtant la membrane nucléaire. ARN Pol : ARN polymérase. |
| Dans le texte | |
 |
Figure 2. Propagation de l’hétérochromatine télomérique : systèmes expérimentaux et extrémités natives. A. Les systèmes expérimentaux d’étude du TPE font appel à des transgènes télomériques initialement portés par des plasmides comportant des répétitions télomériques. Lorsque ces constructions sont introduites dans la cellule, le subtélomère et le télomère natifs du chromosome où a lieu l’insertion sont remplacés par l’ADN plasmidique. Dans ce cas, les éléments régulateurs des subtélomères naturels sont perdus et la propagation de l’hétérochromatine télomérique est généralement exacerbée. B-D. Aux extrémités natives des chromosomes, plusieurs situations sont observées : le subtélomère comprend un ou plusieurs élément(s) propagateur(s) de l’hétérochromatine et l’expression de gènes subtélomériques peut être réprimée (B) ; un élément insulateur est présent en amont des répétitions télomériques et bloque la propagation de l’hétérochromatine télomérique (C) ; ou des éléments propagateurs et insulateurs coexistent au sein du même subtélomère, donnant lieu à un TPE discontinu (D) . |
| Dans le texte | |
 |
Figure 3. Un effet TPE en amont ou en trans ? A. La transcription des télomères humains produit des ARN non codants appelés TERRA qui sont impliqués dans l’hétérochromatinisation des télomères en recrutant des histones méthyltransférases et HP1 [30]. Chez l’homme, la propagation de l’hétérochromatine télomérique est probablement bloquée par les protéines insulatrices CTCF qui se lient directement en amont des répétitions télomériques où elles sont requises pour le recrutement de l’ARN polymérase II (ARN PolII). B. Suite au repliement de l’extrémité chromosomique, les molécules de TERRA pourraient induire l’hétérochromatinisation de régions plus internes des chromosomes (effet TPE en amont) et/ou de régions présentes sur d’autres chromosomes (effet TPE en trans). La dimérisation de molécules de CTCF pourrait être impliquée dans ce processus. |
| Dans le texte | |
Current usage metrics show cumulative count of Article Views (full-text article views including HTML views, PDF and ePub downloads, according to the available data) and Abstracts Views on Vision4Press platform.
Data correspond to usage on the plateform after 2015. The current usage metrics is available 48-96 hours after online publication and is updated daily on week days.
Initial download of the metrics may take a while.




