| Issue |
Med Sci (Paris)
Volume 22, Number 1, Janvier 2006
|
|
|---|---|---|
| Page(s) | 27 - 28 | |
| Section | Nouvelles | |
| DOI | https://doi.org/10.1051/medsci/200622127 | |
| Published online | 15 janvier 2006 | |
Mécanisme du transport des cations Na+ et K+ par la pompe à sodium
A third Na+ binding site in the sodium pump
Département de Pharmacologie et de Toxicologie, Faculté de Biologie et Médecine, Université de Lausanne, Bugnon 27, 1005 Lausanne, Suisse
*
Cette adresse e-mail est protégée contre les robots spammeurs. Vous devez activer le JavaScript pour la visualiser.
La Na+,K+-ATPase, ou pompe à sodium, est un constituant cellulaire essentiel au fonctionnement de pratiquement toutes les cellules animales. C’est le système de transport qui maintient un gradient électrochimique pour les deux principaux cations de nos liquides physiologiques : le sodium, qui a une concentration extracellulaire élevée et intracellulaire basse, et le potassium avec un gradient de concentration inverse. Des mutations dans l’une des isoformes (a2) de la Na+,K+-ATPase ont été récemment associées à une forme héréditaire de migraine sévère (FHM2, OMIM #602481) [1].
Par quel type de mécanique moléculaire s’effectue ce pompage de cations à travers la membrane ? Comment l’énergie libérée par l’hydrolyse d’une molécule d’ATP peut-elle être récupérée pour transporter des cations contre un gradient de concentration qui peut être parfois très élevé ? Ce sont des questions fondamentales de biophysique des protéines de membranes que nous espérons pouvoir résoudre. Nous avons récemment contribué à la compréhension de ce mécanisme de transport en définissant le site de liaison pour l’un des trois ions Na+ qui sont transportés [2].
La Na+,K+-ATPase appartient à la famille des P-ATPases (36 gènes dans le génome humain). Les membres de cette famille dont la fonction est connue sont des transporteurs de cations. Des progrès très importants ont été réalisés récemment dans ce domaine grâce à l’obtention de structure à haute résolution (par cristallographie aux rayons X) de l’une des P-ATPases, la pompe à calcium du réticulum sarcoplasmique et endoplasmique (SERCA) [3]. La sous-unité a de la Na+,K+-ATPase est suffisamment semblable à SERCA pour qu’une structure hypothétique raisonnablement fiable puisse être obtenue en modélisation par homologie. SERCA possède deux sites de liaison pour les ions calcium, et pour le modèle de la Na+,K+-ATPase obtenu par homologie indique clairement l’existence de deux sites homologues [4]. Ces sites sont localisés dans un domaine de la protéine qui est formé de 10 hélices α transmembranaires (M1-M10) (Figure 1). Chacun de ces sites est très probablement occupé alternativement par un ion Na+ et par un ion K+. Les résultats d’expériences de mutagenèse touchant les résidus proches confirment l’existence de ces sites cationiques entre les segments transmembranaires M4, M5 et M6 [5]. Mais la Na+,K+-ATPase échange trois ions Na+ contre deux ions K+ pour chaque molécule d’ATP hydrolysée. Il est donc nécessaire qu’un troisième ion sodium trouve sa place dans la partie transmembranaire de la protéine pour que le rapport d’échange de trois Na+ pour deux K+ soit réalisé. Plusieurs localisations avaient été proposées pour ce troisième site.
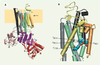 |
Figure 1. Structure moléculaire de la Na+,K+ ATPase. A. Ensemble de la structure tridimensionnelle de la Na+,K+-ATPase obtenue en modélisation par homologie à partir de la structure de SERCA en conformation E1. La position approximative de la membrane est indiquée par le bandeau horizontal jaune. Le côté extracellulaire de la membrane est en haut. Les hélices α de la protéine sont représentées par des cylindres. On distingue le faisceau de 10 segments transmembranaires (colorés en noir pour M1-M2, en gris pour M3-M4, en vert pour M5-M6, en jaune pour M7-M8 et en orange pour M9-M10) et les trois domaines intracellulaires principaux, A (actuator domain), N (domaine de liaison des nucléotides) et P (domaine de phosphorylation). La sous-unité β, dont on ne connaît pas la structure, n’est pas représentée. B. Focalisation sur la partie transmembranaire, vue de la direction indiquée par la flèche noire (en A dans le bandeau jaune). Les segments transmembranaires sont numérotés et colorés comme dans la partie gauche de la figure. Une partie des hélices transmembranaires M8 et M10 a été supprimée pour permettre une meilleure visualisation. Les quatre acides aminés impliqués dans la liaison du 3e ion Na+ sont représentés individuellement avec leur chaîne latérale. |
C’est en cherchant à préciser la nature des interactions entre la sous-unité α de la Na+,K+-ATPase et une protéine régulatrice - de la famille des protéines FXYD [6] - que nous avons découvert le rôle très important joué par un segment transmembranaire peu étudié jusque-là, M9, dans la mécanique du transport des cations. À la suite de l’observation de l’influence très importante d’une mutation (E961C) dans le segment M9 sur la concentration externe de Na+ intervenant dans le fonctionnement de la pompe à sodium, nous avons muté plusieurs acides aminés situés autour d’un des sites suggérés par Ogawa et Toyoshima [4], et étudié en détail les propriétés fonctionnelles de ces mutants par comparaison avec la forme normale de la sous-unité a [2]. Nous avons exprimé ces mutants dans l’ovocyte du xénope par injection d’ARN complémentaire et utilisé ensuite des techniques électrophysiologiques pour étudier la fonction de ces protéines. Tout d’abord, en raison de l’échange asymétrique de trois ions Na+ pour deux ions K+, l’activité de la pompe à sodium produit un courant mesurable en condition de potentiel imposé (voltage clamp). Cette activité peut alors être mesurée précisément en fonction des concentrations, intracellulaire ou extracellulaire, de Na+ et de K+, ce qui nous a permis d’estimer les affinités apparentes de ces cations pour leurs sites de liaison. Par la suite, en enregistrant les courants transitoires qui résultent de changements rapides de potentiel, on peut suivre, en temps réel, la cinétique des événements qui déplacent des charges dans le champ électrique transmembranaire, par exemple la libération d’un ion Na+ vers le milieu extracellulaire.
Les résultats de ces mesures convergent pour indiquer que des mutations touchant quatre des acides aminés étudiés produisent des modifications significatives de l’affinité apparente des ions sodium, surtout lorsque leur accès est étudié à partir de la solution extracellulaire, mais aussi à partir du milieu intracellulaire. Ces mutations ne modifient pas ou peu l’affinité apparente pour le K+. La cinétique de la libération du sodium vers le milieu extracellulaire est aussi significativement modifiée.
Ces résultats nous ont donc permis de proposer une localisation bien définie, pour un troisième site de liaison cationique, spécifique pour le sodium. Ce site se trouve entre les segments transmembranaires M5, M6 et M9 et, approximativement, au même niveau dans l’épaisseur de la membrane que les deux autres sites cationiques. Au cours d’un cycle de transport, deux ions Na+ cytoplasmiques viennent occuper les sites cationiques analogues à ceux identifiés dans la pompe à calcium (sites I et II) et un troisième ion Na+ vient, également à partir du côté cytoplasmique de la membrane, occuper le site (III) que nous avons localisé. Puis, à la suite d’un changement de conformation (de la conformation E1 vers la conformation E2), les ions Na+ sont relâchés du côté extracellulaire. Contrairement aux deux autres sites, qui sont alors occupés par des ions K+ à partir du milieu extracellulaire, le troisième site sodique reste inoccupé lors du retour vers la conformation E1, ce qui confère son caractère électrogénique à l’activité de la pompe à sodium.
Références
- De Fusco M, Marconi R, Silvestri L, et al. Haploinsufficiency of ATP1A2 encoding the Na+/K+ pump alpha 2 subunit associated with familial hemiplegic migraine type 2. Nat Genet 2003; 33 : 192–6. [Google Scholar]
- Li C, Capendeguy O, Geering K, et al. A third Na+ binding site in the sodium pump. Proc Natl Acad Sci USA 2005; 102 : 12706–11. [Google Scholar]
- Toyoshima C, Inesi G. Structural basis of ion pumping by Ca2+-ATPase of the sacroplasmic reticulum. Annu Rev Biochem 2004; 73 : 269–92. [Google Scholar]
- Ogawa H, Toyoshima C. Homology modeling of the cation binding sites of the Na+K+-ATPase. Proc Natl Acad Sci USA 2002; 99 : 15977–82. [Google Scholar]
- Horisberger JD. Recent insights into the structure and mechanism of the sodium pump. Physiology 2004; 19 : 377–87. [Google Scholar]
- Li CM, Grosdidier A, Crambert G, et al. Structural and functional interaction sites between Na, K-ATPase and FXYD proteins. J Biol Chem 2004; 279 : 38895–902. [Google Scholar]
© 2006 médecine/sciences - Inserm / SRMS
Liste des figures
 |
Figure 1. Structure moléculaire de la Na+,K+ ATPase. A. Ensemble de la structure tridimensionnelle de la Na+,K+-ATPase obtenue en modélisation par homologie à partir de la structure de SERCA en conformation E1. La position approximative de la membrane est indiquée par le bandeau horizontal jaune. Le côté extracellulaire de la membrane est en haut. Les hélices α de la protéine sont représentées par des cylindres. On distingue le faisceau de 10 segments transmembranaires (colorés en noir pour M1-M2, en gris pour M3-M4, en vert pour M5-M6, en jaune pour M7-M8 et en orange pour M9-M10) et les trois domaines intracellulaires principaux, A (actuator domain), N (domaine de liaison des nucléotides) et P (domaine de phosphorylation). La sous-unité β, dont on ne connaît pas la structure, n’est pas représentée. B. Focalisation sur la partie transmembranaire, vue de la direction indiquée par la flèche noire (en A dans le bandeau jaune). Les segments transmembranaires sont numérotés et colorés comme dans la partie gauche de la figure. Une partie des hélices transmembranaires M8 et M10 a été supprimée pour permettre une meilleure visualisation. Les quatre acides aminés impliqués dans la liaison du 3e ion Na+ sont représentés individuellement avec leur chaîne latérale. |
| Dans le texte | |
Current usage metrics show cumulative count of Article Views (full-text article views including HTML views, PDF and ePub downloads, according to the available data) and Abstracts Views on Vision4Press platform.
Data correspond to usage on the plateform after 2015. The current usage metrics is available 48-96 hours after online publication and is updated daily on week days.
Initial download of the metrics may take a while.




