| Issue |
Med Sci (Paris)
Volume 20, Number 2, Février 2004
|
|
|---|---|---|
| Page(s) | 213 - 218 | |
| Section | M/S revues | |
| DOI | https://doi.org/10.1051/medsci/2004202213 | |
| Published online | 15 février 2004 | |
SPO11 : une activité de coupure de l’ADN indispensable à la méiose
SPO11: an activity that promotes DNA breaks required for meiosis
Institut de génétique humaine, Cnrs UPR 1142, 141, rue de la Cardonille, 34396 Montpellier Cedex 05, France
*
Cette adresse e-mail est protégée contre les robots spammeurs. Vous devez activer le JavaScript pour la visualiser.
Résumé
La recombinaison entre chromosomes homologues est un processus essentiel dont le rôle mécanique est d’assurer la ségrégation réductionnelle des chromosomes lors de la première division de méiose. La protéine Spo11 est responsable du déclenchement de la recombinaison méiotique par formation de cassures double-brin de l’ADN, et cette activité est apparentée à celle des ADN topo-isomérases de type II. Spo11 et sa fonction ont été conservées au cours de l’évolution, de la levure à l’homme : chez tous les eucaryotes testés, les mutants spo11 sont déficients pour la recombinaison méiotique et ont une fertilité réduite, voire nulle. Cette stérilité reflète selon les cas un dysfonctionnement de la ségrégation des chromosomes ou un arrêt de la différenciation germinale. L’étude phénotypique des différents mutants met en évidence un ensemble de régulations complexes entre la recombinaison et d’autres événements de la prophase de méiose, tels que l’appariement des chromosomes et le contrôle du cycle cellulaire méiotique.
Abstract
Recombination between homologous chromosomes during meiosis is an essential process, which mechanistical function is to ensure the reductional segregation of chromosomes at the first meiotic division. SPO11, one of the key genes directly involved in this process, has been at the origin of considerable interest for the past five years, for several reasons. First, Spo11 is responsible for the initiation of meiotic recombination through the formation of DNA double-strand breaks by a type II DNA topoisomerase-like activity. Moreover, Spo11, and its function, have been conserved through evolution, from yeasts to human, as demonstrated by the identification of members of the Spo11 protein family and the analyses of corresponding mutants. Indeed, for every eukaryote that has been tested, spo11 mutants are deficient for meiotic recombination and are partially or completely sterile. Depending on the species, this reduced fertility reflects either a defect in chromosome segregation, or an arrest response in germ cell differentiation. Similarities and differences from species to species uncover a complex set of regulations that coordinate recombination with other events of meiotic prophase, such as chromosome pairing and meiotic cell cycle.
© 2004 médecine/sciences - Inserm / SRMS
En première division de méiose, chaque paire de chromosomes homologues est connectée par au moins un événement de recombinaison réciproque, ou crossing-over, visible au microscope sous forme de chiasma. Ces événements d’échanges, produits en prophase, sont essentiels pour la ségrégation réductionnelle des chromosomes homologues : en l’absence de recombinaison méiotique, la ségrégation des chromosomes est en effet altérée, ce qui conduit en général à la formation de gamètes au contenu chromosomique anormal, et donc à une stérilité. Au niveau moléculaire, il a été montré chez Saccharomyces cerevisiae (pour revue, voir [1]) que les événements de recombinaison débutent par la formation de cassures double-brin (CDB) de l’ADN chromosomique. Leur réparation par recombinaison avec le chromosome homologue engendre des conversions géniques, événements non réciproques, et des crossing-over. L’étape de cassure est déterminante, puisqu’elle provoque une lésion dans l’ADN (ce qui peut être dangereux pour la cellule) et qu’elle conditionne la fréquence et la distribution des événements de recombinaison. Elle est sous la dépendance de plusieurs gènes dont la fonction est dans la plupart des cas encore inconnue. En 1997, la fonction de l’un d’entre eux a été identifiée : il s’agit du gène codant pour la protéine Spo11, dont la fonction proposée est de catalyser la formation de ces CDB.
Spo11 : un mutant de sporulation chez S. cerevisiae déficient pour le déclenchement de la recombinaison méiotique
Spo11, un mutant de S. cerevisiae isolé en 1969, est caractérisé par une anomalie de la méiose qui conduit à la formation de spores non viables [2]. Dans les mutants nuls spo11∆ (délétion du gène), aucune cassure double-brin méiotique n’est détectée [3], d’où une absence de recombinaison qui a pour conséquences une ségrégation aléatoire des chromosomes à la première division et un contenu chromosomique anormal dans la majorité des spores. À ce stade, un rôle aussi bien direct qu’indirect pouvait être envisagé pour Spo11 dans l’étape de formation des CDB.
La fonction de Spo11 révélée par les archaebactéries
Chez S. cerevisiae, des analyses moléculaires ont montré que - en présence de la mutation rad50S qui bloque la réparation des cassures [4] - les extrémités 5’ des CDB sont associées de manière covalente avec une protéine. Cette observation a conduit à la proposition que ces cassures soient produites par une des protéines connues pour former des liaisons covalentes avec l’ADN comme les topo-isomérases [5–7].
En 1997, une homologie a été identifiée entre la sous-unité catalytique (A) d’une famille de topo-isomérases de type II nouvellement découverte chez les archaebactéries, appelée TopoVI [8], et la protéine Spo11. Or, les topo-isomérases de ce type produisent transitoirement des CDB et restent attachées de façon covalente aux extrémités de ces cassures, celles-ci étant ensuite à nouveau attachées par l’enzyme elle-même. Spo11 est donc apparue comme protéine candidate pour l’activité de formation des CDB méiotiques. L’implication directe de Spo11 dans la catalyse des CDB a par la suite été confirmée par deux approches. D’une part, la coupure d’un brin d’ADN implique la présence dans toutes les topo-isomérases d’une tyrosine, appelée tyrosine catalytique ; or, une souche de S. cerevisiae portant la mutation spo11Y135F (changement de la tyrosine 135 en phénylalanine) à l’état homozygote ne forme pas de CDB méiotiques [8]. D’autre part, Spo11 est effectivement associée de manière covalente aux extrémités 5’ des CDB méiotiques in vivo [9].
Un modèle d’action de Spo11 peut être proposé sur la base des données structurales de l’homologue de Spo11 chez l’archaebactérie Methanococcus jannashii [10] et de la conservation structurelle entre cette TopoVIA et la protéine Spo11 de S. cerevisiae (B. de Massy et J.P. Pin, données non publiées) (Figure 1). Selon ce modèle, Spo11 n’aurait pas, contrairement aux topo-isomérases, les propriétés nécessaires pour attacher de nouveau les CDB.
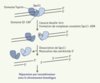 |
Figure 1. Déclenchement de la recombinaison méiotique par formation de cassures double-brin (CDB) catalysée par Spo11. Le domaine carboxy-terminal Toprim (commun aux topo-isomérases et aux primases) de chaque monomère de Spo11 interagit avec le domaine 5Y-CAP (catabolite gene activator protein) de l’autre monomère. Un dimère se fixe sur l’ADN, introduit une cassure double-brin par l’intermédiaire des tyrosines catalytiques (Y) situées dans les domaines 5Y-CAP et forme deux intermédiaires covalents avec les deux extrémités 5’ d’ADN. À ce stade, les monomères peuvent rester associés ou se séparer. Spo11 se dissocie ensuite de l’ADN selon un mécanisme non encore identifié, qui pourrait impliquer soit une réaction d’hydrolyse de la liaison phosphodiester, soit une coupure simple brin en 3’ du complexe Spo11-ADN. Les cassures double-brin ainsi formées sont ensuite réparées par recombinaison avec le chromosome homologue. |
Conservation de Spo11 chez les eucaryotes
Des homologues de TopoVIA et Spo11 sont, respectivement, présents chez toutes les archaebactéries et tous les eucaryotes testés (pour revue, voir [11, 12]). L’analyse des mutants des gènes correspondant à ces homologues a été réalisée par des méthodes différentes selon les organismes étudiés : test de fertilité, analyse cellulaire de la différenciation, analyse cytologique, ou encore analyse génétique et moléculaire de la recombinaison (Tableau I). Les résultats révèlent plusieurs caractéristiques communes aux différentes espèces étudiées [13–19, 20]. La fertilité est réduite ou nulle chez tous les mutants spo11 (délétion ou interruption du gène). Dans les espèces où l’on peut évaluer la fréquence de recombinaison chez des organismes stériles ou à fertilité réduite, une absence totale de recombinaison méiotique est observée. Chez Mus musculus, où une telle approche n’est pas réalisable, le test est celui de la formation des chiasmas. Celle-ci est absente chez toutes les espèces où elle a été recherchée (M. musculus, Caenorhabditis elegans, Arabidopsis thaliana et Sordaria macrospora). L’ensemble de ces observations montre que la majorité, si ce n’est la totalité, des événements de recombinaison méiotique est sous le contrôle de Spo11. Enfin, la recherche directe du rôle de Spo11 dans le déclenchement de la recombinaison n’a pour l’instant été réalisée que chez S. cerevisiae et S. pombe, des organismes chez lesquels cette étape est effectivement analysable par détection moléculaire des CDB en méiose : aucune CDB ne peut être détectée en l’absence de Spo11 [3, 15].
Phénotype des mutants spo11. CDB : cassure double-brin ; nt : non testé(e) ; 1 : les différences de fertilité peuvent s’expliquer par celles du nombre de chromosomes ; 2 : pas de complexe synaptonémal chez S. pombe. Par exemple, chez S. cerevisiae, qui possède seize paires de chromosomes, la probabilité de former un gamète euploïde par ségrégation aléatoire est considérablement plus faible que pour S. pombe, qui n’a que trois paires de chromosomes.
Les mutations de Spo11 n’ont toutefois pas toujours des conséquences identiques pour toutes les espèces : ainsi en est-il des altérations observées dans l’appariement des chromosomes et la progression du cycle méiotique. L’appariement des chromosomes est caractérisé en prophase par la formation d’une structure protéique nommée complexe synaptonémal (pour la souris, en particulier, voir [21]). Plusieurs études suggèrent que les étapes de déclenchement de la recombinaison ont lieu avant la formation de ce complexe [22]. D’ailleurs, celle-ci n’est pas assurée dans les mutants spo11 de S. cerevisiae, S. macrospora, Coprinus cinereus et M. musculus (Figure 2), suggérant que le déclenchement de la recombinaison est requis pour l’assemblage du complexe synaptonémal. En revanche, dans d’autres modèles comme C. elegans ou Drosophila melanogaster, le complexe synaptonémal se forme normalement [16, 23], ce qui suggère l’existence, au moins chez ces organismes, d’un mécanisme d’appariement des chromosomes indépendant de la recombinaison.
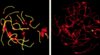 |
Figure 2. Analyse de l’appariement des chromosomes dans des ovocytes de souris. Les protéines Sycp3 (synaptonemal complex protein 3) (en rouge) et Sycp1 (synaptonemal complex protein 1) (en vert) marquent respectivement les axes des chromosomes et les régions appariées dans le complexe synaptonémal. La superposition de ces deux marquages produit un signal jaune. Les centromères situés à l’extrémité de chacun des chromosomes sont également repérés (en rouge) par des anticorps anticentromères (provenant du sérum de sujets présentant un syndrome Crest - calcinose, Raynaud, œsophage, sclérodactylie, télangiectasies). À gauche, dans une lignée sauvage, les 20 paires de chromosomes homologues sont appariées. À droite, chez un mutant Spo11−/−, les axes des 40 chromosomes sont formés, mais les chromosomes ne sont pas appariés (la tache verte est un artéfact). |
L’absence de recombinaison a également des conséquences très différentes sur le déroulement du cycle méiotique selon les espèces. Ainsi, chez S. cerevisiae, S. macrospora, S. pombe, A. thaliana, C. elegans ou D. melanogaster, les divisions méiotiques se poursuivent malgré le dysfonctionnement de la ségrégation réductionnelle. En revanche, chez C. cinereus et M. musculus, le cycle méiotique est interrompu en prophase et les cellules méiotiques entrent en apoptose. Il est intéressant de remarquer qu’au sein même de l’espèce M. musculus, les réponses du cycle cellulaire et d’induction d’apoptose diffèrent entre les méioses mâle et femelle.
Questions encore sans réponse
Quel rôle pour les partenaires de Spo11 ?
Bien que le modèle actuel du rôle direct de Spo11 dans le déclenchement de la recombinaison par formation de CDB explique de manière assez satisfaisante plusieurs aspects de la recombinaison méiotique, l’activité enzymatique de Spo11 n’a pas encore été démontrée in vitro. À l’image de son homologue chez les archaebactéries, composé de la sous-unité catalytique TopoVIA et d’une autre sous-unité, TopoVIB, qui contient un site de fixation de l’ATP nécessaire à l’activité de coupure de l’ADN [24], l’activité de Spo11 pourrait nécessiter la présence d’une autre protéine. Or, aucune protéine homologue à TopoVIB n’a été identifiée chez les eucaryotes : il est possible que Spo11 ait évolué de manière à ne plus nécessiter une seconde sous-unité pour son activité catalytique, ou que les propriétés de l’éventuelle seconde sous-unité diffèrent de celles de TopoVIB.
Une situation qui reste exceptionnelle a été décrite chez A. thaliana : son génome possède trois homologues de Spo11, et il est le seul eucaryote connu à ce jour pour posséder un homologue identifié de la sous-unité TopoVIB. Un des homologues de Spo11, exprimé spécifiquement dans les tissus floraux, est requis pour la recombinaison méiotique, suggérant qu’il s’agit là de l’homologue fonctionnel de Spo11 [17]. Les deux autres sont exprimés dans les tissus végétatifs et interagissent tous deux avec l’homologue de TopoVIB : ils pourraient donc avoir avec cette dernière une activité de topo- isomérase [25]. Cette situation suggère une corrélation entre la différenciation des fonctions TopoVI et Spo11 et la présence ou l’absence de la sous-unité B.
Malgré l’absence d’homologue de TopoVIB identifié, l’activité de Spo11 semble nécessiter la présence de partenaires dont le rôle reste à définir : en effet, chez S. cerevisiae, pas moins de dix gènes, outre SPO11, sont nécessaires à la formation des CDB (pour revue, voir [11]). Certaines de ces protéines interagissent d’ailleurs avec Spo11 : Rec102 et Spo11 ont ainsi été co-immunoprécipités au sein d’un même complexe [26], et une interaction entre Ski8 et Spo11 a été mise en évidence par la méthode du double hybride [27]. En revanche, aucun partenaire de Spo11 n’a pu être identifié chez les autres eucaryotes.
Comment les cibles de Spo11 sont-elles choisies ?
Bien que les CDB méiotiques soient localisées dans des régions précises, aucune spécificité de séquence n’a encore été mise en évidence. Toutefois, des études menées chez la levure montrent que les cibles de Spo11 correspondent à certaines régions accessibles de la chromatine (pour revue, voir [28]) dont les spécificités ne sont pas connues. A. Peciña et al. [29] ont étudié les propriétés de la protéine de fusion Gal4-Spo11, Gal4 portant un domaine de reconnaissance et de fixation à une séquence spécifique de l’ADN. Cette protéine chimérique permet la formation de CDB ciblées vers de nouveaux sites : les motifs de fixation de Gal4. Cependant, les dix autres gènes nécessaires à la formation des CDB méiotiques restent tous indispensables à la formation de CDB à ces nouveaux sites. Ces expériences démontrent que ces gènes jouent un rôle essentiel pour l’activité de Spo11, indépendamment du contrôle du choix de la cible [29].
Que fait Spo11 avant et après la formation des CDB ?
La phase de réplication préméiotique se déroule juste avant le début de la prophase. Deux analyses chez S. cerevisiae ont mis en évidence une relation entre cette phase S et le début de la recombinaison. D’une part, il a été montré qu’un intervalle de temps constant sépare la réplication de la formation des CDB, qui intervient par conséquent plus tôt dans les régions répliquées précocement que dans les régions répliquées tardivement [30]. D’autre part, la phase S est raccourcie chez le mutant spo11∆. Bien qu’encore inexpliquées, ces observations suggèrent que certains éléments impliqués dans le déclenchement de la recombinaison, et peut-être Spo11 elle-même, sont mis en place dès la réplication préméiotique [31].
Par ailleurs, un rôle tardif de Spo11, postérieur à la formation des CDB, a été suggéré. La localisation de Spo11 par immunocytochimie chez M. musculus et S. macrospora met en évidence des foyers au stade leptotène, stade auquel les CDB sont détectées chez la levure. De plus, au stade pachytène, alors que les étapes de déclenchement de la recombinaison sont en principe passées, Spo11 est détectée le long des axes des chromosomes appariés [32]. L’ensemble de ces résultats, s’ils n’apportent pas de réponse claire, reflètent sans doute une régulation complexe de la protéine Spo11 avant et après son activité de formation de CDB.
Conclusions
L’étude des caractéristiques de la protéine Spo11 dans différentes espèces révèle une conservation du mécanisme de déclenchement de la recombinaison méiotique par formation de cassures double-brin, qui devra toutefois être confirmée par la mise en évidence des propriétés de coupures de l’ADN de la protéine Spo11 in vitro, et par la mise en évidence de CDB méiotiques chez les eucaryotes supérieurs. Compte tenu du danger potentiel que peut constituer l’activité de Spo11 dans une cellule, un aspect tout à fait fascinant et encore à explorer est celui de sa régulation : comment Spo11 est-elle activée, dirigée vers ses cibles et par la suite inactivée ? Un dérèglement pourrait en effet avoir des conséquences délétères non seulement sur le déroulement de la méiose, mais également dans les cellules somatiques. En effet, même si le gène SPO11 n’est normalement exprimé qu’en méiose (l’analyse génétique des mutants spo11 n’a d’ailleurs permis de déceler aucun phénotype somatique jusqu’à ce jour), on peut imaginer les conséquences sur la stabilité du génome d’une expression inappropriée de SPO11 dans les cellules végétatives.
Références
- Smith KN, Nicolas A. Recombination at work for meiosis. Curr Opin Genet Dev 1998; 8 : 200–11. [Google Scholar]
- Klapholz S, Waddell CS, Esposito RE. The role of the SP011 in meiotic recombination in yeast. Genetics 1985; 110 : 187–216. [Google Scholar]
- Cao L, Alani E, Kleckner N. A pathway for generation and processing of double-strand breaks during meiotic recombination in S. cerevisiae. Cell 1990; 61 : 1089–101. [Google Scholar]
- Alani E, Padmore R, Kleckner N. Analysis of wild-type and rad50 mutants of yeast suggests an intimate relationship between meiotic chromosome synapsis and recombination. Cell 1990; 61 : 419–36. [Google Scholar]
- Liu J, Wu TC, Lichten M. The location and structure of double-strand DNA breaks induced during yeast meiosis : evidence for a covalently linked DNA-protein intermediate. Embo J 1995; 14 : 4599–608. [Google Scholar]
- Keeney S, Kleckner N. Covalent protein-DNA complexes at the 5’ strand termini of meiosis-specific double-strand breaks in yeast. Proc Natl Acad Sci USA 1995; 92 : 11274–8. [Google Scholar]
- De Massy B, Rocco V, Nicolas A. The nucleotide mapping of DNA double-strand breaks at the CYS3 initiation site of meiotic recombination in Saccharomyces cerevisiae. Embo J 1995; 14 : 4589–98. [Google Scholar]
- Bergerat A, de Massy B, Gadelle D, Varoutas PC, Nicolas A, Forterre P. An atypical topoisomerase II from Archaea with implications for meiotic recombination. Nature 1997; 386 : 414–7. [Google Scholar]
- Keeney S, Giroux CN, Kleckner N. Meiosis-specific DNA double-strand breaks are catalyzed by Spo11, a member of a widely conserved protein family. Cell 1997; 88 : 375–84. [Google Scholar]
- Nichols MD, DeAngelis K, Keck JL, Berger JM. Structure and function of an archaeal topoisomerase VI subunit with homology to the meiotic recombination factor Spo11. Embo J 1999; 18 : 6177–88. [Google Scholar]
- Keeney S. Mechanism and control of meiotic recombination initiation. Curr Top Dev Biol 2001; 52 : 1–53. [Google Scholar]
- Lichten M. Meiotic recombination : breaking the genome to save it. Curr Biol 2001; 11 : R253–6. [Google Scholar]
- Baudat F, Manova K, Yuen JP, Jasin M, Keeney S. Chromosome synapsis defects and sexually dimorphic meiotic progression in mice lacking spo11. Mol Cell 2000; 6 : 989–98. [Google Scholar]
- Celerin M, Merino ST, Stone JE, Menzie AM, Zolan ME. Multiple roles of spo11 in meiotic chromosome behavior. Embo J 2000; 19 : 2739–50. [Google Scholar]
- Cervantes MD, Farah JA, Smith GR. Meiotic DNA breaks associated with recombination in S. pombe. Mol Cell 2000; 5 : 883–8. [Google Scholar]
- Dernburg AF, McDonald K, Moulder G, Barstead R, Dresser M, Villeneuve AM. Meiotic recombination in C. elegans initiates by a conserved mechanism and is dispensable for homologous chromosome synapsis. Cell 1998; 94 : 387–98. [Google Scholar]
- Grelon M, Vezon D, Gendrot G, Pelletier G. AtSPO11-1 is necessary for efficient meiotic recombination in plants. Embo J 2001; 20 : 589–600. [Google Scholar]
- McKim KS, Hayashi-Hagihara A. mei-W68 in Drosophila melanogaster encodes a Spo11 homolog : evidence that the mechanism for initiating meiotic recombination is conserved. Genes Dev 1998; 12 : 2932–42. [Google Scholar]
- Lin Y, Smith GR. Transient, meiosis-induced expression of the rec6 and rec12 genes of Schizosaccharomyces pombe. Genetics 1994; 136 : 769–79. [Google Scholar]
- Storlazzi A, Tesse S, Gargano S, James F, Kleckner N, Zickler D. Meiotic double-strand breaks at the interface of chromosome movement, chromosome remodeling, and reductional division. Genes Dev 2003; 16 : 16. [Google Scholar]
- Moens PB, Kolas NK, Tarsounas M, Marcon E, Cohen PE, Spyropoulos B. The time course and chromosomal localization of recombination-related proteins at meiosis in the mouse are compatible with models that can resolve the early DNA-DNA interactions without reciprocal recombination. J Cell Sci 2002; 115 : 1611–22. [Google Scholar]
- Zickler D, Kleckner N. Meiotic chromosomes : integrating structure and function. Annu Rev Genet 1999; 33 : 603–754. [Google Scholar]
- McKim KS, Green-Marroquin BL, Sekelsky JJ, et al. Meiotic synapsis in the absence of recombination. Science 1998; 279 : 876–8. [Google Scholar]
- Buhler C, Lebbink JH, Bocs C, Ladenstein R, Forterre P. DNA topoisomerase VI generates ATP-dependent double-strand breaks with two-nucleotide overhangs. J Biol Chem 2001; 276 : 37215–22. [Google Scholar]
- Hartung F, Puchta H. Molecular characterization of homologues of both subunits A (SPO11) and B of the archaebacterial topoisomerase 6 in plants. Gene 2001; 271 : 81–6. [Google Scholar]
- Kee K, Keeney S. Functional interactions between SPO11 and REC102 during initiation of meiotic recombination in Saccharomyces cerevisiae. Genetics 2002; 160 : 111–22. [Google Scholar]
- Uetz P, Giot L, Cagney G, et al. A comprehensive analysis of protein-protein interactions in Saccharomyces cerevisiae. Nature 2000; 403 : 623–7. [Google Scholar]
- Petes TD. Meiotic recombination hot spots and cold spots. Nat Rev Genet 2001; 2 : 360–9. [Google Scholar]
- Peciña A, Smith KN, Mezard C, Murakami H, Ohta K, Nicolas A. Targeted stimulation of meiotic recombination. Cell 2002; 111 : 173–84. [Google Scholar]
- Borde V, Goldman AS, Lichten M. Direct coupling between meiotic DNA replication and recombination initiation. Science 2000; 290 : 806–9. [Google Scholar]
- Cha RS, Weiner BM, Keeney S, Dekker J, Kleckner N. Progression of meiotic DNA replication is modulated by interchromosomal interaction proteins, negatively by Spo11p and positively by Rec8p. Genes Dev 2000; 14 : 493–503. [Google Scholar]
- Romanienko PJ, Camerini-Otero RD. The mouse spo11 gene is required for meiotic chromosome synapsis. Mol Cell 2000; 6 : 975–87. [Google Scholar]
Liste des tableaux
Phénotype des mutants spo11. CDB : cassure double-brin ; nt : non testé(e) ; 1 : les différences de fertilité peuvent s’expliquer par celles du nombre de chromosomes ; 2 : pas de complexe synaptonémal chez S. pombe. Par exemple, chez S. cerevisiae, qui possède seize paires de chromosomes, la probabilité de former un gamète euploïde par ségrégation aléatoire est considérablement plus faible que pour S. pombe, qui n’a que trois paires de chromosomes.
Liste des figures
 |
Figure 1. Déclenchement de la recombinaison méiotique par formation de cassures double-brin (CDB) catalysée par Spo11. Le domaine carboxy-terminal Toprim (commun aux topo-isomérases et aux primases) de chaque monomère de Spo11 interagit avec le domaine 5Y-CAP (catabolite gene activator protein) de l’autre monomère. Un dimère se fixe sur l’ADN, introduit une cassure double-brin par l’intermédiaire des tyrosines catalytiques (Y) situées dans les domaines 5Y-CAP et forme deux intermédiaires covalents avec les deux extrémités 5’ d’ADN. À ce stade, les monomères peuvent rester associés ou se séparer. Spo11 se dissocie ensuite de l’ADN selon un mécanisme non encore identifié, qui pourrait impliquer soit une réaction d’hydrolyse de la liaison phosphodiester, soit une coupure simple brin en 3’ du complexe Spo11-ADN. Les cassures double-brin ainsi formées sont ensuite réparées par recombinaison avec le chromosome homologue. |
| Dans le texte | |
 |
Figure 2. Analyse de l’appariement des chromosomes dans des ovocytes de souris. Les protéines Sycp3 (synaptonemal complex protein 3) (en rouge) et Sycp1 (synaptonemal complex protein 1) (en vert) marquent respectivement les axes des chromosomes et les régions appariées dans le complexe synaptonémal. La superposition de ces deux marquages produit un signal jaune. Les centromères situés à l’extrémité de chacun des chromosomes sont également repérés (en rouge) par des anticorps anticentromères (provenant du sérum de sujets présentant un syndrome Crest - calcinose, Raynaud, œsophage, sclérodactylie, télangiectasies). À gauche, dans une lignée sauvage, les 20 paires de chromosomes homologues sont appariées. À droite, chez un mutant Spo11−/−, les axes des 40 chromosomes sont formés, mais les chromosomes ne sont pas appariés (la tache verte est un artéfact). |
| Dans le texte | |
Current usage metrics show cumulative count of Article Views (full-text article views including HTML views, PDF and ePub downloads, according to the available data) and Abstracts Views on Vision4Press platform.
Data correspond to usage on the plateform after 2015. The current usage metrics is available 48-96 hours after online publication and is updated daily on week days.
Initial download of the metrics may take a while.




