| Issue |
Med Sci (Paris)
Volume 35, Number 5, Mai 2019
|
|
|---|---|---|
| Page(s) | 423 - 430 | |
| Section | M/S Revues | |
| DOI | https://doi.org/10.1051/medsci/2019077 | |
| Published online | 22 May 2019 | |
Milieu Intérieur
Comprendre l’hétérogénéité du système immunitaire sain pour avancer sur la voie de la médecine personnalisée
Milieu Intérieur: understanding healthy immune system heterogeneity to move along the path towards personalized medicine
Cytométrie et Biomarqueurs (UTechS CB), Centre de recherche translationnelle (CRT), Institut Pasteur, 25, rue du Docteur Roux, 75015 Paris, France
*
This email address is being protected from spambots. You need JavaScript enabled to view it.
Résumé
Le projet Milieu Intérieur vise à élucider les facteurs environnementaux et héréditaires qui façonnent un système immunitaire sain, et à définir ses frontières lors de l’homéostasie et à la suite d’une stimulation immunitaire. Le projet repose sur un phénotypage immunitaire de 1 000 donneurs sains. En corrélant les mesures obtenues par analyse en cytométrie en flux de la composition des cellules immunitaires du sang périphérique en homéostasie avec les métadonnées associées, nous avons défini des valeurs de référence de phénotypes en fonction du sexe et de l’âge et constaté un impact significatif du tabagisme et de l’infection latente par le cytomégalovirus sur les phénotypes mesurés. Nous avons également identifié onze nouveaux polymorphismes (SNP, single-nucleotide polymorphism), associés à des phénotypes spécifiques de certaines cellules immunitaires. Des conduites expérimentales robustes et standardisées ont été établies pour quantifier les signatures protéiques et transcriptionnelles de la réponse immunitaire résultant de la stimulation des cellules du sang périphérique et pour explorer les déterminants génétiques et non-génétiques de la variabilité de cette réponse. Les approches analytiques établies par Milieu Intérieur et l’ensemble des données recueillies pourront ainsi servir de référence pour des études comparatives avec différentes maladies.
Abstract
The Milieu Intérieur project aims to define the boundaries of a healthy immune system in steady state and upon immune stimulation, and to elucidate environmental and hereditary determinants of its variability. The project is based on an in-depth immune phenotyping of 1 000 healthy donors. By correlating the cytometry measurements of peripheral blood immune cell composition in homeostasis, with the associated metadata, we have defined reference values of phenotypes related to sex and age, and found a significant impact of latent cytomegalovirus infection and smoking on measured phenotypes. In addition, we identified eleven novel Single-Nucleotide Polymorphisms (SNPs) associated with immune cell phenotypes. Immune response signatures were measured upon stimulation of fresh peripheral blood by 40 immune stimuli. Robust and standardized pipelines were established to quantify expression of 29 proteins and 572 genes and to explore genetic and non-genetic determinants of the variability of healthy immune response. The analytical approaches established by Milieu Intérieur and the collected data set represent an ideal reference for comparison studies of disease populations.
© 2019 médecine/sciences – Inserm
 Article publié sous les conditions définies par la licence Creative Commons Attribution License CC-BY (http://creativecommons.org/licenses/by/4.0), qui autorise sans restrictions l'utilisation, la diffusion, et la reproduction sur quelque support que ce soit, sous réserve de citation correcte de la publication originale.
Article publié sous les conditions définies par la licence Creative Commons Attribution License CC-BY (http://creativecommons.org/licenses/by/4.0), qui autorise sans restrictions l'utilisation, la diffusion, et la reproduction sur quelque support que ce soit, sous réserve de citation correcte de la publication originale.
Vignette (Photo © Inserm – Sebastian Amigorena).
Étudier l’hétérogénéité de la réponse immunitaire humaine
La communauté biomédicale déploie beaucoup d’efforts pour trouver des solutions qui remplaceront les stratégies thérapeutiques actuelles par des approches fondées sur une médecine personnalisée de précision. Ces approches reposent sur la compréhension des biomarqueurs de variabilité de la réponse aux traitements médicaux au sein de la population. Les conditions préalables à l’identification des biomarqueurs immunitaires sont : (1) l’établissement des limites des phénotypes immunitaires sains à l’état basal et au cours de la réponse immunitaire ; (2) la quantification de l’hétérogénéité de la réponse immunitaire interindividuelle observée dans les populations humaines ; et (3) la compréhension des facteurs qui conduisent à cette variabilité.
La variabilité d’une réponse immunitaire humaine saine peut résulter d’une multitude de facteurs biologiques (âge, sexe), génétiques (polymorphismes ou SNP), épigénétiques, environnementaux (microbiote, infections latentes ou chroniques) ou liés au mode de vie (alimentation, tabagisme, historique médical). La majorité des études ont examiné individuellement l’impact de chacun de ces déterminants sur la réponse immunitaire, habituellement dans le contexte d’une pathologie donnée et sur certains types de cellules ou tissus d’intérêt. Depuis peu, cependant, plusieurs projets ont été initiés pour réaliser une analyse intégrée de l’impact de différents cofacteurs sur l’hétérogénéité du système immunitaire. Ces nouvelles études utilisent des approches d’immunologie systémique ou d’immunologie des populations (systems or population immmunology) pour étudier la variabilité d’un système immunitaire sain, soit dans des cohortes de jumeaux, soit dans des cohortes bien définies d’enfants ou d’adultes sains [1-10].
L’une des principales études d’immunologie systémique en cours est le projet Milieu Intérieur 1, détaillé dans la Synthèse de Darragh Duffy parue dans le précédent numéro de médecine/sciences [23] (→).
(→) Voir la Synthèse de D. Duffy, m/s n° 4, avril 2019, page 327
Le projet Milieu Intérieur a été créé en 2011 dans le but d’élucider les facteurs environnementaux et héréditaires qui façonnent un système immunitaire sain dans les populations européennes et de définir ses frontières en homéostasie et à la suite d’une stimulation immunitaire. La définition de la variabilité immunitaire naturelle et son association avec des facteurs physiologiques, environnementaux et génétiques pourraient servir de référence pour des études comparatives intégrant différentes maladies.
L’étude Milieu Intérieur repose sur l’analyse d’échantillons prélevés chez 1 000 donneurs sains, stratifiés sur 5 décennies d’âge (20-69 ans) et par sexe (500 femmes et 500 hommes). Cette cohorte a été décrite par D. Duffy dans le précédent numéro de m/s [23] (→). Afin d’éviter la présence de sous-populations dans la population étudiée, ce qui aurait une incidence sur la détection des associations génotype-phénotype, l’étude a été limitée aux personnes d’origine européenne, citoyens français métropolitains depuis trois générations au moins. Les échantillons prélevés comprenaient du sang périphérique frais, des PBMC (cellules mononucléées isolées du sang périphérique), de l’ADN et de l’ARN extraits du sang, des selles, des écouvillons nasaux et des biopsies de peau. Des tests biochimiques et hématologiques classiques ont été effectués et, pour chaque participant, ont été collectés des renseignements détaillés sur les antécédents médicaux, le mode de vie, l’alimentation, le tabagisme et sur d’autres paramètres pouvant avoir un impact sur le système immunitaire [11].
(→) Voir la Synthèse de D. Duffy, m/s n° 4, avril 2019, page 327
Phénotypage du système immunitaire sain en homéostasie
La composition du sang périphérique en cellules immunitaires a été déterminée pour évaluer la variabilité du système immunitaire des individus sains à l’état basal. Un total de 168 paramètres a été quantifié par cytométrie en flux, comprenant le nombre absolu et la fréquence des cellules immunitaires, ainsi que le niveau d’expression (MFI, intensité moyenne de fluorescence) des marqueurs spécifiques présents sur ces cellules. Ce dernier paramètre a permis de suivre et de comparer le statut d’activation des cellules étudiées au sein de la cohorte. En corrélant les mesures obtenues par cytométrie en flux aux métadonnées associées, nous avons défini des valeurs de référence selon le sexe et l’âge, et évalué l’impact des facteurs environnementaux sur les phénotypes des cellules immunitaires [12]. Nous avons observé que les lymphocytes T CD8+ naïfs diminuaient plus de deux fois plus rapidement avec l’âge que les lymphocytes T CD4+ naïfs (respectivement 3,5 % versus 1,5 % par année). Ces résultats pourraient expliquer l’impact de l’âge sur l’efficacité des vaccins, une vaccination réussie entraînant la différenciation de cellules naïves en cellules mémoire à longue durée de vie. Nous avons également détecté chez les femmes, par rapport aux hommes, un nombre absolu de lymphocytes T invariants associés à la muqueuse (MAIT) inférieur, et un nombre accru de cellules NKT (natural killer T lymphocytes), ce qui reflète probablement une influence hormonale sur les phénotypes examinés. Il est d’autre part intéressant de noter que, sur plus de 300 variables cliniques recueillies, seules deux d’entre elles ont révélé une influence significative sur les phénotypes des cellules immunitaires : l’infection latente par le cytomégalovirus (CMV) et le tabagisme. L’infection latente par le CMV a en effet un impact majeur sur le statut de différenciation des sous-populations de lymphocytes T. Elle est associée à un nombre de lymphocytes T CD4+ et CD8+ effecteurs mémoire (TEM) 12 fois plus élevé et de lymphocytes T effecteurs mémoire RA (TEMRA) 4,5 fois plus important. Le tabagisme actif, quant à lui, entraîne une augmentation significative du nombre de leucocytes circulants, en particulier de lymphocytes T régulateurs (Treg). Dans les compartiments cellulaires innés, le tabagisme est à l’origine d’une réduction du nombre de cellules lymphoïdes innées (ILC), peut-être en raison du recrutement continu de ces cellules dans le tissu épithélial pulmonaire.
La variabilité génétique entre individus a un impact significatif sur les phénotypes immunitaires en situation d’homéostasie. En corrélant les évaluations réalisées avec plus de 5 millions de SNP par donneur, nous avons pu identifier 11 nouveaux polymorphismes génétiques associés à des phénotypes de cellules immunitaires. Il s’agit par exemple du polymorphisme du gène SELL (codant la L-sélectine ou CD62L), qui affecte de façon différentielle l’expression de la protéine à la surface des polynucléaires. Il est intéressant de noter que cette différence concerne les éosinophiles et les neutrophiles, mais pas les basophiles [12]. Au total, 25 % des phénotypes cellulaires examinés ont été associés à des variabilités génétiques. Parmi celles-ci, la majorité (80 %) affecte les cellules immunitaires innées, en modifiant préférentiellement le niveau d’expression des protéines qu’elles présentent à leur surface. Ceci peut être la conséquence d’une durée de vie plus courte de ces cellules, ce qui les empêche d’être influencées par des facteurs externes non génétiques. Ces déterminants non-génétiques ont, par contre, un effet prédominant sur les populations de cellules immunitaires adaptatives. Ayant une longue durée de vie, celles-ci sont plus susceptibles d’être affectées par l’âge, le tabagisme, les infections latentes, les vaccins et d’autres facteurs non héréditaires résultant du mode de vie de l’individu. La Figure 1 résume la contribution des différents déterminants à la variabilité des phénotypes immunitaires cellulaires.
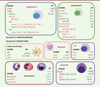 |
Figure 1. Les déterminants héréditaires et non héréditaires des phénotypes de cellules immunitaires à l’état basal. Dans le cadre du projet Milieu Intérieur, la cytométrie en flux a été utilisée pour quantifier l’expression de marqueurs phénotypiques de différenciation ou d’activation dans des cellules immunitaires de différentes lignées, ainsi que pour quantifier les cellules elles-mêmes, afin d’identifier les immunophénotypes associés de manière significative à des facteurs non-génétiques (en rouge) ou génétiques (en bleu) à l’état basal. MFI : mean fluorescence intensity. |
Bien que la production continue de lymphocytes T naïfs autotolérants par le thymus soit la clé d’une réponse immunitaire efficace des lymphocytes T contre les antigènes nouvellement rencontrés chez les individus sains, la régulation de la thymopoïèse reste mal comprise. Le débit thymique peut être mesuré indirectement par la quantification des cercles d’excision des récepteurs des lymphocytes T (TREC) qui sont produits pendant la recombinaison somatique thymique du récepteur de ces cellules, le TCR (T cell receptor). Les TREC sont maintenus dans les cellules T matures sous forme d’un ADN épisomique qui ne peut se reproduire. Il sera ainsi dilué au cours des divisions des cellules périphériques. En utilisant la quantification des TREC comme mesure de l’activité thymique dans la cohorte de Milieu Intérieur, nous avons récemment rapporté que la diminution de la production thymique avec l’âge était différente chez les hommes et les femmes et était indépendante de tout autre facteur environnemental mesuré [13]. Nous avons identifié une variation commune dans le locus TCRA (T cell receptor alpha) - TCRD (T cell receptor delta) du TCR comme étant un déterminant majeur de nombre de TREC. Environ 50 % de la variabilité observée est cependant demeurée inexpliquée, ce qui suggère le rôle de facteurs qui restent encore inconnus. En fournissant des valeurs de référence de la fonction thymique dans une grande population en bonne santé, ces données constituent une ressource qui peut être utile dans le contexte de la médecine de précision et des stratégies régénératives pour diverses maladies et qui peut contribuer à une meilleure compréhension du vieillissement du système immunitaire.
Dissection des signatures d’une réponse immunitaire saine lors d’une stimulation
Comprendre la variabilité du système immunitaire en homéostasie est insuffisant pour prévoir l’hétérogénéité de la réponse immunitaire à une stimulation donnée. Il est donc nécessaire d’identifier des signatures de réponses obtenues chez des individus en bonne santé. Milieu Intérieur a mis en place des stratégies pour mieux comprendre les spécificités de ces signatures au niveau protéique et transcriptionnel, en réponse à la stimulation de différents récepteurs immunitaires.
À cette fin, le sang périphérique frais isolé de chaque donneur a été exposé à un ensemble de 40 stimulus immunitaires, allant des cytokines utilisées dans les traitements médicaux (IFN-g, interféron gamma ; TNF-a, tumor necrosis factor ; etc.), à des ligands de récepteurs immunitaires (ligands des TLR [Toll-like receptor], activateurs des lymphocytes [CD3/CD28]) et à des microbes entiers (bactéries, virus et champignons). Pour un sous-groupe de 25 donneurs sains, la production de 29 protéines a été quantifiée dans les surnageants de culture de leurs cellules activées par ces stimulus afin d’établir la signature spécifique de chacune des réponses. L’application de l’analyse en composantes principales (PCA, principal component analysis) non-supervisée2 a permis d’identifier clairement les profils d’expression des protéines spécifiques de la réponse immunitaire innée et de la réponse des lymphocytes T. Elle a en particulier permis de révéler une réponse à la stimulation par l’acide polycytidylique (poly I:C), un analogue d’ARN double brin, reconnu par le TLR3 (CD283) [14]. La résolution de l’analyse était suffisamment sensible pour identifier les valeurs atypiques. Chez deux sujets, par exemple, contrairement aux autres individus, aucun des stimulus utilisés n’a conduit à une production mesurable d’IL-1a (interleukine 1a), alors que le reste de la signature observée pour les 28 autres protéines possiblement induites était intact chez ces individus. Étant donné l’importance de l’IL-1a dans l’inflammation en condition stérile (c’est-à-dire en l’absence de stimulus microbien), et la pathogenèse des maladies liées à son absence, une analyse plus poussée des sujets ne répondant pas à une stimulation par la production de cette cytokine (individus non-répondeurs) pourrait avoir un réel intérêt.
Ces mêmes échantillons provenant de ces 25 donneurs ont été analysés afin de déterminer les signatures transcriptionnelles de la réponse immunitaire par quantification de l’expression de 572 gènes liés au système immunitaire. La PCA et l’algorithme linear support vector machine 3 ont conduit à l’identification de 44 gènes dont l’analyse s’est révélée être nécessaire pour caractériser la signature transcriptionnelle de la réponse à la stimulation par quatre cytokines innées clés (IFN-b, IFN-g, IL-1b et TNF-a) [15]. Ces signatures génétiques sont suffisantes pour évaluer la diversité des réponses immunitaires innées complexes après stimulation par des ligands de différents TLR ou par des microbes entiers. Nous avons ainsi déterminé dans quelle mesure les signatures associées à des stimulus immunitaires simples ou complexes se chevauchaient, et nous avons pu identifier des gènes dont l’expression est spécifiquement induite par une stimulation microbienne. L’ampleur de la variabilité interindividuelle de l’expression génétique ainsi observée au sein de ces 25 donneurs s’est révélée dépendre largement du type de stimulus appliqué. Des expériences en cours qui étendent l’analyse du profil transcriptionnel à l’ensemble de la cohorte Milieu Intérieur permettront d’établir des valeurs de référence pour les signatures d’expression génique pour chaque stimulus. Elles permettront également de considérer la variabilité naturelle des réponses immunitaires des individus sains.
Déterminants de la variabilité de la réponse immunitaire
Les déterminants de la variabilité interindividuelle de la réponse immunitaire induite ont été étudiés dans l’ensemble de la cohorte de 1 000 donneurs, après stimulation par des microbes entiers. La contribution relative de la génétique, du sexe, de l’âge et de la composition en cellules immunitaires, mesurée à l’état d’équilibre, a été évaluée à partir des signatures d’expression des 572 gènes [16]. L’impact de l’âge sur la réponse dépend largement du microbe utilisé. Néanmoins, pour la plupart des stimulus, l’effet délétère de l’âge sur l’expression de la majorité des gènes analysés est apparu être linéaire. En particulier, la régulation étroite du système immunitaire tout au long de la vie peut être reliée à l’effet de l’âge sur l’expression génétique de l’IL-13 et du récepteur du lipopolysaccharide bactérien CD144, à la suite d’une stimulation par le SEB (Staphylococcal enterotoxin B). En effet, bien que la production d’IL-13 augmente avec l’âge, une diminution de l’expression de CD14 par les cellules est observée. Le sexe a, quant à lui, un effet sur l’expression de la majorité des gènes analysés (506/572), dont environ 1/3 est modifié selon le sexe, mais uniquement après une stimulation immunitaire. Cet effet dépend, en général, de la nature de la stimulation microbienne. Par exemple, l’expression de CD278, l’inhibiteur d’activation des lymphocytes T, est systématiquement plus élevée chez les femmes, tandis que celle de CD14 est plus importante chez les hommes.
L’impact des polymorphismes génétiques sur la variabilité des profils d’expression induits lors des stimulations a été évalué par l’analyse des associations des signatures à l’échelle du génome (étude d’association pangénomique ou GWA) pour chaque stimulus. Nous avons identifié un certain nombre de polymorphismes génétiques ayant un impact sur l’expression de gènes locaux5 (cis-eQTL [expression quantitative trait loci]). Certains de ces polymorphismes avaient déjà été décrits pour leur association avec différentes pathologies comme, par exemple, le gène LILRA3 (leukocyte immunoglobulin-like receptor A3), exprimé par les lymphocytes T, qui régule la réponse inflammatoire : un polymorphisme touchant le locus de ce gène entraîne en effet une modification d’expression de la protéine en condition homéostasique et lors de la stimulation avec des agents pathogènes. Des travaux antérieurs avaient montré que la délétion du gène LILRA3 avait un effet protecteur dans le cancer de la prostate [17], mais une association avec les maladies infectieuses n’avait pas encore été décrite. Nous avons également identifié le locus TLR 10/1/6 comme étant le régulateur à distance (trans-eQTL) le plus puissant de la réponse immunitaire. Ce locus s’est en effet avéré être le régulateur principal de l’expression des gènes lors de la stimulation par la bactérie Escherichia coli et le bacille Calmette-Guérin (BCG). Cette découverte s’inscrit dans la continuité d’un travail de Quatch et al. qui ont analysé la réponse immunitaire des monocytes primaires de donneurs sains européens et africains à la suite d’une stimulation par les ligands de différents récepteurs immunitaires innés [18]. Ces auteurs ont ainsi montré l’impact des polymorphismes du TLR1 sur un réseau de gènes, et comment ces polymorphismes touchant la population européenne résultent en des réponses inflammatoires plus faibles, comparativement à la population africaine. Ces mutations avantageuses (réduisant la réponse) résultent d’une sélection positive et d’un mélange ancien avec des gènes néandertaliens, il y a environ 30 000 à 50 000 ans [18].
Nous avons en parallèle construit un modèle statistique qui nous a permis d’évaluer les parts respectives sur la réponse des effets liés à l’âge et au sexe, ainsi que de déterminer si la contribution observée est obtenue de manière directe ou indirecte, par modification de la composition des populations de cellules immunitaires dans le sang. La part de l’impact de chacun des déterminants, génétiques et non génétiques, sur l’expression génique après une stimulation immunitaire a également été déterminée. Comme indiqué dans la Figure 2, la principale contribution à la variabilité de l’expression génique en réponse à différents microbes repose sur la composition en cellules immunitaires dans le sang. L’âge et le sexe contribuent pour 5 % de la variabilité observée. Les régulateurs génétiques, surtout les trans-eQTL, agissent, eux, comme des « régulateurs maîtres » : même s’ils n’affectent que peu de gènes, leur effet sur les signatures immunitaires s’est révélé être significatif.
 |
Figure 2. La variabilité d’expression génétique expliquée par l’âge, le sexe, la génétique et par la composition des cellules sanguines. Variance moyenne, entre les gènes, expliquée par l’âge (vert), le sexe (orange), la génétique (cis-eQTL en bleu et trans-eQTL en noir) et les proportions des populations de cellules CD45+ (rose) en l’absence de stimulation (NS) et dans les six conditions de stimulation indiquées. La taille des cercles correspond au nombre de gènes affectés par chaque facteur dans chaque condition. SEB : staphylococcal enterotoxin B ; IAV : influenza A virus ; BCG : bacille Calmette-Guérin. |
L’interaction de déterminants qui maintiennent l’équilibre du système immunitaire et l’efficacité de la réponse reste complexe et nécessite des études approfondies. Un exemple de cette complexité est la régulation de l’expression des gènes appartenant aux voies de signalisation des interféron de type I (IFN- a/b) ou de MyD88 (myeloid differentiation primary response 88), un intermédiaire de signalisation induite par les TLR, pour laquelle la variabilité d’expression de différents gènes peut s’expliquer par différents facteurs génétiques et non-génétiques (Figure 3) [16].
 |
Figure 3. Complexité de la régulation de la variabilité transcriptionnelle : l’exemple des voies de signalisation immunitaire. La proportion de la variabilité transcriptionnelle expliquée par les différents facteurs génétiques et non-génétiques des gènes appartenant aux voies IFN de type I (panneau supérieur) et TLR-MyD88 (panneau inférieur) dans l’état basal et suite à la stimulation par Escherichia coli. NS : contrôle non-stimulé. TLR-MyD88 : Toll-like receptor-myeloid differentiation primary response 88. |
Importance de la standardisation
La clé de la réalisation d’une étude d’immunologie systémique est la qualité des données recueillies. Le projet Milieu Intérieur a pris un soin extrême à standardiser toutes les conduites expérimentales et procédures, du traitement des échantillons aux protocoles d’analyse et à l’interprétation des données. En ce qui concerne la cytométrie en flux, les échantillons de sang total frais ont été analysés par un laboratoire centralisé, en utilisant des lots de réactifs testés et un robot de pipetage pour la préparation des échantillons afin d’éviter des erreurs qui seraient dues à une manipulation manuelle. Bien que l’analyse des données ait été manuelle, nous avons appliqué des matrices de compensation6 prédéfinies pour éviter tout biais dans l’attribution des cellules à une population donnée [19]. Une méthode semi-supervisée d’analyse7 des données, qui s’est avérée efficace pour améliorer la discrimination de certaines populations cellulaires, a été employée [20]. Ces mesures de standardisation ont permis de distinguer des erreurs techniques de variations extrêmes des phénotypes biologiques. Il a été ainsi montré, par exemple, qu’une petite proportion d’individus n’exprimait pas CD168 (ou FcγRIII, l’un des récepteurs pour la région Fc des immunoglobulines), à la surface de leurs neutrophiles et qu’il ne s’agissait pas d’une erreur technique9.
La réponse à la stimulation immunitaire est généralement étudiée sur des cellules périphériques (les PBMC). La préparation de ces cellules est difficile à normaliser au sein des laboratoires cliniques ; elle nécessite un personnel qualifié. La manipulation du sang peut également être à l’origine d’une activation non spécifique des cellules isolées ou de leur mort. Les plaquettes sanguines et les granulocytes ne sont pas présents dans les échantillons de PBMC. La stimulation des PBMC ne peut donc refléter la réaction qui serait obtenue avec du sang total. Afin de minimiser la manipulation pré-expérimentale et les biais techniques qui en résultent, nous avons utilisé des dispositifs fondés sur des seringues TruCulture pour la stimulation du sang total [14]. Une étude clinique multicentrique récente a ainsi montré que la reproductibilité des résultats obtenus avec cette méthode est considérablement améliorée par rapport à celle observée après stimulation de PBMC [21].
Dans le cadre du projet Milieu Intérieur, les signatures protéiques de la réponse cellulaire ont été évaluées par l’analyse simultanée de protéines produites dans les surnageants de culture (Luminex) et les signatures d’expression génique, par hybridation de code-barres colorés (Nanostring). Des protocoles normalisés de préparation des échantillons et des conduites expérimentales ont été établis et de nombreuses validations techniques ont été effectuées aux fins d’analyse par l’une ou l’autre de ces technologies.
Tout au long de la phase de leur prélèvement, le traitement des échantillons du projet Milieu Intérieur et leur stockage après la stimulation ont été étroitement contrôlés et standardisés afin de permettre l’établissement d’une base d’échantillons contenant au total 220 000 tubes. L’analyse a été réalisée à l’aide d’outils certifiés pour le diagnostic in vitro. Les protocoles du projet Milieu Intérieur sont donc transposables à toute étude clinique.
Conclusion
La compréhension du comportement du système immunitaire dans un contexte de maladie, ainsi que l’identification de biomarqueurs diagnostiques ou de biomarqueurs d’une réponse efficace à des traitements ou à des vaccins n’est possible que si l’on dispose d’une connaissance approfondie du système immunitaire de personnes en bonne santé. Le projet Milieu Intérieur a établi des stratégies robustes et normalisées pour mesurer les limites d’une réponse immunitaire saine, pour identifier les phénotypes extrêmes et pour quantifier les biomarqueurs de la réponse à la stimulation immunologique. Les données de Milieu Intérieur s’enrichissent en permanence. Récemment, nous avons exploré les mesures sérologiques au sein de la cohorte pour évaluer la variabilité des réponses immunitaires antimicrobiennes humorales et identifier des associations entre génétique, sexe, âge, et réponse humorale chez les individus sains [22]. Les associations ainsi identifiées ont le potentiel d’aider à améliorer les stratégies de vaccination et/ou à disséquer les mécanismes pathogènes impliqués dans les maladies humaines liées à la production d’immunoglobulines, comme l’auto-immunité. Les analyses en cours comprennent des études d’échantillons de selles et d’écouvillons nasaux pour estimer la contribution du microbiote à la variabilité immunitaire observée.
Une compréhension approfondie de la nature des déterminants de la variabilité de la réponse immunitaire, tant héréditaires qu’environnementaux, et l’établissement de valeurs de référence pour les phénotypes immunitaires mesurés sont des facteurs clés pour prédire l’efficacité du système immunitaire dans le contexte de différentes maladies et la réponse au traitement. La Figure 4 résume les stratégies développées par Milieu Intérieur pour recueillir une base de données des phénotypes immunitaires sains à l’homéostasie et après une stimulation immunitaire, et ainsi générer une référence pour des études sur des personnes malades. La résolution fine des outils établis fait des données recueillies une excellente base pour l’étude des biomarqueurs immunitaires au niveau cellulaire, protéique et transcriptionnel et constitue ainsi un pas important vers des approches personnalisées et précises dans les décisions médicales relatives à la vaccination, au diagnostic et aux solutions thérapeutiques.
 |
Figure 4. Ensemble des données de référence de Milieu Intérieur : progresser sur la voie de la médecine personnalisée et de précision. Le projet Milieu Intérieur a mis en place des moyens robustes pour l’évaluation globale du système immunitaire inné et adaptatif et pour déterminer les limites des phénotypes immunitaires sains en homéostasie et suite à une stimulation immunitaire. Toutes les mesures cytométriques, signatures protéiques et transcriptionnelles de Milieu Intérieur et leurs corrélations avec les métadonnées collectées sont mises à disposition pour exploration grâce à des outils interactifs Shiny en libre accès (http://www.milieuinterieur.fr/en/research/data-visualization). |
Liens d’intérêt
L’auteure déclare n’avoir aucun lien d’intérêt concernant les données publiées dans cet article.
Remerciements
L’auteure tient à remercier Clémentine Schilte et Julien Descles pour leur lecture critique du manuscrit et Bernd Jagla pour la mise en forme des figures.
Sans a priori sur les échantillons analysés.
Cet algorithme comprend des méthodes d’analyse supervisées, utilisées pour la classification, la régression et la détection des valeurs atypiques.
L’expression du gène codant l’IL-13 est associée à la stimulation de CD14 par les bactéries.
C’est-à-dire touchant le gène ciblé. Ce type de eQTL est appelé cis, alors que si le polymorphisme touche un gène éloigné, il sera appelé trans.
Ces matrices permettent d’identifier les fluorescences spécifiques de chaque anticorps, en intégrant les intensités respectives des signaux.
Cette approche repose sur les algorithmes bio-informatiques, en s’appuyant sur l’expertise immunologique dans l’interprétation des données.
Du fait de l’absence d’un lien glycosylphosphatidylinositol (GPI) entre CD16b et la membrane plasmique.
La molécule CD16b est une molécule ancrée dans la membrane des neutrophiles par un lien glycosylphosphatidylinositol. Un petit nombre d’individus présentent une absence de ce lien et leurs neutrophiles n’expriment pas CD16b sans qu’aucune pathologie n’ait été associée à cette absence, à l’exception d’une neutropénie néo-natale due à la production d’anticorps anti-CD16b chez les mères CD16b-.
Références
- Aguirre-Gamboa R, Joosten I, Urbano PCM, et al. Differential effects of environmental and genetic factors on T and B cell immune traits. Cell Rep. 2016 ; 17 : 2474–2487. [CrossRef] [PubMed] [Google Scholar]
- Brodin P, Jojic V, Gao T, et al. Variation in the human immune system is largely driven by non-heritable influences. Cell. 2015 ; 160 : 37–47. [CrossRef] [PubMed] [Google Scholar]
- Orrù V, Steri M, Sole G, et al. Genetic variants regulating immune cell levels in health and disease. Cell. 2013 ; 155 : 242–256. [CrossRef] [PubMed] [Google Scholar]
- Ter Horst R, Jaeger M, Smeekens SP, et al. Host and environmental factors influencing individual human cytokine responses. Cell. 2016 ; 167 : 1111–24. e13. [CrossRef] [PubMed] [Google Scholar]
- Mangino M, Roederer M, Beddall MH, et al. Innate and adaptive immune traits are differentially affected by genetic and environmental factors. Nat Commun. 2017 ; 8 : 13850. [CrossRef] [PubMed] [Google Scholar]
- Olin A, Henckel E, Chen Y, et al. Stereotypic immune system development in newborn children. Cell. 2018 ; 174 : 1277–92. e14. [CrossRef] [PubMed] [Google Scholar]
- Enroth S, Johansson A, Enroth SB, et al. Strong effects of genetic and lifestyle factors on biomarker variation and use of personalized cutoffs. Nat Commun. 2014 ; 5 : 4684. [CrossRef] [PubMed] [Google Scholar]
- Zalocusky KA, Kan MJ, Hu Z, et al. The 10,000 Immunomes project: Building a resource for human immunology. Cell Rep. 2018 ; 25 : 513–22. e3. [CrossRef] [PubMed] [Google Scholar]
- Carr EJ, Dooley J, Garcia-Perez JE, et al. The cellular composition of the human immune system is shaped by age and cohabitation. Nat Immunol. 2016 ; 17 : 461–468. [CrossRef] [PubMed] [Google Scholar]
- Roederer M, Quaye L, Mangino M, et al. The genetic architecture of the human immune system: a bioresource for autoimmunity and disease pathogenesis. Cell. 2015 ; 161 : 387–403. [CrossRef] [PubMed] [Google Scholar]
- Thomas S, Rouilly V, Patin E, et al. The Milieu Intérieur study - an integrative approach for study of human immunological variance. Clin Immunol. 2015 ; 157 : 277–293. [CrossRef] [PubMed] [Google Scholar]
- Patin E, Hasan M, Bergstedt J, et al. Natural variation in the parameters of innate immune cells is preferentially driven by genetic factors. Nat Immunol. 2018 ; 19 : 302–314. [CrossRef] [PubMed] [Google Scholar]
- Clave E, Araujo IL, Alanio C, et al. Human thymopoiesis is influenced by a common genetic variant within the TCRA-TCRD locus. Sci Transl Med 2018; 10 : eaao2966. [CrossRef] [PubMed] [Google Scholar]
- Duffy D, Rouilly V, Libri V, et al. Functional analysis via standardized whole-blood stimulation systems defines the boundaries of a healthy immune response to complex stimuli. Immunity. 2014 ; 40 : 436–450. [CrossRef] [PubMed] [Google Scholar]
- Urrutia A, Duffy D, Rouilly V, et al. Standardized whole-blood transcriptional profiling enables the deconvolution of complex induced immune responses. Cell Rep. 2016 ; 16 : 2777–2791. [CrossRef] [PubMed] [Google Scholar]
- Piasecka B, Duffy D, Urrutia A, et al. Distinctive roles of age, sex, and genetics in shaping transcriptional variation of human immune responses to microbial challenges. Proc Natl Acad Sci USA. 2018 ; 115 : E488–EE97. [CrossRef] [Google Scholar]
- Xu J, Mo Z, Ye D, et al. Genome-wide association study in Chinese men identifies two new prostate cancer risk loci at 9q31.2 and 19q13.4. Nat Genet. 2012 ; 44 : 1231–1235. [Google Scholar]
- Quach H, Rotival M, Pothlichet J, et al. Genetic adaptation and neandertal admixture shaped the immune system of human populations. Cell. 2016 ; 167 : 643–56. e17. [CrossRef] [PubMed] [Google Scholar]
- Hasan M, Beitz B, Rouilly V, et al. Semi-automated and standardized cytometric procedures for multi-panel and multi-parametric whole blood immunophenotyping. Clin Immunol. 2015 ; 157 : 261–276. [CrossRef] [PubMed] [Google Scholar]
- Chen X, Hasan M, Libri V, et al. Automated flow cytometric analysis across large numbers of samples and cell types. Clin Immunol. 2015 ; 157 : 249–260. [CrossRef] [PubMed] [Google Scholar]
- Duffy D, Rouilly V, Braudeau C, et al. Standardized whole blood stimulation improves immunomonitoring of induced immune responses in multi-center study. Clin Immunol. 2017 ; 183 : 325–335. [CrossRef] [PubMed] [Google Scholar]
- Scepanovic P, Alanio C, Hammer C, et al. Human genetic variants and age are the strongest predictors of humoral immune responses to common pathogens and vaccines. Genome Med. 2018 ; 10 : 59. [CrossRef] [PubMed] [Google Scholar]
- Duffy D.. Milieu Intérieur : définir les limites d’une réponse immunitaire saine pour mieux comprendre la maladie. Med Sci (Paris). 2019 ; 35 : 327–331. [CrossRef] [EDP Sciences] [PubMed] [Google Scholar]
Liste des figures
 |
Figure 1. Les déterminants héréditaires et non héréditaires des phénotypes de cellules immunitaires à l’état basal. Dans le cadre du projet Milieu Intérieur, la cytométrie en flux a été utilisée pour quantifier l’expression de marqueurs phénotypiques de différenciation ou d’activation dans des cellules immunitaires de différentes lignées, ainsi que pour quantifier les cellules elles-mêmes, afin d’identifier les immunophénotypes associés de manière significative à des facteurs non-génétiques (en rouge) ou génétiques (en bleu) à l’état basal. MFI : mean fluorescence intensity. |
| Dans le texte | |
 |
Figure 2. La variabilité d’expression génétique expliquée par l’âge, le sexe, la génétique et par la composition des cellules sanguines. Variance moyenne, entre les gènes, expliquée par l’âge (vert), le sexe (orange), la génétique (cis-eQTL en bleu et trans-eQTL en noir) et les proportions des populations de cellules CD45+ (rose) en l’absence de stimulation (NS) et dans les six conditions de stimulation indiquées. La taille des cercles correspond au nombre de gènes affectés par chaque facteur dans chaque condition. SEB : staphylococcal enterotoxin B ; IAV : influenza A virus ; BCG : bacille Calmette-Guérin. |
| Dans le texte | |
 |
Figure 3. Complexité de la régulation de la variabilité transcriptionnelle : l’exemple des voies de signalisation immunitaire. La proportion de la variabilité transcriptionnelle expliquée par les différents facteurs génétiques et non-génétiques des gènes appartenant aux voies IFN de type I (panneau supérieur) et TLR-MyD88 (panneau inférieur) dans l’état basal et suite à la stimulation par Escherichia coli. NS : contrôle non-stimulé. TLR-MyD88 : Toll-like receptor-myeloid differentiation primary response 88. |
| Dans le texte | |
 |
Figure 4. Ensemble des données de référence de Milieu Intérieur : progresser sur la voie de la médecine personnalisée et de précision. Le projet Milieu Intérieur a mis en place des moyens robustes pour l’évaluation globale du système immunitaire inné et adaptatif et pour déterminer les limites des phénotypes immunitaires sains en homéostasie et suite à une stimulation immunitaire. Toutes les mesures cytométriques, signatures protéiques et transcriptionnelles de Milieu Intérieur et leurs corrélations avec les métadonnées collectées sont mises à disposition pour exploration grâce à des outils interactifs Shiny en libre accès (http://www.milieuinterieur.fr/en/research/data-visualization). |
| Dans le texte | |
Current usage metrics show cumulative count of Article Views (full-text article views including HTML views, PDF and ePub downloads, according to the available data) and Abstracts Views on Vision4Press platform.
Data correspond to usage on the plateform after 2015. The current usage metrics is available 48-96 hours after online publication and is updated daily on week days.
Initial download of the metrics may take a while.




