Figure 1
Télécharger l'image originale
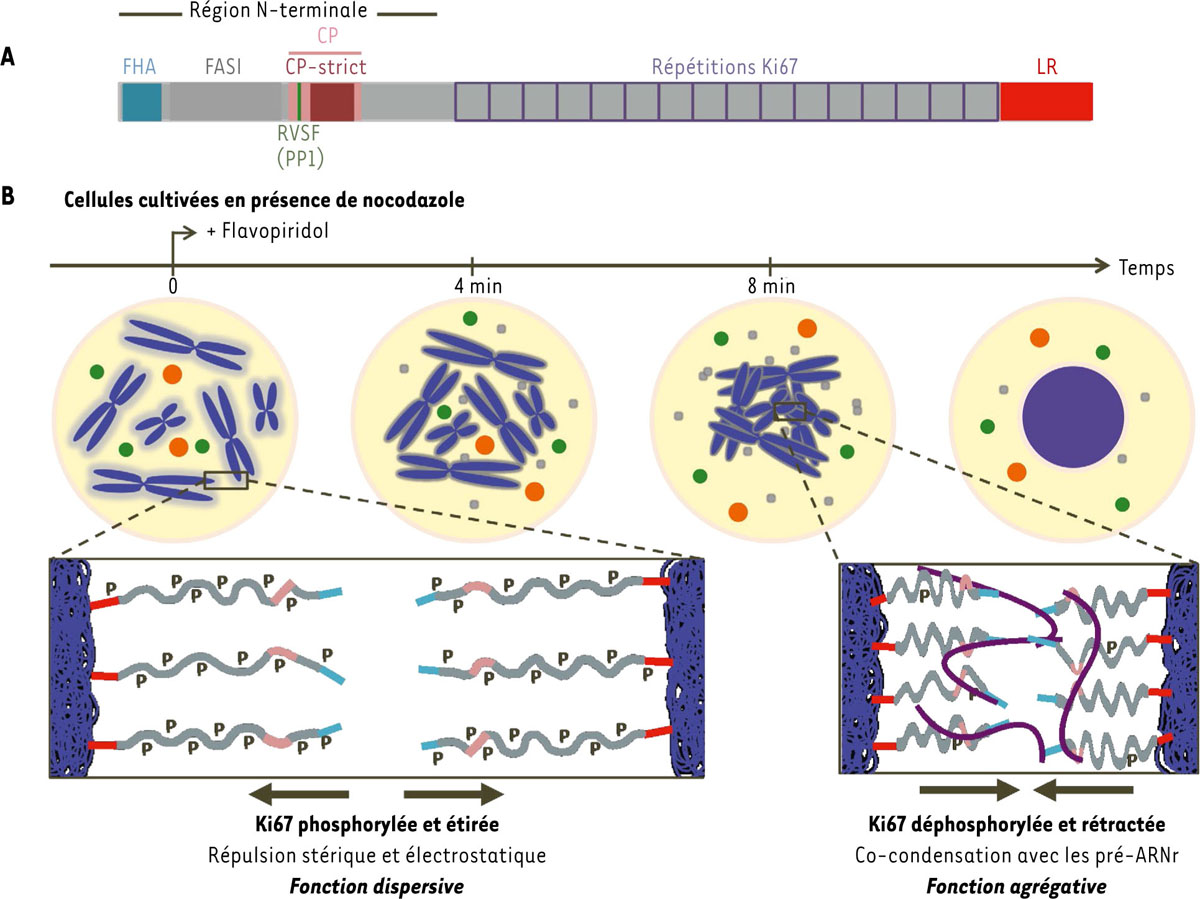
La protéine Ki67 et ses rôles dans la mitose. A. Domaines de la protéine Ki67 humaine. L’isoforme longue (3256 résidus) est représentée. FHA : forkheadassociated domain ; FASI : fragment absent in the short isoform (codé par l’exon 7) ; CP : charged patch (chevauche le domaine conservé CD précédemment défini [3, 6, 12]) ; CP-strict : partie du domaine CP la plus riche en résidus basiques (arginine et lysine) ; RVSF : motif impliqué dans le recrutement de la phosphoprotéine phosphatase PP1 et présent dans le domaine CP (hors CP-strict) ; Succession de 16 répétitions imparfaites d’un domaine d’environ 120 résidus (le nombre de répétions varie selon les espèces) [5, 6] ; LR : domaine riche en résidus leucine (L) et arginine (R), permettant l’ancrage de Ki67 aux chromosomes mitotiques [1–7]. Notons que la portion N-terminale du domaine CP recrutant PP1 est structurellement et fonctionnellement conservée dans la protéine Repo-Man (recruits PP1 onto mitotic chromatin at anaphase) [5, 11]. La redondance entre ces deux protéines pour le recrutement de PP1 (isoforme γ) sur les chromosomes en anaphase, avec une certaine prédominance de Repo-Man [11], pourrait en partie expliquer pourquoi la sortie de mitose n’est pas perturbée par l’expression d’une forme mutante de Ki67 (dans le motif RVSF) incapable de recruter PP1 [4, 7, 11]. B. Changement structurel et fonctionnel de Ki67 au cours de la mitose. En début de mitose (prométaphase), les chromosomes sont dispersés par les protéines Ki67 phosphorylées (P) et étirées (environ 90 nm) perpendiculairement à la surface des chromosomes (halo gris sur les chromosomes, et couleurs correspondant aux domaines de la Figure 1A sur le grossissement). En fin de mitose, les chromosomes se regroupent par cocondensation des protéines Ki67 rétractées (environ 30 nm), déphosphorylées, et encore plus abondantes à leur surface (halo gris plus étroit et plus foncé), et des pré-ARNr (couleur prune) également présents à leur surface [4, 7]. Ce regroupement intervient juste avant la reformation de l’enveloppe nucléaire, et chasse hors du futur noyau des gros composants cytoplasmiques (ronds orange et verts) présents dans l’espace interchromosomique. En fin de mitose, Ki67 forme également des foyers cytoplasmiques (en gris) qui contiennent aussi des pré-ARNr [7]. Dans le protocole expérimental utilisé, les cellules sont synchronisées par le nocodazole (un poison du fuseau mitotique), puis traitées par un inhibiteur de la kinase CDK1, le flavopiridol, ce qui déclenche une sortie rapide de mitose (sans fuseau mitotique) et permet d’en suivre précisément le déroulement. Ce protocole correspond à la majorité des expériences dans [4, 7], notamment celles visant à étudier le rôle de Ki67 et des pré-ARNr dans le regroupement des chromosomes. Notons que ce regroupement se produit également avec d’autres protocoles de blocage ou de déclenchement de sortie de mitose, et à la fin d’une mitose normale [4]. Le schéma comporte certaines simplifications. Les modalités du recrutement des pré-ARNr par Ki67 autour des chromosomes mitotiques restent à préciser [7, 8]. Il est possible que Ki67 et d’autres protéines de la périphérie chromosomique (non représentées) forment aussi des ponts entre les chromosomes en fin de mitose, mais insuffisamment pour les regrouper en l’absence des pré-ARNr [7]. En plus du domaine LR, la partie N-terminale de Ki67, vraisemblablement par son domaine CP, pourrait interagir avec les chromosomes en fin de mitose [7]. Enfin, les pré-ARNr sont présents à la surface des chromosomes dès la prométaphase, mais leur quantité augmente ensuite (au moins lors d’une mitose normale) [7, 8]. En dehors de la mitose, Ki67 est principalement localisée dans et juste autour des nucléoles [1–3, 5–7, 11, 12].
Current usage metrics show cumulative count of Article Views (full-text article views including HTML views, PDF and ePub downloads, according to the available data) and Abstracts Views on Vision4Press platform.
Data correspond to usage on the plateform after 2015. The current usage metrics is available 48-96 hours after online publication and is updated daily on week days.
Initial download of the metrics may take a while.




