| Numéro |
Med Sci (Paris)
Volume 22, Numéro 11, Novembre 2006
|
|
|---|---|---|
| Page(s) | 926 - 928 | |
| Section | Nouvelles | |
| DOI | https://doi.org/10.1051/medsci/20062211926 | |
| Publié en ligne | 15 novembre 2006 | |
Sans Tsix, les mâles aussi inactivent leur chromosome X
Without Tsix, male X chromosome is inactivated
Unité Génétique Moléculaire Murine, CNRS URA 2578, Institut Pasteur, 25, rue du Docteur Roux, 75724 Paris Cedex 15, France
Chez les femelles de mammifères, chaque cellule somatique de l’individu adulte exprime les gènes portés par un seul des deux chromosomes X. Le second chromosome X est maintenu transcriptionnellement inactif par un mécanisme épigénétique complexe appelé inactivation du chromosome X (→). Cette inactivation permet la compensation de dose des gènes liés au chromosome X entre les sexes, en assurant un niveau d’expression équivalent de ces gènes chez les femelles (XX) et les mâles (XY). Les tissus de l’adulte dérivent de l’épiblaste, formé dans l’embryon au moment de l’implantation, environ 5 jours et demi après la fécondation chez la souris. L’inactivation aléatoire de l’un ou l’autre des chromosomes X est initiée de manière indépendante dans chaque cellule de l’épiblaste de l’embryon femelle, au moment où elles s’engagent dans les voies de différenciation contemporaines à la gastrulation. Une fois établie, l’inactivation est transmise de manière stable lors des divisions mitotiques, ce qui aboutit à un individu adulte femelle mosaïque pour l’expression des gènes du chromosome X.
(→) m/s 2006, n° 11, p. 910
Les cellules souches embryonnaires (cellules ES) constituent un modèle de choix pour l’étude de l’inactivation du chromosome X (Figure 1). Elles dérivent de la masse cellulaire interne des blastocystes, tissu précurseur de l’épiblaste où n’a pas encore eu lieu l’inactivation aléatoire du chromosome X. La même séquence d’événements aboutissant à l’inactivation de l’un des deux chromosomes X dans l’embryon femelle est observée dans des cellules ES femelles après différenciation in vitro. De plus, aussi bien dans l’embryon mâle que dans les cellules ES mâles, l’inactivation de l’unique chromosome X n’est jamais observée. En effet, un unique chromosome X par complément diploïde d’autosomes est toujours maintenu actif, du fait d’un mécanisme de comptage évaluant le rapport entre le nombre de chromosomes X et le nombre d’autosomes. Chez les femelles, un mécanisme additionnel de choix permet de décider aléatoirement quel chromosome X sera inactivé ou maintenu actif dans chaque cellule. À l’heure actuelle, les mécanismes moléculaires du choix et du comptage restent encore à définir.
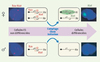 |
Figure 1. L’inactivation du chromosome X met en jeu les ARN non codants Xist et Tsix. L’expression de Xist et de Tsix est ici visualisée par RNA-FISH dans des cellules souches ES murines. Dans les cellules indifférenciées aussi bien mâles que femelles, les chromosomes X sont actifs (Xa), Tsix est fortement exprimé et Xist est très faiblement exprimé. En cours de différenciation, l’expression de Tsix est perdue et une forte expression de Xist est observée sur l’un des deux chromosomes X dans les cellules femelles (pour revue, voir [2]). |
L’inactivation du chromosome X requiert son recouvrement par un ARN non codant, Xist, qui recrute des facteurs aboutissant à l’hétérochromatinisation du chromosome. Le gène Xist est localisé dans une région du chromosome X, le centre d’inactivation du chromosome X, nécessaire et suffisante pour diriger le processus d’inactivation. Chez la souris, l’expression de Xist est réprimée par un ARN non codant antisens, Tsix. Chez les femelles, l’absence d’expression de Tsix sur un allèle conduit à l’inactivation systématique du chromosome déficient, démontrant l’implication de ce gène dans le mécanisme de choix (pour revue, voir [1]). En revanche, la participation de Tsix dans le processus de comptage restait sujette à débat, sur la base d’observations suggérant que Tsix n’est pas nécessaire au maintien de l’état actif chez les mâles (pour revue, voir [2]). Il a toutefois été établi par des approches délétionnelles qu’un ou plusieurs éléments requis pour le comptage sont présents dans une région de 37 kb immédiatement en 3’ de Xist [3]. Cette région inclut la partie 5’ de Tsix, dans laquelle sont situés un homologue de l’activateur de transcription du récepteur pré-T, et deux minisatellites constitués de répétitions de 17 pb pour l’un et 34 pb pour l’autre.
L’invalidation de Tsix conduit à l’inactivation de l’unique chromosome X de cellules ES mâles différenciées
Dans le but d’identifier les éléments de comptage contenus dans la région candidate située en 3’ de Xist, une série de délétions (∆AJ, ∆AS et ∆AV) ciblant ces éléments a été réalisée dans des cellules ES murines mâles (Figure 2) [4]. Les délétions ∆AJ et ∆AS, ciblant le premier minisatellite et la région d’homologie, ne conduisent pas à une inactivation ectopique chez les mâles et permettent d’exclure ces deux éléments d’une fonction de comptage. Au contraire, la délétion ∆AV, qui supprime le second minisatellite, appelé DXPas34, ainsi que le promoteur de Tsix, a pour effet de conduire de manière très efficace à l’inactivation inappropriée du chromosome X. Les cellules porteuses d’un chromosome X inactif sont détectables, par hybridation in situ en fluorescence (RNA-FISH) de l’ARN Xist ou par immunofluorescence pour l’histone 3 triméthylé sur la lysine 27, dans les phases précoces de la différenciation. Elles disparaissent ensuite du fait de la nullisomie pour les gènes du chromosome X. L’insertion d’un signal d’arrêt de transcription au début du gène Tsix (lignée Ma2L [5]) produit le même effet, suggérant que la transcription de Tsix est requise pour empêcher le déclenchement inapproprié de l’inactivation dans les cellules mâles et participe donc de manière essentielle au processus de comptage. L’absence de Tsix a ainsi des conséquences similaires en cis chez les mâles et les femelles, ce qui affaiblit les arguments en faveur de mécanismes de régulation de l’inactivation différents dans les deux sexes dont, notamment, l’existence d’un facteur de compétence spécifique aux cellules femelles.
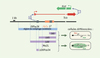 |
Figure 2. Caractérisation d’éléments participant au comptage par une approche délétionnelle en 3’ de Xist. La fonction des différents éléments contenus dans la région candidate de comptage a été étudiée dans des cellules souches embryonnaires murines mâles au moyen de délétions (lignées ∆AJ, ∆AS, ∆AV et ∆DXPas34) représentées par des barres pleines mauves, ainsi que par l’insertion d’un signal d’arrêt de transcription, figuré par une barre verticale. Les phénotypes des différentes lignées après différenciation in vitro sont représentés à droite. L’ensemble des observations supporte la conclusion que Tsix est impliqué dans la répression de l’inactivation dans les cellules mâles [4]. |
Le minisatellite DXPas34 est essentiel au contrôle transcriptionnel de Tsix
Compte tenu de l’importance et de la multiplicité des fonctions de Tsix, il est essentiel de comprendre comment ce gène est régulé au cours du développement. Le minisatellite DXPas34 (pour revue, voir [2]), situé à proximité du promoteur de Tsix, est inclus dans un îlot riche en CpG méthylés différentiellement selon l’état actif ou inactif du chromosome X, et peut être associé aux facteurs CTCF et YY1 [6], de manière similaire aux centres régulateurs des gènes soumis à empreinte parentale. La délétion ciblée de DXPas34 dans des cellules ES murines mâles [4] conduit à une diminution de 90 % de l’expression de Tsix dans les cellules non différenciées. De plus, une réduction importante de l’association de la machinerie de transcription au promoteur de Tsix est observée, ce qui démontre le rôle joué par DXPas34 dans la régulation au niveau transcriptionnel de l’expression de Tsix. Enfin, la suppression partielle de Tsix résultant de la délétion de DXPas34 est associée en cours de différenciation à l’inactivation inappropriée de l’unique chromosome X dans un nombre modéré de cellules. Ce résultat contraste cependant avec le phénotype plus marqué observé lorsque l’expression de Tsix est presque complètement abolie, dans les lignées ∆AV et Ma2L.
Si l’on considère l’ensemble des lignées mutantes, il apparaît que l’expression du gène Xist est directement couplée au niveau d’expression résiduelle de Tsix, aussi bien avant qu’en cours de différenciation. Cela suggère qu’une régulation précise de Tsix au cours du développement contrôle le processus d’inactivation du chromosome X. L’implication de mécanismes reposant sur des interactions d’ARN sens et antisens n’a pour l’instant pas été démontrée. En revanche, le contrôle de Xist par Tsix semble mettre en jeu le remodelage de la chromatine à l’échelle du locus et au promoteur de Xist, et la répression de Xist aux niveaux transcriptionnels et post-transcriptionnels [7–9]. La fonction du bloc d’ADN répété DXPas34 reste, quant à elle, pour l’essentiel, à définir. Outre la régulation directe du promoteur de Tsix, on peut envisager une fonction de barrière vis-à-vis d’un régulateur de Tsix, ou un rôle dans la conformation tridimensionnelle de la chromatine, notamment via la formation de boucles. L’association à des mécanismes de type ARNi spécifiques a été également montrée pour certains éléments répétés en tandem [10]. L’étude de DXPas34 pourrait ainsi contribuer à mieux comprendre la fonction des éléments répétés dans les génomes des mammifères.
Références
- Clerc P, Avner P. Random X-chromosome inactivation: skewing lessons for mice and men. Curr Opin Genet Dev 2006; 16 : 246–53. [Google Scholar]
- Rougeulle C, Avner P. The role of antisense transcription in the regulation of X-inactivation. Curr Top Dev Biol 2004; 63 : 61–89. [Google Scholar]
- Morey C, Navarro P, Debrand E, et al. The region 3’ to Xist mediates X chromosome counting and H3 Lys-4 dimethylation within the Xist gene. EMBO J 2004; 23 : 594–604. [Google Scholar]
- Vigneau S, Augui S, Navarro P, et al. An essential role for the DXPas34 tandem repeat and Tsix transcription in the counting process of X chromosome inactivation. Proc Natl Acad Sci USA 2006; 103 : 7390–5. [Google Scholar]
- Luikenhuis S, Wutz A, Jaenisch R. Antisense transcription through the Xist locus mediates Tsix function in embryonic stem cells. Mol Cell Biol 2001; 21 : 8512–20. [Google Scholar]
- Do Kim J, Hinz AK, Bergmann A, et al. Identification of clustered YY1 binding sites in imprinting control regions. Genome Res 2006; 16 : 901–11. [Google Scholar]
- Navarro P, Pichard S, Ciaudo C, et al. Tsix transcription across the Xist gene alters chromatin conformation without affecting Xist transcription: implications for X-chromosome inactivation. Genes Dev 2005; 19 : 1474–84. [Google Scholar]
- Sado T, Hoki Y, Sasaki H. Tsix silences Xist through modification of chromatin structure. Dev Cell 2005; 9 : 159–65. [Google Scholar]
- Sun BK, Deaton AM, Lee JT. A transient heterochromatic state in Xist preempts X inactivation choice without RNA stabilization. Mol Cell 2006; 21 : 617–28. [Google Scholar]
- Lippman Z, Gendrel AV, Black M, et al. Role of transposable elements in heterochromatin and epigenetic control. Nature 2004; 430 : 471–6. [Google Scholar]
© 2006 médecine/sciences - Inserm / SRMS
Liste des figures
 |
Figure 1. L’inactivation du chromosome X met en jeu les ARN non codants Xist et Tsix. L’expression de Xist et de Tsix est ici visualisée par RNA-FISH dans des cellules souches ES murines. Dans les cellules indifférenciées aussi bien mâles que femelles, les chromosomes X sont actifs (Xa), Tsix est fortement exprimé et Xist est très faiblement exprimé. En cours de différenciation, l’expression de Tsix est perdue et une forte expression de Xist est observée sur l’un des deux chromosomes X dans les cellules femelles (pour revue, voir [2]). |
| Dans le texte | |
 |
Figure 2. Caractérisation d’éléments participant au comptage par une approche délétionnelle en 3’ de Xist. La fonction des différents éléments contenus dans la région candidate de comptage a été étudiée dans des cellules souches embryonnaires murines mâles au moyen de délétions (lignées ∆AJ, ∆AS, ∆AV et ∆DXPas34) représentées par des barres pleines mauves, ainsi que par l’insertion d’un signal d’arrêt de transcription, figuré par une barre verticale. Les phénotypes des différentes lignées après différenciation in vitro sont représentés à droite. L’ensemble des observations supporte la conclusion que Tsix est impliqué dans la répression de l’inactivation dans les cellules mâles [4]. |
| Dans le texte | |
Les statistiques affichées correspondent au cumul d'une part des vues des résumés de l'article et d'autre part des vues et téléchargements de l'article plein-texte (PDF, Full-HTML, ePub... selon les formats disponibles) sur la platefome Vision4Press.
Les statistiques sont disponibles avec un délai de 48 à 96 heures et sont mises à jour quotidiennement en semaine.
Le chargement des statistiques peut être long.




