Figure 1.
Télécharger l'image originale
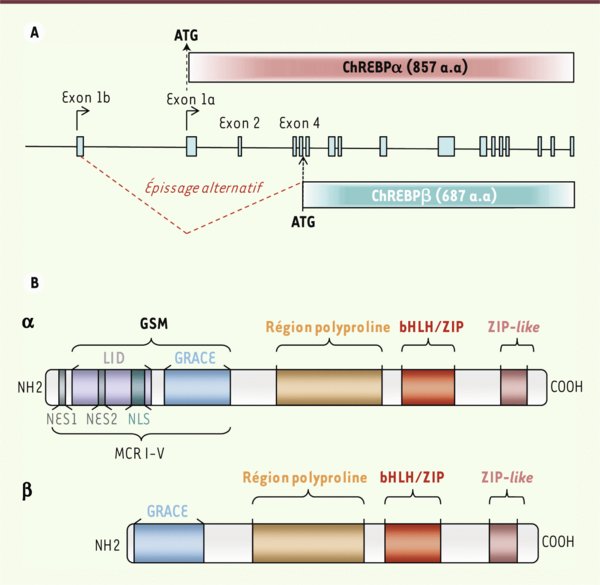
Représentations génique et protéique de ChREBP α et β. A. Epissage alternatif de ChREBPβ. ChREBPα est synthétisée à partir du site d’initiation de la traduction localisé dans l’exon 1a. ChREBPβ est transcrite à partir du promoteur situé dans l’exon 1b et par un épissage des exons 1a et 2. Le site d’initiation de la traduction est localisé dans l’exon 4 conduisant à la formation d’une protéine plus courte de 687 acides aminés. Adapté de [23]. B. Structure des protéines ChREBP α et β. La protéine ChREBPα (857 a.a) possède différents domaines dont un signal de localisation nucléaire (NLS), deux signaux d’export nucléaire (NES1 et NES2), un domaine riche en proline, un domaine bHLH/ZIP permettant l’interaction avec son partenaire d’hétérodimérisation Mlx et un domaine leucine-zipper-like. Une région très conservée et sensible au glucose (GSM) a été identifiée par analyse structure/fonction. Cette région est comprend les domaines LID (low-glucose inhibitory domain) et GRACE (glucose conserved response element). Le domaine LID est absent de la protéine courte ChREBPβ. MCR : mondo conserved region.
Current usage metrics show cumulative count of Article Views (full-text article views including HTML views, PDF and ePub downloads, according to the available data) and Abstracts Views on Vision4Press platform.
Data correspond to usage on the plateform after 2015. The current usage metrics is available 48-96 hours after online publication and is updated daily on week days.
Initial download of the metrics may take a while.




