| Numéro |
Med Sci (Paris)
Volume 27, Numéro 12, Décembre 2011
|
|
|---|---|---|
| Page(s) | 1053 - 1055 | |
| Section | Les grandes avancées françaises en biologie récompensées par l'Académie des sciences | |
| DOI | https://doi.org/10.1051/medsci/20112712005 | |
| Publié en ligne | 23 décembre 2011 | |
Comment sont choisis les sites d’échanges entre chromosomes lors de la méiose ?
What determines the localisation of spots of meiotic recombination?
Institut de génétique humaine, UPR1142 CNRS, 141, rue de la Cardonille, 34396 Montpellier Cedex 5, France
Lors de la méiose, une seule réplication du génome suivie de deux divisions permet à une cellule germinale diploïde de produire des gamètes haploïdes. La première division se distingue par le fait que les chromosomes homologues d’origines maternelle et paternelle ségrégent. Les échanges réciproques entre chromosomes homologues, ou crossing-over, qui surviennent lors de la prophase de cette division jouent un rôle essentiel pour la formation de gamètes fonctionnels : ils forment un lien physique entre les chromosomes homologues, nécessaire à leur ségrégation. La recombinaison méiotique, à l’origine des crossing-over, a également pour conséquence de provoquer un réassortiment des allèles dans le génome, générant de la diversité génétique.
Les crossing-over sont concentrés dans les points chauds
Les crossing-over ne sont pas répartis de manière aléatoire le long des chromosomes [1]. Au contraire, ils sont concentrés dans des intervalles de 1 à 2 kilobases, appelés points chauds de crossing-over, séparés les uns des autres par des régions de quelques dizaines de kilobases. Au niveau moléculaire, la recombinaison méiotique est déclenchée par des cassures double-brin de l’ADN dont la formation est catalysée par la protéine SP011 [11], et qui sont réparées par recombinaison avec le chromosome homologue. Les sites préférentiels de formation de cassures double-brin par SP011 sont donc des points chauds de recombinaison. Chez la souris et l’homme, seul un petit nombre de points chauds de crossing-over ont été identifiés et caractérisés directement. Néanmoins, l’analyse de la diversité génétique dans des populations humaines a permis de prédire la présence de plus de 25 000 points chauds à haute résolution dans l’ensemble du génome. Un motif partiellement dégénéré de séquence d’ADN (le 13-mère CCNCCNTNNCCNC) est associé à 41 % de ces points chauds [2]. Alors que les points chauds chez la levure Saccharomyces cerevisiae sont associés aux promoteurs des gènes, les points chauds humains ne sont pas associés à des éléments fonctionnels connus du génome, et sont situés plutôt en dehors des gènes. Pourquoi la recombinaison est-elle ainsi ciblée vers des sites précis du génome ? Comment ces sites sont-ils choisis ? Ce sont des questions restées sans réponse jusqu’à la découverte très récente d’un facteur majeur impliqué dans ce processus.
Le gène Prdm9 contrôle I’activité des points chauds dans I’ensemble du génome
L’idée qui prévalait était que des facteurs multiples contrôleraient la position des points chauds de recombinaison chez les mammifères. Les contributions relatives des différents facteurs, incluant des caractéristiques locales de la séquence d’ADN et de la structure de la chromatine, varieraient entre points chauds. De façon inattendue, nous avons mis à jour un système plus simple : un seul facteur, la protéine PRDM9 (PR domain zinc finger protein 9), contrôle la distribution de la quasi-totalité des sites de recombinaison en se liant spécifiquement à un motif d’ADN et en modifiant localement la structure de la chromatine [12].
Le gène Prdm9 est exprimé spécifiquement lors de la prophase de méiose. Son produit est une histone méthyltransférase qui catalyse la triméthylation de la lysine 4 de l’histone H3 (H3K4) [3]. Or notre équipe a montré que cette modification d’histone est associée à l’initiation de la recombinaison aux points chauds chez la souris [4]. En plus du domaine responsable de son activité d’histone méthyltransférase, la protéine PRDM9 contient un domaine carboxy-terminal constitué d’une série de doigts de zinc de type C2H2 se succédant en tandem (Figure 1A). Ces doigts de zinc sont des peptides capables de lier des séquences spécifiques d’ADN. Ces séquences cibles peuvent être prédites dans une certaine mesure d’après l’identité des acides aminés présents à trois positions importantes sur chaque doigt de zinc.
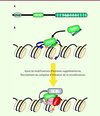 |
Figure 1. Modèle de ciblage des événements de recombinaison méiotique par PRDM9. A. PRDM9 possède trois domaines connus : un domaine KRAB (impliqué dans des interactions entre protéines), un domaine PR/SET (activité méthyltransférase) et un domaine à doigt de zinc (liaison à l’ADN). B. Grâce à ses doigts de zinc, PRDM9 se lie à un motif de séquence d’ADN spécifique et triméthyle la lysine 4 de l’histone H3 des nucléosomes les plus proches (pastilles oranges). D’autres modifications post-traductionnelles d’histones sont mises en place (pastilles grises), peut-être par des protéines recrutées par PRDM9 (rectangle gris). PDRM9 et/ou l’ensemble spécifique des modifications d’histones présentes est reconnu par un complexe protéique (en rose), non identifié à ce jour, qui va permettre le recrutement et l’activation du complexe d’initiation de la recombinaison symbolisé par la protéine SP011 (en rouge) (d’après [6], avec modifications). |
Nos travaux de recherche nous ont conduits à comparer deux lignées de souris (b et wm7) qui ont des points chauds de crossing-over spécifiques, c’est-à-dire actifs dans une lignée et inactifs dans l’autre. De façon remarquable, les allèles Prdm9b et Prdm9wm7 de ces deux lignées diffèrent spécifiquement au niveau des séries de doigts de zinc, de telle manière que des séquences d’ADN différentes sont prédites être reconnues par l’une et l’autre formes de PRDM9 [5]. En construisant des souris transgéniques, nous avons démontré le rôle essentiel des doigts de zinc de PRDM9 pour déterminer la position des points chauds : la forme PRDM9wm7 introduite dans la lignée b se fixe sur des motifs de séquence d’ADN trouvés au centre de points chauds spécifiques de la lignée wm7, induit la triméthylation de H3K4 sur les nucléosomes les plus proches et active la recombinaison au niveau de ces sites [6]. C’est peut-être la modification locale de la chromatine qui favorise l’initiation de la recombinaison à ces sites selon un mécanisme qui reste à définir (Figure 1B).
Nous avons étendu ces conclusions à l’espèce humaine en mettant en évidence l’existence d’une grande diversité de PRDM9, dont les variants diffèrent les uns des autres au niveau de leurs séries de doigts de zinc, et en montrant que le variant majoritaire reconnaît le motif d’ADN associé à 41 % des points chauds cités plus haut. Enfin, par une analyse d’association, nous avons établi une corrélation forte entre le génotype de PRDM9 et la localisation des crossing-over [5]. Les travaux présentés ci-dessus montrent que, aussi bien chez l’homme que chez la souris, PRDM9 est un acteur majeur du contrôle de la position des crossing-over. La fixation de PRDM9 sur ses cibles, reconnues grâce aux doigts de zinc de cette protéine, permet de recruter la protéine SP011 selon un mécanisme qui reste à découvrir. Des approches différentes ont permis à deux autres équipes d’identifier indépendamment le rôle de PRDM9 dans la spécification des points chauds de recombinaison chez la souris et l’homme [7, 8].
Les dynamiques évolutives des points chauds et de PRDM9
Une particularité remarquable de ce mécanisme est que des changements d’acides aminés dans les doigts de zinc de PRDM9 suffisent à modifier les cibles génomiques de PRDM9, et par conséquent à changer les points chauds de recombinaison dans l’ensemble du génome. Par exemple, les protéines PRDM9 de l’homme et du chimpanzé diffèrent fortement au niveau de leurs doigts de zinc, ce qui permet d’expliquer que, malgré des génomes aux séquences très similaires (moins de 1,2 % de divergence), les points chauds de crossing-over ne sont pas conservés entre ces deux espèces [7]. Cette variation entre les protéines PRDM9 de l’homme et du chimpanzé illustre une propriété particulière de PRDM9 : l’évolution extrêmement rapide de ses doigts de zinc. Pourquoi et comment les protéines PRDM9 varient-elles si rapidement [9] ?
Cette variabilité pourrait être la solution à l’extinction inexorable de l’activité de recombinaison aux points chauds, qui est une conséquence prévisible de cette même activité. En effet, une propriété remarquable du mécanisme de la recombinaison méiotique est que la molécule d’ADN qui subit une cassure double-brin est dégradée sur quelques dizaines de paires de bases, puis remplacée par l’ADN provenant du chromosome homologue (voir la figure 1 de la référence [1]). Lorsqu’il y a un polymorphisme nucléotidique au niveau d’un site de cassures double-brin, un allèle qui augmente la fréquence de formation de cassure double-brin sera systématiquement remplacé par l’allèle le moins favorable à la formation de cassures double-brin. Les sites de plus forte affinité pour PRDM9, où plus de cassures double-brin seraient formées, sont donc condamnés à disparaître : l’activité de recombinaison de PRDM9 conduit à la disparition de ses propres substrats. L’apparition de nouveaux allèles de Prdm9 peut potentiellement résoudre ce paradoxe : les nouvelles isoformes de PRDM9 vont reconnaître de nouveaux sites, créant un ensemble de nouveaux points chauds de crossing-over qui vont remplacer ceux reconnus par l’isoforme originelle, devenus de moins en moins actifs par le processus décrit ci-dessus. L’apparition de nouveaux allèles de Prdm9, favorisée par son évolution rapide, permettrait donc de maintenir une densité élevée de points chauds de crossing-over dans le génome.
L’érosion des points chauds est-elle une force sélective suffisamment puissante pour favoriser l’émergence de nouveaux allèles ? Prdm9 a peut être d’autres rôles que celui de spécifier la position des sites de recombinaison. En fait, Prdm9 a été également identifié comme un gène responsable de stérilité hybride chez la souris, par un mécanisme qui n’est pas connu à ce jour [10]. Ce mécanisme, quel qu’il soit, pourrait lui aussi contribuer à favoriser l’émergence de nouveaux allèles.
Enfin il est intéressant d’explorer la conservation évolutive de cette machinerie moléculaire. On note d’une part que Prdm9 n’est identifiée que chez les métazoaires, avec des absences curieuses dans certaines lignées [9]. Les facteurs qui contrôlent la localisation des crossing-over ne sont connus dans aucun autre organisme en dehors des levures Saccharomyces cerevisiae et Schizosaccharomyces pombe. Chez ces levures, on a observé dans un cas une localisation des sites de cassures double-brin au niveau de régions de chromatine accessibles à proximité des promoteurs de transcription (S. cerevisiae), et dans l’autre cas une spécificité apportée par des facteurs de transcription (S. pombe). Ces situations possèdent quelques points communs avec les mammifères, d’autant plus que PRDM9 fait partie d’une famille de facteurs de transcription (la famille des protéines PRDM), bien qu’une telle activité n’ait pas été mise en évidence à ce jour pour PRDM9.
Conflit d’intérêts
Les auteurs déclarent n’avoir aucun conflit d’intérêts concernant les données publiées dans cet article.
Remerciements
Ce travail a été financé par le Centre national de la recherche scientifique (CNRS), l’Association pour la recherche sur le cancer (ARC), la fondation Jérôme Lejeune et l’Agence nationale pour la recherche (ANR). C. Grey a bénéficié d’une bourse d’Électricité de France (EDF).
Références
- Buard J, de Massy B. Playing hide and seek with mammalian meiotic crossover hotspots. Trends Genet 2007 ; 23 : 301–309. [CrossRef] [PubMed] [Google Scholar]
- Myers S, Freeman C, Auton A, et al. A common sequence motif associated with recombination hot spots and genome instability in humans. Nat Genet 2008 ; 40 : 1124–1129. [CrossRef] [PubMed] [Google Scholar]
- Hayashi K, Yoshida K, Matsui Y. A histone H3 methyltransferase controls epigenetic events required for meiotic prophase. Nature 2005 ; 438 : 374–378. [CrossRef] [PubMed] [Google Scholar]
- Buard J, Barthès P, Grey C, de Massy B. Distinct histone modifications define initiation and repair of meiotic recombination in the mouse. EMBO J 2009 ; 28 : 2616–2624. [CrossRef] [PubMed] [Google Scholar]
- Baudat F, Buard J, Grey C, et al. PRDM9 is a major determinant of meiotic recombination hotspots in humans and mice. Science 2010 ; 327 : 836–840. [CrossRef] [PubMed] [Google Scholar]
- Grey C, et al. Mouse PRDM9 DNA-binding specificity determines sites of histone H3 lysine 4 trimethylation for initiation of meiotic recombination. PLoS Biol 2011 ; 9 : e1001176. [CrossRef] [PubMed] [Google Scholar]
- Myers S, Bowden R, Tumian A, et al. Drive against hotspot motifs in primates implicates the PRDM9 gene in meiotic recombination. Science 2010 ; 327 : 876–879. [CrossRef] [PubMed] [Google Scholar]
- Parvanov ED, Petkov PM, Paigen K. Prdm9 controls activation of mammalian recombination hotspots. Science 2010 ; 327 : 835. [CrossRef] [PubMed] [Google Scholar]
- Ponting CP. What are the genomic drivers of the rapid evolution of PRDM9? Trends Genet 2011 ; 27 : 165–171. [CrossRef] [PubMed] [Google Scholar]
- Mihola O, Trachtulec Z, Vlcek C, et al. A mouse speciation gene encodes a meiotic histone H3 methyltransferase. Science 2009 ; 323 : 373–375. [CrossRef] [PubMed] [Google Scholar]
- Baudat F, de Massy B. SP011 : une activité de coupure de l’ADN indispensable à la méiose. Med Sci (Paris) 2004 ; 20 : 213–218. [CrossRef] [EDP Sciences] [PubMed] [Google Scholar]
- Grey C, Sommermeyer V, Borde V, de Massy B. Déterminants de la carte génétique : le rôle-clé de la spécification des sites de recombinaison méiotique. Med Sci (Paris) 2011 ; 27 : 63–69. [CrossRef] [EDP Sciences] [PubMed] [Google Scholar]
© 2011 médecine/sciences – Inserm / SRMS
Liste des figures
 |
Figure 1. Modèle de ciblage des événements de recombinaison méiotique par PRDM9. A. PRDM9 possède trois domaines connus : un domaine KRAB (impliqué dans des interactions entre protéines), un domaine PR/SET (activité méthyltransférase) et un domaine à doigt de zinc (liaison à l’ADN). B. Grâce à ses doigts de zinc, PRDM9 se lie à un motif de séquence d’ADN spécifique et triméthyle la lysine 4 de l’histone H3 des nucléosomes les plus proches (pastilles oranges). D’autres modifications post-traductionnelles d’histones sont mises en place (pastilles grises), peut-être par des protéines recrutées par PRDM9 (rectangle gris). PDRM9 et/ou l’ensemble spécifique des modifications d’histones présentes est reconnu par un complexe protéique (en rose), non identifié à ce jour, qui va permettre le recrutement et l’activation du complexe d’initiation de la recombinaison symbolisé par la protéine SP011 (en rouge) (d’après [6], avec modifications). |
| Dans le texte | |
Les statistiques affichées correspondent au cumul d'une part des vues des résumés de l'article et d'autre part des vues et téléchargements de l'article plein-texte (PDF, Full-HTML, ePub... selon les formats disponibles) sur la platefome Vision4Press.
Les statistiques sont disponibles avec un délai de 48 à 96 heures et sont mises à jour quotidiennement en semaine.
Le chargement des statistiques peut être long.




