| Issue |
Med Sci (Paris)
Volume 25, Number 5, Mai 2009
Évaluation des risques et perspectives thérapeutiques en oncologie colorectale
|
|
|---|---|---|
| Page(s) | 467 - 472 | |
| Section | M/S revues | |
| DOI | https://doi.org/10.1051/medsci/2009255467 | |
| Published online | 15 May 2009 | |
Micro-ARN (miARN) et cancer : le cas des tumeurs hépatocellulaires
miRNAs in cancer: the case of liver tumors
Inserm U674, Équipe Génétique des tumeurs hépatiques. Université Paris Diderot, Génomique fonctionnelle des tumeurs solides, 27, rue Juliette Dodu, 75010 Paris, France
*
This email address is being protected from spambots. You need JavaScript enabled to view it.
Résumé
Les micro-ARN (miARN) sont des petits ARN régulateurs de l’expression génique. De nombreux travaux ont montré leur implication dans des fonctions physiologiques cellulaires essentielles et en particulier dans les tumeurs. Les altérations d’expression de plusieurs miARN pourraient être directement impliquées dans les mécanismes de carcinogenèse, les miARN pouvant agir comme de véritables oncogènes ou gènes suppresseurs de tumeurs. Par ailleurs, les dérégulations d’expression de certains miARN semblent spécifiques de types ou sous-types particuliers de tumeurs suggérant que ces molécules pourraient être utilisées comme de véritables biomarqueurs tumoraux. Cet article fait le point sur les travaux récents concernant le rôle de la dérégulation d’expression des miARN dans les mécanismes de tumorigenèse hépatocellulaire, ainsi que leur possible utilisation en tant qu’outils diagnostiques ou prédictifs du pronostic de ces tumeurs.
Abstract
Micro RNAs (miRNAs) are small non-coding RNAs that regulate gene expression. Many studies show that they are implicated in essential physiological functions and particularly in tumors. Specific alterations of miRNA expression have been identified directly involved in carcinogenesis. Indeed, miRNAs could act as oncogenes or tumor suppressors. In addition, some miRNAs deregulations seem to be associated to specific tumors subtypes, suggesting that they could be used as tumor biomarkers. In this review, we summarize recent works about miRNAs and hepatocellular tumorigenesis in order to understand the role of these small non-coding RNAs in the carcinogenesis process and their possible use as diagnostic and prognostic markers of these tumors.
© 2009 médecine/sciences - Inserm / SRMS
Les miARN, petits ARN régulateurs de l’expression des gènes
Les miARN sont des petits ARN non codants d’environ 22 nucléotides, capables de réguler de façon négative l’expression des ARN messagers (ARNm) ; ils ont été identifiés pour la première fois en 1993 chez Caenorhabditis elegans avec la découverte de lin-4, miARN essentiel au développement du nématode (voir pour revue [1, 2]). Chez l’homme, les miARN sont en général transcrits à partir de locus chromosomiques isolés ou regroupés en clusters sous la forme d’un transcrit précurseur de plusieurs centaines de nucléotides appelé pri(pour primary)-miARN ; cette molécule d’ARN comporte des structures en tige-boucle d’environ 80 nucléotides (pré-miARN, pour precursor miRNA) qui sont clivées par l’endonucléase nucléaire Drosha [37](→).Après l’exportation du pré-miARN dans le cytoplasme par l’exportine-5 et ran-GTP, les précurseurs sont clivés par Dicer en un miARN mature de 19 à 23 nucléotides. Le miARN mature est ensuite pris en charge par le complexe protéique RISC (RNA-induced silencing complex). Cette association permet l’appariement du miARN à un ARNm cible puis l’induction, suivant la complémentarité des deux molécules, d’une inhibition de la traduction et/ou d’une déstabilisation de l’ARN messager. La petite taille du miARN et la présence de mésappariements entre les séquences du miARN et celles de l’ARNm cible expliquent qu’un miARN peut reconnaître plusieurs ARNm et vice versa, un ARNm peut être reconnu par plusieurs miARN. Ainsi, ces différentes combinaisons d’appariement attestent d’un mécanisme très fin de régulation de l’expression des gènes.
(→) Voir l’article de Patrice Dunoyer, page 505 de ce numéro.
miARN et cancer
Récemment, les rôles des miARN commencent à être élucidés, en particulier dans le contrôle de grandes fonctions physiopathologiques comme le développement, la différenciation cellulaire, l’inflammation ou la réponse immunitaire. En 2002, l’équipe de Carlo Croce a proposé pour la première fois un lien causal entre l’altération de l’expression de miARN et l’émergence d’un processus de tumorigenèse chez l’homme. Les auteurs ont observé un défaut d’expression de 2 miARN, miR-15a et miR-16-1, dans la majorité des leucémies lymphoïdes chroniques (LLC). Ce cluster est localisé dans la région chromosomique 13q14.3, qui est perdue de manière hétérozygote ou homozygote dans plus de la moitié des LLC [3]. Le rôle de miR-15a et miR-16-1 dans la leucémogenèse a été élucidé par la découverte que le gène anti-apoptotique BCL2 était une de leurs cibles directes dans les cellules leucémiques [4]. En accord avec ses propriétés onco-suppressives, miR-16-1 a été identifié comme un régulateur négatif de la croissance cellulaire et de la progression dans le cycle cellulaire [5, 36].
Les miARN peuvent être soumis aux mêmes altérations que des oncogènes ou des suppresseurs de tumeur classiques (amplifications, translocations, délétions, mutations), mais leur expression est le plus souvent globalement réprimée dans les tissus tumoraux [6]. L’analyse fonctionnelle des conséquences de la dérégulation d’expression de miARN sur le contrôle du cycle cellulaire ou la prolifération a permis de proposer de véritables fonctions de suppresseur de tumeur pour plusieurs d’entre eux comme miR-145 ou la famille let-7 qui régulent les oncogènes de la famille RAS (voir pour revue [2, 7]). Inversement, des fonctions oncogéniques ont été proposées pour des miARN surexprimés dans les tumeurs comme le cluster miR-17-92 et miR-21 qui contrôle l’expression des suppresseurs de tumeur PTEN (phosphatase and tensin homolog) et TMP1 (thymidylate synthase), ou miR-155 qui régule RhoA [2, 7]. Ces observations soulignent l’importance du rôle des altérations de l’expression des miARN dans les mécanismes de carcinogenèse, contribuant ainsi à l’accumulation des altérations génétiques et épigénétiques essentielles aux étapes d’initiation et de progression tumorales.
Ces dernières années, l’analyse de l’expression d’un grand nombre de miARN dans des tumeurs humaines a permis d’identifier des profils d’expression spécifiques des tissus tumoraux et non tumoraux de même origine [6, 8]. De plus, ces études globales ont aussi permis l’identification de profils d’expression de miARN spécifiques de sous-types tumoraux définis par des phénotypes ou des génotypes particuliers [6, 9]. Enfin, plusieurs miARN surexprimés (miR-10b, miR-373 et miR-21) ou sous-exprimés (let-7, miR-335 et miR-126) de manière récurrente dans les tumeurs ont été identifiés comme contribuant significativement au phénotype métastatique (pour revue, voir [10]). Ces observations devront être complétées et confirmées par l’analyse d’un très grand nombre de tumeurs, mais elles suggèrent dès à présent l’intérêt de l’utilisation de l’expression des miARN ; ceux-ci pourraient s’avérer être des biomarqueurs utiles pour affiner les classifications moléculaires des tumeurs, mais aussi comme marqueurs pronostiques. La robustesse de ces signatures, qui peuvent être obtenues à partir de prélèvements tissulaires fixés, permettant donc un typage de ces marqueurs dans la plupart des situations cliniques, ne fait que renforcer leur intérêt [11].
Les tumeurs hépatocellulaires : une grande diversité de lésions
Parmi les tumeurs hépatocellulaires secondaires à la prolifération des hépatocytes, on distingue les tumeurs bénignes et les tumeurs malignes.
Les tumeurs hépatocellulaires bénignes sont le plus souvent découvertes chez des femmes. Elles comprennent les hyperplasies nodulaires focales, proliférations hépatocellulaires fréquentes, le plus souvent polyclonales, secondaires à des malformations vasculaires et caractérisées par une activation de la voie β-caténine [12]. À l’inverse, les adénomes hépatocellulaires (AHC) sont des tumeurs rares, monoclonales, dont le principal facteur de risque est la prise de contraception orale. Les AHC peuvent être classés en fonction de leur génotype : mutation inactivatrice d’HNF1α (human hepatocyte nuclear factor 1 α) dans 30-45 % des cas [13], mutation activatrice de la β-caténine (15-19 % des AHC) [14] ou mutation activatrice de gp130 qu’accompagne la présence d’un infiltrat inflammatoire (30-35 % des cas) [15–17].
Les tumeurs hépatocellulaires malignes sont essentiellement représentées par les carcinomes hépatocellulaires (CHC) qui touchent préférentiellement les hommes porteurs d’une cirrhose. Parmi les principaux facteurs de risques, on trouve l’infection par les virus de l’hépatite B (VHB) ou C (VHC), la consommation excessive d’alcool, des maladies génétiques comme l’hémochromatose ou l’exposition à des génotoxiques (aflatoxine B1). Pendant les étapes prénéoplasiques, les hépatocytes accumulent successivement de nombreuses altérations génétiques (les mutations de TP53 et de la ß-caténine étant les plus fréquentes) et épigénétiques (nombreuses méthylations de promoteurs) qui contribuent à la transformation maligne. Récemment, l’analyse transcriptomique globale de CHC a permis de proposer une classification moléculaire de ces tumeurs étroitement liée à leurs caractéristiques cliniques et génétiques [18].
Expression des miARN dans les tumeurs hépatocellulaires bénignes
Dans un travail récent, nous avons analysé l’expression de 250 miARN par RT-PCR quantitative dans une série de 18 tumeurs bénignes (13 AHC et 5 hyperplasies nodulaires focales), 28 CHC, et 4 échantillons de foies normaux. Une analyse non supervisée de ces données d’expression a montré des profils d’expression de miARN très différents dans les tumeurs bénignes, les CHC et les foies normaux. Deux miARN, miR-200c et miR-203, sont sous-exprimés de manière significative dans toutes les tumeurs bénignes étudiées, non seulement par rapport aux tissus normaux mais aussi par rapport aux carcinomes (données validées dans une deuxième série de tumeurs). De plus, nous avons identifié une sous-expression de certains miARN spécifiquement dans deux des principaux sous-types d’AHC. (1) miR-107 est sous-exprimé dans les AHC caractérisés par des mutations inactivatrices d’HNF1α ; dans un système cellulaire nous avons montré que l’expression de miR-107 était sous le contrôle de l’expression du facteur de transcription HNF1a. (2) miR-375 est sous-exprimé dans les AHC ayant une mutation activatrice de la β-caténine ; il existe une corrélation négative forte entre l’expression de miR-375 et celle des gènes cibles de la β-caténine, ce qui suggère une répression de l’expression de miR-375 par cet oncogène [19].
Expression des miARN dans les lésions prénéoplasiques
Dans plus de 90 % des cas, le CHC se développe sur un terrain cirrhotique. L’analyse de tissu hépatique de patients cirrhotiques permet donc d’étudier les étapes très précoces de la carcinogenèse. Jiang et al ont observé une surexpression significative mais modeste d’au moins une vingtaine de miARN dans des cirrhoses d’origine virale B ou C chez des patients présentant un CHC [20]. Par analogie avec les dérégulations d’expression de miARN observées dans différents systèmes cellulaires soumis à des stress métaboliques, la surexpression de miR-22, miR-182b, miR-198, miR-221, et miR-222 dans les cirrhoses d’origine virale pourrait être liée à la réponse cellulaire au stress. Dans leur étude, Varnholt et al ont analysé l’expression de 80 miARN chez des patients présentant un CHC associé à une infection chronique par le VHC [21]. Ils ont montré que les dérégulations d’expression de miARN observées dans les CHC étaient déjà toutes présentes dans les nodules cirrhotiques dysplasiques prénéoplasiques et à un moins grand degré aussi ; ces résultats suggèrent que l’altération d’expression des miARN est un événement survenant précocement au cours de la tumorigenèse. Ainsi, l’analyse de l’expression des miARN semble pouvoir être utilisée comme marqueur précoce d’initiation et de progression de la tumorigenèse.
Altérations de l’expression des miARN dans les CHC
Depuis 2005, une dizaine d’études globales de l’expression des miARN dans les CHC a été publiée (Tableau 1) [19–28]. Varnholt et al. ont montré dans une méta-analyse récente que les résultats de ces différentes études étaient assez peu concordants [29]. La variabilité des résultats obtenus peut être en grande partie expliquée par les différences d’échantillonnage des tumeurs (en particulier concernant les facteurs de risques de CHC), le nombre relativement petit de tumeurs analysées dans chaque étude, l’expression des résultats obtenus dans les tumeurs, qui peut être comparée à ceux obtenus dans du tissu hépatique sain ou dans du foie non tumoral, qui sont très hétérogènes par nature (en particulier selon qu’il existe ou non une cirrhose) ; enfin, les méthodes de quantification (PCR quantitative, microarray, Northern blot) et d’analyse statistique utilisées sont très variables. Cependant, malgré l’hétérogénéité de ces travaux, quelques miARN semblent dérégulés de façon récurrente dans les CHC (Figure 1).
Comparaison des différentes études de profilage d’expression des miARN dans les CHC. MA : microarray ; NB : Northern blot ; RT-PCR quantitative : RT-PCRq ; FNT : foie non tumoral adjacent ; FN : foie normal ; miARN soulignés : miARN communs à au moins 2 études ; VHB : virus de l’hépatite B ; VHC : virus de l’hépatite C.
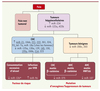 |
Figure 1. miARN dérégulés de manière récurrente dans les tumeurs hépatocellulaires [19–28]. Les miARN dont l’expression est altérée de façon similaire dans au moins 2 études ou plus sont soulignés. L’expression des miARN est associée à des caractéristiques cliniques, génétiques, phénotypiques et des facteurs de risque particuliers de ces tumeurs. ↑: sur-expression dans la tumeur ; ↓ : sous-expression dans la tumeur ; CHC : carcinome hépatocellulaire ; AHC : adénome hépatocellulaire ; VHB : virus de l’hépatite B. |
Faible expression de plusieurs miARN dans les CHC
Une expression faible de miR-122, miR-125a, miR-130a, miR-139, miR-145, miR-150, miR-199a, miR-200b, miR-214 et miR-223 dans les CHC est répertoriée de manière récurrente dans la littérature. Un des cas les plus intéressants est celui de miR-122 [30]. Ce miARN représente à lui seul 70 % de l’expression des miARN du foie ; essentiel au fonctionnement hépatique, il est sous-exprimé dans la majorité des CHC. Récemment, une de ses cibles impliquée dans la régulation du cycle cellulaire, la cycline G1, a été validée expérimentalement dans un modèle cellulaire d’hépatocytes [25]. Par ailleurs, l’observation d’une sous-expression de miR-122 à la fois dans les CHC et les tumeurs bénignes suggère que la dérégulation de miR-122 serait liée à des évènements précoces de tumorigenèse [19]. Enfin, l’expression de miR-122 semble essentielle à la réplication et au maintien du VHC dans l’hépatocyte [31]. Cette observation pourrait expliquer la surexpression de miR-122 spécifiquement observée dans les CHC liés à l’infection virale C [21]. De manière intéressante, Varnholt et al ont montré que la sous expression de miR-145 était corrélée au degré de différenciation des CHC [21]. Outre le fait que des gènes impliqués dans la carcinogenèse pourraient faire partie de ses cibles hypothétiques, miR-145 est aussi sous-exprimé dans d’autres types de tumeurs, suggérant un rôle général dans l’initiation et/ou la progression tumorale.
Surexpression de miARN dans les CHC
Les données de la littérature indiquent une surexpression récurrente delet-7a, miR-21, miR-106b, miR-221, miR-222, miR-224, miR-301et miR-93 dans les CHC. La surexpression de miR-21 est aussi un événement fréquent dans d’autres tumeurs malignes. Des arguments expérimentaux ont démontré que miR-21 contrôlait plusieurs suppresseurs de tumeurs dont PDCD4 (programmed cell death protein 4) [32]. Dans les CHC, il participerait aussi à la sous-expression de PTEN. De plus, une surexpression importante de miR-21 a été observée dans les CHC les plus faiblement différenciés [24]. La surexpression de miR-221 et miR-222 est elle aussi souvent détectée dans les tumeurs humaines et, dans les CHC, miR-222 est associé à un mauvais pronostic [20]. Enfin, récemment, p27Kip1, impliqué dans la régulation du cycle cellulaire, a été validé comme étant une cible de miR-222 dans des modèles expérimentaux de plusieurs cancers dont celui de la prostate [33].
Corrélation entre l’expression de miARN et des caractéristiques génétiques, cliniques ou des facteurs de risque dans les CHC
Comme c’est le cas dans les adénomes, l’expression de miR-375 est diminuée dans les CHC ayant une mutation de la β-caténine par rapport à l’expression observée dans les tumeurs non mutées [19]. Une forte corrélation négative entre l’expression de ce miARN et celle des gènes cibles directs de la β-caténine activée est aussi identifiée. Une expression particulière de certains miARN est aussi associée à des facteurs de risque : une surexpression de miR-96 a été identifiée dans des CHC liés à l’infection par le VHB, ce qui n’est pas le cas dans les tissus hépatiques non tumoraux infectés par le VHB, suggérant un lien entre la surexpression de miR-96 et le processus de carcinogenèse spécifique à l’infection par ce virus. Autre exemple, nous avons observé une diminution de l’expression de miR-126*1 dans les CHC associés à la consommation excessive d’alcool. Cette dérégulation n’est pas retrouvée dans les cirrhoses d’origine alcoolique, suggérant également son association préférentielle au processus de carcinogenèse spécifique à ce facteur de risque [19]. Récemment, Liu et al. ont identifié une surexpression de miR-18a spécifiquement dans des CHC développés chez des femmes. Cette observation est intéressante car les auteurs ont montré que miR-18a régule l’expression du récepteur α des œstrogènes (ERα) bloquant l’effet potentiellement protecteur des œstrogènes [34]. Ainsi, il pourrait contribuer à expliquer la faible incidence des CHC chez la femme par l’action des œstrogènes [34]. Enfin, Budhu et al. ont récemment identifié une vingtaine de miARN dont l’expression est associée au potentiel métastatique des CHC [35].
Conclusion
L’étude de l’expression des miARN apporte de nouvelles informations pour la compréhension des mécanismes de carcinogenèse hépatique. Des profils de dérégulation et d’expression de miARN semblent spécifiques à des sous-groupes de tumeurs, en particulier lorsqu’elles sont associées à des caractéristiques cliniques, génétiques, phénotypiques et des facteurs de risque particuliers. Afin de mieux comprendre le rôle oncogénique ou suppresseur de tumeur des miARN, il est très important d’identifier leurs gènes cibles potentiellement impliqués dans la prolifération cellulaire et ce domaine est en pleine émergence. Par ailleurs, ces mêmes miARN peuvent être sous le contrôle d’oncogènes et/ou de gènes suppresseurs de tumeurs classiques et participer au réseau complexe de contrôle de l’expression des gènes. Enfin, ces petits ARN non codants constituent des outils particulièrement prometteurs pour le développement de nouveaux marqueurs diagnostiques et pronostiques.
L’astérisque indique le brin concerné par la forme mature du miR (nomenclature officielle).
Remerciements
Ce travail a bénéficié de financements de l’ANRS, l’Inserm (réseaux de recherche clinique et réseaux de recherche en santé des populations), et de la Ligue nationale contre le cancer. Y.L. est financé par une bourse de l’ANRS.
Références
- Cullen BR. Transcription and processing of human microRNA precursors. Mol cell 2004; 16 : 861–5. [Google Scholar]
- Finoux AL, Chartrand P. Oncogenic and tumour suppressor microRNAs. Med Sci (Paris) 2008; 24 : 1049–54. [Google Scholar]
- Calin GA, Croce CM. Genomics of chronic lymphocytic leukemia microRNAs as new players with clinical significance. Sem in Oncol 2006; 33 : 167–73. [Google Scholar]
- Cimmino A, Calin GA, Fabbri M, et al. miR-15 and miR-16 induce apoptosis by targeting BCL2. Proc Natl Acad Sci USA 2005; 102 : 13944–9. [Google Scholar]
- Linsley PS, Schelter J, Burchard J, et al. Transcripts targeted by the microRNA-16 family cooperatively regulate cell cycle progression. Mol Cell Biol 2007; 27 : 2240–52. [Google Scholar]
- Lu J, Getz G, Miska EA, et al. MicroRNA expression profiles classify human cancers. Nature 2005; 435 : 834–8. [Google Scholar]
- Schickel R, Boyerinas B, Park SM, Peter ME. MicroRNAs : key players in the immune system, differentiation, tumorigenesis and cell death. Oncogene 2008; 27 : 5959–74. [Google Scholar]
- Liu CG, Calin GA, Meloon B, et al. An oligonucleotide microchip for genome-wide microRNA profiling in human and mouse tissues. Proc Natl Acad Sci USA 2004; 101 : 9740–4. [Google Scholar]
- Fabbri M, Garzon R, Andreeff M, Kantarjian HM, Garcia-Manero G, Calin GA. MicroRNAs and noncoding RNAs in hematological malignancies : molecular, clinical and therapeutic implications. Leukemia 2008; 22 : 1095–105. [Google Scholar]
- Ma L, Weinberg RA. Micromanagers of malignancy : role of microRNAs in regulating metastasis. Trends Genet 2008; 24 : 448–56. [Google Scholar]
- Nelson PT, Baldwin DA, Scearce LM, Oberholtzer JC, Tobias JW, Mourelatos Z. Microarray-based, high-throughput gene expression profiling of microRNAs. Nat Meth 2004; 1 : 155–61. [Google Scholar]
- Rebouissou S, Couchy G, Libbrecht L, et al. The beta-catenin pathway is activated in focal nodular hyperplasia but not in cirrhotic FNH-like nodules. J Hepatol 2008; 49 : 61–71. [Google Scholar]
- Bluteau O, Jeannot E, Bioulac-Sage P, et al. Bi-allelic inactivation of TCF1 in hepatic adenomas. Nat Genet 2002; 32 : 312–5. [Google Scholar]
- Chen YW, Jeng YM, Yeh SH, Chen PJ. P53 gene and Wnt signaling in benign neoplasms : beta-catenin mutations in hepatic adenoma but not in focal nodular hyperplasia. Hepatology 2002; 36 : 927–35. [Google Scholar]
- Zucman-Rossi J, Jeannot E, Nhieu JT, et al. Genotype-phenotype correlation in hepatocellular adenoma : new classification and relationship with HCC. Hepatology 2006; 43 : 515–24. [Google Scholar]
- Rebouissou S, Amessou M, Couchy G, et al. Frequent in-frame somatic deletions activate gp130 in inflammatory hepatocellular tumours. Nature 2008; 457 : 200–4. [Google Scholar]
- Zucman-Rossi J, Amessou M, Bioulac-Sage P, Rebouissou S. Gp130 activating mutations in inflammatory adenomas. Med Sci (Paris) 2008; 24 : 1113–4. [Google Scholar]
- Boyault S, Rickman DS, de Reynies A, et al. Transcriptome classification of HCC is related to gene alterations and to new therapeutic targets. Hepatology 2007; 45 : 42–52. [Google Scholar]
- Ladeiro Y, Couchy G, Balabaud C, et al. MicroRNA profiling in hepatocellular tumors is associated with clinical features and oncogene/tumor suppressor gene mutations. Hepatology (Baltimore, Md 2008; 47 : 1955–63. [Google Scholar]
- Jiang J, Gusev Y, Aderca I, et al. Association of MicroRNA expression in hepatocellular carcinomas with hepatitis infection, cirrhosis, and patient survival. Clin Cancer Res 2008; 14 : 419–27. [Google Scholar]
- Varnholt H, Drebber U, Schulze F, et al. MicroRNA gene expression profile of hepatitis C virus-associated hepatocellular carcinoma. Hepatology 2008; 47 : 1223–32. [Google Scholar]
- Murakami Y, Yasuda T, Saigo K, et al. Comprehensive analysis of microRNA expression patterns in hepatocellular carcinoma and non-tumorous tissues. Oncogene 2006; 25 : 2537–45. [Google Scholar]
- Kutay H, Bai S, Datta J, et al. Downregulation of miR-122 in the rodent and human hepatocellular carcinomas. J Cell Biochem 2006; 99 : 671–8. [Google Scholar]
- Meng F, Henson R, Wehbe-Janek H, Ghoshal K, Jacob ST, Patel T. MicroRNA-21 regulates expression of the PTEN tumor suppressor gene in human hepatocellular cancer. Gastroenterology 2007; 133 : 647–58. [Google Scholar]
- Gramantieri L, Ferracin M, Fornari F, et al. Cyclin G1 is a target of miR-122a, a microRNA frequently down-regulated in human hepatocellular carcinoma. Cancer Res 2007; 67 : 6092–9. [Google Scholar]
- Huang YS, Dai Y, Yu XF, et al. Microarray analysis of microRNA expression in hepatocellular carcinoma and non-tumorous tissues without viral hepatitis. J Gastroenterol Hepatol 2008; 23 : 87–94. [Google Scholar]
- Wang Y, Lee AT, Ma JZ, et al. Profiling microRNA expression in hepatocellular carcinoma reveals microRNA-224 up-regulation and apoptosis inhibitor-5 as a microRNA-224-specific target. J Biol Chem 2008; 283 : 13205–15. [Google Scholar]
- Connolly E, Melegari M, Landgraf P, et al. Elevated expression of the miR-17-92 polycistron and miR-21 in hepadnavirus-associated hepatocellular carcinoma contributes to the malignant phenotype. Am J Pathol 2008; 173 : 856–64. [Google Scholar]
- Varnholt H. The role of microRNAs in primary liver cancer. Ann Hepatol 2008; 7 : 104–13. [Google Scholar]
- Girard M, Jacquemin E, Munnich A, Lyonnet S, Henrion-Caude A. miR-122, a paradigm for the role of microRNAs in the liver. J Hepatol 2008; 48 : 648–56. [Google Scholar]
- Jopling CL, Norman KL, Sarnow P. Positive and negative modulation of viral and cellular mRNAs by liver-specific microRNA miR-122. Cold Spring Harbor symposia on quantitative biology 2006; 71 : 369–76. [Google Scholar]
- Frankel LB, Christoffersen NR, Jacobsen A, Lindow M, Krogh A, Lund AH. Programmed cell death 4 (PDCD4) is an important functional target of the microRNA miR-21 in breast cancer cells. J Biol Chem 2008; 283 : 1026–33. [Google Scholar]
- Galardi S, Mercatelli N, Giorda E, et al. miR-221 and miR-222 expression affects the proliferation potential of human prostate carcinoma cell lines by targeting p27Kip1. J Biol Chem 2007; 282 : 23716–24. [Google Scholar]
- Liu WH, Yeh SH, Lu CC, et al. MicroRNA-18a prevents estrogen receptor-alpha expression, promoting proliferation of hepatocellular carcinoma cells. Gastroenterology 2009; 136 : 683–93 [Google Scholar]
- Budhu A, Jia HL, Forgues M, et al. Identification of metastasis-related microRNAs in hepatocellular carcinoma. Hepatology 2008; 47 : 897–907. [Google Scholar]
- Bousquet M, Dastugue N, Brousset P. MicroARN et translocations chromosomiques dans les hémopathies malignes. Med Sci 2009 (sous presse). [Google Scholar]
- Dunoyer P. La bataille du silence : mécanisme et inhibition du RNA silencing au cours des interactions plante/virus. Med Sci (Paris) 2009; 25 : 505–11. [Google Scholar]
Liste des tableaux
Comparaison des différentes études de profilage d’expression des miARN dans les CHC. MA : microarray ; NB : Northern blot ; RT-PCR quantitative : RT-PCRq ; FNT : foie non tumoral adjacent ; FN : foie normal ; miARN soulignés : miARN communs à au moins 2 études ; VHB : virus de l’hépatite B ; VHC : virus de l’hépatite C.
Liste des figures
 |
Figure 1. miARN dérégulés de manière récurrente dans les tumeurs hépatocellulaires [19–28]. Les miARN dont l’expression est altérée de façon similaire dans au moins 2 études ou plus sont soulignés. L’expression des miARN est associée à des caractéristiques cliniques, génétiques, phénotypiques et des facteurs de risque particuliers de ces tumeurs. ↑: sur-expression dans la tumeur ; ↓ : sous-expression dans la tumeur ; CHC : carcinome hépatocellulaire ; AHC : adénome hépatocellulaire ; VHB : virus de l’hépatite B. |
| Dans le texte | |
Current usage metrics show cumulative count of Article Views (full-text article views including HTML views, PDF and ePub downloads, according to the available data) and Abstracts Views on Vision4Press platform.
Data correspond to usage on the plateform after 2015. The current usage metrics is available 48-96 hours after online publication and is updated daily on week days.
Initial download of the metrics may take a while.




