| Issue |
Med Sci (Paris)
Volume 25, Number 5, Mai 2009
Évaluation des risques et perspectives thérapeutiques en oncologie colorectale
|
|
|---|---|---|
| Page(s) | 441 - 444 | |
| Section | Nouvelles | |
| DOI | https://doi.org/10.1051/medsci/2009255441 | |
| Published online | 15 mai 2009 | |
Les cellules souches intestinales
30 ans d’une histoire exemplaire
Intestinal stem cells: thirty years of a long and exemplary story
Institut de genomique fonctionnelle, departement d’oncologie, 141, rue de la Cardonille, 34094 Montpellier Cedex 05, France
*
Cette adresse e-mail est protégée contre les robots spammeurs. Vous devez activer le JavaScript pour la visualiser.
L’épithélium intestinal est composé de villi et de cryptes (Figure 1). Il est constitué d’une monocouche de cellules qui assurent des fonctions très spécialisées d’une part et le renouvellement de l’épithélium d’autre part. Les cellules spécialisées, différenciées, recouvrent les villi dans l’intestin grêle et se positionnent dans le tiers supérieur des cryptes dans le côlon. Quatre types principaux de cellules différenciées sont détectés dans l’intestin : les cellules caliciformes, qui produisent le mucus nécessaire à l’évacuation des matières solides et à la protection de la muqueuse, les cellules entéroendocrines qui produisent des hormones, les entérocytes qui assurent la fonction d’absorption de l’intestin et les cellules de Paneth impliquées dans la défense vis-à-vis des pathogènes présents dans la lumière intestinale. D’autres cellules sont beaucoup moins représentées, par exemple les cellules « tuft » dont le rôle est encore mal connu. Les cryptes contiennent les cellules en phase de prolifération, aussi bien les cellules progénitrices que les cellules souches. Cette répartition topographique très précise des cellules de l’épithélium intestinal fait de cet organe un très bon modèle d’étude des cellules qui en assurent le renouvellement.
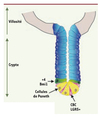 |
Figure 1. L’épithélium intestinal. CBC : crypt base columnar cells. |
L’histoire de l’identification des cellules souches intestinales commence il y a plus de 30 ans
Premières expériences : histologie et marqueurs de prolifération
Quelques scientifiques de renom ont forgé cette histoire (Figure 2) : Charles P. Leblond, Hazel Cheng, Matthew Bjerknes, Christopher S. Potten et Hans Clevers. Au début des années 1970, C.P. Leblond et H. Cheng (Montréal, Canada) identifient des cellules initialement appelées crypt base columnar cells, situées entre les cellules de Paneth à la base des cryptes, et ils publient en 1974 dans l’American Journal of Anatomy leur unitarian theory of the origin of the four epithelial cell types [1]. L’approche technologique utilisée à l’époque consiste alors en une observation histologique très précise couplée à l’utilisation de l’autoradiographie. Par la suite, Potten a analysé la dynamique de renouvellement de cet épithélium grâce à des marquages in vivo des cellules qui incorporaient la thymidine tritiée ou la bromo-déoxy-uridine (brdU) [2, 3]. Très tôt, C. Potten a identifié la zone où les cellules incorporaient activement ces marqueurs et il a contribué de façon très importante à la compréhension non seulement du renouvellement de l’épithélium mais aussi des cryptes elles-mêmes. Le temps de doublement des cellules au fond de la crypte a pu être calculé de même qu’une estimation a pu aussi être faite de la durée de vie d’une crypte. Potten utilisait au départ le terme de cellule clonogénique et pas encore celui de cellule souche. Ces cellules pouvaient donner naissance à des clones de cellules contenant plusieurs types cellulaires, mais pas tous [4].
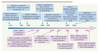 |
Figure 2. Marqueurs de prolifération. |
L’apport des manipulations génétiques
M. Bjerknes (Toronto, Canada), quant à lui, a utilisé un autre stratagème qui lui a permis d’avoir une vision plus fine de la dynamique du renouvellement de l’épithélium intestinal. Il a réalisé une mutagenèse chimique pour introduire des mutations somatiques dans le locus Dlb-1, et marquer ainsi génétiquement et de façon aléatoire les cellules épithéliales [5]. Le gène autosomal dominant Dlb-1b code pour le récepteur d’une lectine, l’agglutinine Dolichos biflorus (DBA), exprimée à la surface des cellules. Des mutations dans l’allèle Dlb-1b d’une cellule souche d’une souris hétérozygote Dlb-1a/Dlb-1b ont pour conséquence la présence d’un ruban de cellules non marquées sur un fond de cellules marquées avec un conjugué DBA-peroxidase. Cette souris permet véritablement de suivre le devenir d’une cellule souche qui a intégré une mutation dans le locus Dlb-1b. Cette stratégie de mutagenèse qui réalise presque un dosage in vivo du site de liaison a permis de démontrer l’existence de progéniteurs à courte durée de vie capables de se différencier en un ou deux types cellulaires et de progéniteurs et cellules souches à durée de vie beaucoup plus longue, capables de se différencier dans tous les types cellulaires. On peut donc considérer que c’est M. Bjerknes qui a réellement démontré expérimentalement le premier la réalité de la cellule souche intestinale. Par ailleurs, dès 1981, M. Bjerknes et H. Cheng proposent également l’existence d’une niche, au sein de laquelle les cellules souches seraient en position 1-4 en partant du fond de crypte [6].
Viennent ensuite tous les travaux du groupe de Hans Clevers à Utrecht. Grâce aux possibilités apportées par la transgenèse et le suivi du lignage des cellules de l’intestin, celui-ci a apporté les preuves formelles que les cellules situées en fond de cryptes, celles-là mêmes décrites par C.P. Leblond en 1974, sont capables de donner naissance à l’ensemble des cellules différenciées de l’épithélium intestinal. La démonstration est le fruit d’un travail organisé et construit, fondée sur l’analyse des dysfonctionnements de certaines voies de signalisation dans le tissu tumoral. Tout d’abord, Hans Clevers a démontré que l’activation de la voie de signalisation appelée Wnt/β-caténine/Tcf4 était un événement essentiel et précoce de la transformation de l’épithélium colique [7, 23]. Puis, il a apporté la preuve que cette voie de signalisation est indispensable au renouvellement du tissu sain [8, 9]. Par des études d’expression de gènes, il a ensuite déterminé la « signature génétique » de la voie β-caténine/Tcf4 [10, 11]. Enfin, grâce à ce travail, un gène, dénommé Lgr5 (leucine-rich repeat-containing G protein-coupled receptor 5) et codant pour un récepteur orphelin à sept domaines transmembranaires, a été identifié comme marqueur permettant de tracer avec exactitude les cellules souches de l’intestin capables de donner naissance aux différents types cellulaires [12]. Deux souris transgéniques ont été produites : l’une a un rapporteur lacZ inséré dans le dernier exon du gène Lgr5 (souris knock-in), l’autre la construction inductible EGFP-IRES-creERT2 insérée dans le premier exon de Lgr5 ; cette seconde souris peut être croisée avec une souris exprimant le gène lacZ dans le locus Rosa26, sous le contrôle du tamoxifène. Grâce à ces souris, le devenir de l’ensemble des cellules différenciées de l’intestin a été suivi à partir des cellules exprimant Lgr5. Les cellules qui expriment ce gène sont localisées en fond de crypte et sont reconnues aujourd’hui comme les cellules souches de l’intestin.
Cellules souches intestinales : tout au fond ou presque au fond des cryptes ?
Cependant, un article publié en 2008 maintient un suspense relatif quant à la nature des « véritables » cellules souches. En effet, utilisant un marqueur d’autorenouvellement dénommé Bmi11, Sangiorgi et Capecchi relancent le débat [13]. Le gène Bmi1 est exprimé dans les cellules en position +4 qui correspondent probablement à celles qui ont été décrites par C.S. Potten il y a plus de 20 ans. Selon ces auteurs, ces cellules se divisent et seraient en amont dans la hiérarchie des cellules caractérisées par M. Bjerknes et H. Clevers comme étant les cellules souches. En effet, l’ablation des cellules Bmi1+ en utilisant une expression conditionnelle de la toxine diphtérique sur le locus Rosa26 entraîne la perte des cellules au fond de crypte.
Ainsi, depuis plus de 30 ans, les scientifiques ont affiné la traque des cellules souches en utilisant les approches technologiques propres à chaque époque [24]. Parallèlement s’est posée la question d’utiliser ces connaissances pour identifier la cellule d’origine du cancer colorectal, et ainsi apporter des arguments supplémentaires à l’hypothèse générale d’une transformation ayant son origine dans les « cellules souches ».
Le cancer intestinal a pour origine la cellule souche
Cellules souches initiatrices de tumeurs
Avant de rentrer dans le vif du sujet, rappelons les grandes étapes qui ont mené à l’hypothèse selon laquelle les cancers auraient pour origine une cellule souche.
Tout a commencé en 1994, dans le domaine hématopoïétique, par l’observation que seule une sous-population rare de cellules humaines de phénotype CD34+CD38-, isolée de la moelle osseuse ou de sang périphérique de patients atteints de leucémie myéloïde aiguë (LAM), était capable, lorsqu’elle était injectée à des souris immunodéficientes SCID (severe combined immune-deficiency) de reproduire beaucoup des aspects de la leucémie observée chez le patient. Cette entité cellulaire pouvait se définir comme une cellule « initiatrice de leucémie » (leukemia- ou cancer-initiating cell) [14]. Ce travail pionnier est dû au laboratoire de John Dick, qui dirige le département de génétique moléculaire de l’université de Toronto. Peu de temps après, en 1997, J. Dick démontre que cette cellule initiatrice de leucémie possède des caractéristiques de « cellule souche » en ce qu’elle reconstitue une hiérarchie de progéniteurs et précurseurs dans plusieurs lignées myéloïdes, et a la capacité de s’autorenouveler [15]. Les mots sont en place : la cellule souche tumorale est née.
De nouveaux marqueurs ont peu à peu été identifiés. Parmi eux, la protéine membranaire CD133 a une histoire particulière car elle a permis d’isoler, à partir de nombreuses tumeurs solides, une fraction de cellules ayant des caractéristiques de cellules initiatrices de tumeurs. Une nouvelle fois, le système hématopoïétique a été pionnier pour l’identification de ce marqueur. CD133 est identifié en 1997 comme marqueur de cellules souches et progénitrices hématopoïétiques saines, les cellules souches dites SRC, ou SCID repopulating cells, exprimant CD133 [16]. Mais l’expression de CD133 n’est pas restreinte au système hématopoïétique et le laboratoire de I. Weissman a par la suite utilisé ce marqueur pour isoler des cellules souches du système nerveux central (SNC) [17]. Dès 2003, le laboratoire de P. Dirks isolait à partir de gliomes une fraction de cellules CD133+ capables de reproduire in vivo des tumeurs dans le SNC contrairement aux cellules CD133- [18]. Ce n’est qu’en 2007 que la démonstration a été faite par deux équipes dont celle de J. Dick de l’existence de cellules CD133+ initiatrices de tumeurs à partir de tumeurs du côlon humain [19]. Par la suite, une polémique est née quant à la pertinence de ce marqueur et quant à sa signification [20]. Toutes les tumeurs ne possèdent pas, c’est vrai, des cellules initiatrices de tumeurs CD133+, mais l’utilisation de ce marqueur a permis des avancées considérables dans le domaine des cellules initiatrices de tumeurs.
Le cas des CS tumorales intestinales : une démonstration directe
La génération d’une nouvelle tumeur à partir de cellules ayant des caractéristiques de cellule souche était un argument fort pour impliquer les cellules souches dans l’émergence du processus tumoral, mais ce n’était pas une démonstration expérimentale en bonne et due forme. La réelle démonstration expérimentale, en ce qui concerne l’intestin, est venue à nouveau du groupe de Hans Clevers [21]. L’expérience suivante a été réalisée : la tumorigenèse de l’intestin est associée très tôt à la présence d’une mutation dans le gène APC (adenomatous polyposis coli) au point que cet événement mutationnel est dit initiateur de la tumeur de l’intestin. H. Clevers a introduit cette mutation sélectivement dans les cellules souches de l’intestin grâce au gène Lgr5 qu’il avait identifié comme marqueur de ces cellules. Très vite sont apparus des foyers adénomateux puis des adénomes et adénocarcinomes. Lorsque cette mutation est introduite dans les cellules progénitrices (descendantes des cellules souches), des foyers adénomateux apparaissent, mais ils n’évoluent pas en adénocarcinomes et leur taille reste limitée. Même si la démonstration formelle que les cellules souches intestinales sont bien le siège de l’initiation tumorale chez l’homme n’est pas encore obtenue, ces travaux suggèrent donc fortement que seules les cellules Lgr5+ sont capables d’engendrer de vraies tumeurs in vivo.
La boucle est en quelque sorte bouclée, tout du moins pour l’instant. Les cellules souches de l’intestin sont le siège de l’initiation de la tumeur, alors que les autres cellules ne semblent pas capables de cette transformation.
Quelles conséquences pour le traitement des patients ?
Ces découvertes ont des répercussions potentiellement très importantes dans le domaine de la thérapeutique. En effet, il est de plus en plus clair que les traitements actuels ne permettent pas d’éradiquer la population de cellules initiatrices de tumeurs [22]. Une meilleure caractérisation, à la fois des cellules souches saines et des cellules initiatrices de tumeurs devrait ainsi permettre de produire des outils thérapeutiques ciblant les cellules initiatrices de tumeurs, avec pour conséquence la prévention de l’apparition de récidives tumorales.
Ainsi, l’histoire de la découverte des cellules souches de l’intestin et des cellules initiatrices de tumeurs intestinales offre un très bel exemple d’une utilisation raisonnée des données issues de modèles physiologiques et pathologiques au bénéfice de la progression des connaissances, et sans frontières.
Le gène Bmi1 code pour un membre de la famille Polycomb, et réprime les gènes P16Ink4a et P19Arf, impliqués dans la régulation du cycle cellulaire. Exprimé par les cellules souches hématopoïétiques et les cellules souches neurales, Bmi1 est nécessaire à leur autorenouvellement.
Références
- Cheng H, Leblond CP. Origin, differentiation and renewal of the four main epithelial cell types in the mouse small intestine. I. Columnar cell. Am J Anat 1974; 141 : 461–79. [Google Scholar]
- Chwalinski S, Potten CS, Evans G. Double labelling with bromodeoxyuridine and 3H-thymidine of proliferative cells in small intestinal epithelium in steady state and after irradiation. Cell Tissue Kinet 1988; 21 : 317–29. [Google Scholar]
- Potten CS, Owen G, Booth D. Intestinal stem cells protect their genome by selective segregation of template DNA strands. J Cell Sci 2002; 115 : 2381–8. [Google Scholar]
- Marshman E, Booth C, Potten CS. The intestinal epithelial stem cell. Bioessays 2002; 24 : 91–8. [Google Scholar]
- Bjerknes M, Cheng H. Clonal analysis of mouse intestinal epithelial progenitors. Gastroenterology 1999; 116 : 7–14. [Google Scholar]
- Bjerknes M, Cheng H. The stem-cell zone of the small intestinal epithelium. V. Evidence for controls over orientation of boundaries between the stem-cell zone, proliferative zone, and the maturation zone. Am J Anat 1981; 160 : 105–12. [Google Scholar]
- Korinek V, Barker N, Morin PJ, et al. Constitutive transcriptional activation by a beta-catenin-Tcf complex in APC−/− colon carcinoma. Science 1997; 275 : 1784–7. [Google Scholar]
- Korinek V, Barker N, Moerer P, et al. Depletion of epithelial stem-cell compartments in the small intestine of mice lacking Tcf-4. Nat Genet 1998; 19 : 379–83. [Google Scholar]
- Pinto D, Gregorieff A, Begthel H, Clevers H. Canonical Wnt signals are essential for homeostasis of the intestinal epithelium. Genes Dev 2003; 17 : 1709–13. [Google Scholar]
- Bienz M, Clevers H. Linking colorectal cancer to Wnt signaling. Cell 2000; 103 : 311–20. [Google Scholar]
- Van der Flier LG, Sabates-Bellver J, Oving I, et al. The Intestinal Wnt/TCF Signature. Gastroenterology 2007; 132 : 628–32. [Google Scholar]
- Barker N, van Es JH, Kuipers J, et al. Identification of stem cells in small intestine and colon by marker gene Lgr5. Nature 2007; 449 : 1003–7. [Google Scholar]
- Sangiorgi E, Capecchi MR. Bmi1 is expressed in vivo in intestinal stem cells. Nat Genet 2008; 40 : 915–20. [Google Scholar]
- Lapidot T, Sirard C, Vormoor J, et al. A cell initiating human acute myeloid leukaemia after transplantation into SCID mice. Nature 1994; 367 : 645–8. [Google Scholar]
- Bonnet D, Dick JE. Human acute myeloid leukemia is organized as a hierarchy that originates from a primitive hematopoietic cell. Nat Med 1997; 3 : 730–7. [Google Scholar]
- Yin AH, Miraglia S, Zanjani ED, et al. AC133, a novel marker for human hematopoietic stem and progenitor cells. Blood 1997; 90 : 5002–12. [Google Scholar]
- Uchida N, Buck DW, He D, et al. Direct isolation of human central nervous system stem cells. Proc Natl Acad Sci USA 2000; 97 : 14720–5. [Google Scholar]
- Singh SK, Clarke ID, Terasaki M, et al. Identification of a cancer stem cell in human brain tumors. Cancer Res 2003; 63 : 5821–8. [Google Scholar]
- O’Brien CA, Pollett A, Gallinger S, Dick JE. A human colon cancer cell capable of initiating tumour growth in immunodeficient mice. Nature 2007; 445 : 106–10. [Google Scholar]
- LaBarge MA, Bissell MJ. Is CD133 a marker of metastatic colon cancer stem cells ? J Clin Invest 2008; 118 : 2021–4. [Google Scholar]
- Barker N, Ridgway RA, van Es JH, et al. Crypt stem cells as the cells-of-origin of intestinal cancer. Nature 2009; 457 : 608–11. [Google Scholar]
- Dylla SJ, Beviglia L, Park IK, et al. Colorectal cancer stem cells are enriched in xenogeneic tumors following chemotherapy. PLoS One 2008; 3 : e2428. [Google Scholar]
- Andreu P, Perret C, Romagnolo B. Wnt et cellules souches intestinales : des liaisons dangereuses… Med Sci (Paris) 2006; 22 : 693–5. [Google Scholar]
- Robine S, Fre S, Huyghe M, Artavanis-Tsakonas S, Louvard D. Notch, un gène clé de l’équilibre entre prolifération et différenciation des cellules épithéliales de l’intestin. Med Sci (Paris) 2005; 21 : 780–2. [Google Scholar]
© 2009 médecine/sciences - Inserm / SRMS
Liste des figures
 |
Figure 1. L’épithélium intestinal. CBC : crypt base columnar cells. |
| Dans le texte | |
 |
Figure 2. Marqueurs de prolifération. |
| Dans le texte | |
Current usage metrics show cumulative count of Article Views (full-text article views including HTML views, PDF and ePub downloads, according to the available data) and Abstracts Views on Vision4Press platform.
Data correspond to usage on the plateform after 2015. The current usage metrics is available 48-96 hours after online publication and is updated daily on week days.
Initial download of the metrics may take a while.




