| Issue |
Med Sci (Paris)
Volume 23, Number 2, Février 2007
|
|
|---|---|---|
| Page(s) | 130 - 132 | |
| Section | Nouvelles | |
| DOI | https://doi.org/10.1051/medsci/2007232130 | |
| Published online | 15 février 2007 | |
Calcium et signalisation Nod
Calcium and Nod signaling
1
Laboratoire des Interactions Plantes-Micro-organismes, INRA UMR 441, CNRS, UMR 2594, BP 52627, 31320 Castanet-Tolosan, France
2
Surfaces cellulaires et Signalisation chez les végétaux, UMR 5546 CNRS-Université Paul Sabatier Toulouse III, Pôle de Biotechnologie végétale, 24, chemin de Borde Rouge, BP 42617 Auzeville, 31320 Castanet-Tolosan, France
*
Cette adresse e-mail est protégée contre les robots spammeurs. Vous devez activer le JavaScript pour la visualiser.
Les plantes de la famille des légumineuses sont capables d’établir une relation symbiotique avec des bactéries du sol, les rhizobium. La symbiose se caractérise par la présence d’organes particuliers, situés au niveau de la racine, appelés nodosités, au sein desquels la bactérie réduit l’azote atmosphérique en ammoniac, assimilable par la plante. En contrepartie, la plante fournit à son symbiote une niche écologique et les substrats carbonés issus de la photosynthèse, nécessaires à son métabolisme. L’établissement de cette interaction symbiotique est très spécifique et résulte d’un dialogue moléculaire entre les deux partenaires, schématisé sur la Figure 1. Dans un premier temps, des exsudats racinaires contenant des flavonoïdes sont perçus par la bactérie et activent la transcription de gènes particuliers : les gènes nod. Ces gènes sont responsables de la biosynthèse de composés appelés facteurs de nodulation ou facteurs Nod, qui, en retour, vont déclencher chez la plante le programme d’organogenèse conduisant à la formation du nodule. Les facteurs Nod, isolés de différentes espèces de rhizobium, possèdent tous la même structure de base : ce sont des lipo-chito-oligosaccharides constitués d’un squelette d’oligochitine de 3 à 5 résidus de N-acétyl-glucosamine, acylé à l’extrémité non réductrice par un acide gras. La nature de l’acide gras (longueur et degré d’insaturation) et des substituants chimiques présents sur le squelette d’oligochitine sont caractéristiques d’une espèce bactérienne donnée et déterminent la spécificité d’interaction entre la bactérie et sa plante hôte [1].
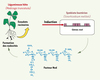 |
Figure 1. La symbiose Rhizobium /légumineuses : un dialogue moléculaire entre la plante et la bactérie. |
Les facteurs Nod sont des molécules extrêmement actives susceptibles d’induire, à de très faibles concentrations (nano- à picomolaires), des réponses variées dans différents tissus de l’hôte, comparables à celles provoquées par la bactérie lors des phases de l’interaction symbiotique : réorganisation du cytosquelette des poils absorbants, induction de gènes symbiotiques végétaux appelés nodulines, mitoses et formation de primordium nodulaires dans le cortex [2]. Au cours de ces dix dernières années, les recherches entreprises sur des légumineuses modèles telles que Lotus japonicus ou Medicago truncatula ont permis : (1) de mettre en évidence une voie de signalisation Nod et d’identifier les gènes qui la contrôlent ; (2) de montrer l’intervention de l’ion calcium à différents niveaux de cette voie.
La voie de signalisation Nod
Les fluctuations calciques
L’application de facteurs Nod à des racines provoque deux types de variations calciques au niveau des poils absorbants : un influx rapide dans la minute suivant l’application, suivi de variations calciques oscillatoires, localisées au niveau péri-nucléaire et nucléaire, intervenant une dizaine de minutes après traitement et se poursuivant pendant 30 à 45 minutes.
L’influx rapide de calcium
Un influx rapide de calcium, suivi d’une sortie de Cl-, de K+ et d’une alcalinisation du cytoplasme a d’abord été observé à l’aide de micro-électrodes sélectives. Ces mouvements ioniques sont à l’origine de la dépolarisation membranaire qui avait été décrite initialement comme le premier événement associé à la perception des facteurs Nod. Cet influx rapide de Ca2+ a également été mesuré à l’aide de sondes calciques fluorescentes (oregon green, calcium green) qui ont permis d’apporter des informations spatiales (pour revue, voir [3]). Ainsi, au sein des poils absorbants en croissance, le calcium se répartit selon un gradient orienté de l’apex à la base. L’ajout de facteurs Nod à des concentrations relativement élevées (10 nM), accentue ce gradient et provoque une vague calcique en direction du noyau, situé en position basale. Les données obtenues sembleraient indiquer qu’au cours de cette phase, les variations calciques feraient intervenir du calcium d’origine extracellulaire mais provenant également de réserves internes comme le suggère, au niveau des poils absorbants, la présence de zones où la concentration en Ca2+ est très élevée.
Les oscillations calciques
Les oscillations calciques (Ca2+ spiking), sont observées en réponse à un traitement par les facteurs Nod pour des concentrations dix fois plus faibles (1 nM) que celles provoquant l’influx rapide. Elles sont localisées dans les régions périnucléaire et nucléaire, et se propagent en direction de l’apex. Le signal se décompose en une phase d’élévation très rapide de la concentration en Ca2+, suivie d’un retour progressif à l’état initial. Ce schéma bi-phasique pourrait correspondre à l’ouverture d’un canal calcique sollicitant un pool interne, puis à sa fermeture et à un re-pompage actif du calcium vers ce même compartiment ou un autre. Cette hypothèse est confortée par des données pharmacologiques mettant en évidence une inhibition des oscillations calciques en présence d’inhibiteurs de canaux calciques et d’une pompe à Ca2+ de type IIA [4, 5]. Les événements intervenant durant la période de latence (10 minutes en moyenne) qui sépare l’influx initial et les oscillations calciques ne sont pas encore caractérisés. Il est probable que ce temps de latence correspond à une modification de l’homéostasie calcique nécessaire à la mise en place des variations oscillatoires. Toutefois, l’influx rapide de calcium et les oscillations constituent deux évènements indépendants pouvant être découplés. Ainsi, chez M. truncatula, certains mutants de nodulation répondent au traitement par les facteurs Nod par un flux rapide de Ca2+ qui n’est pas suivi d’oscillations calciques [6]. L’ensemble de ces données suggère que les deux types de variations calciques sont associés à des voies de signalisation cellulaire différentes mais faisant probablement intervenir des éléments communs.
Chez les eucaryotes, les oscillations calciques sont impliquées dans différents processus physiologiques. Dans plusieurs cas, la réponse biologique peut être modulée en fonction de l’amplitude et/ou de la fréquence des oscillations. Par analogie, les oscillations calciques pourraient transduire, vers les étapes en aval, l’information initiale codée lors de la perception du facteur Nod.
Les protéines de la voie de signalisation Nod
La symbiose constitue un modèle d’étude remarquable en terme de signalisation cellulaire végétale car elle représente l’unique exemple d’organogenèse (formation du nodule), où le composé morphogène (facteur Nod) a été identifié. Son caractère facultatif pour la plante a permis d’engendrer des mutants et de sélectionner, à l’aide d’un crible simple (absence de nodules), ceux qui étaient affectés dans le processus de nodulation. Ainsi, l’approche génétique a permis d’identifier chez M. truncatula six gènes (DMI1, DMI2, DMI3, NFP, NSP1 et NSP2), impliqués dans les étapes précoces de signalisation par les facteurs Nod et nécessaires à des réponses symbiotiques telles que : la déformation des poils absorbants racinaires, l’expression de gènes de nodulines et la division des cellules corticales [7, 8]. Il a été ainsi possible d’ordonner ces gènes par rapport à ces réponses morphologiques et cellulaires, en incluant les variations calciques, et de proposer un modèle de voie de signalisation schématisé sur la Figure 2. De façon inattendue, les plantes affectées dans les gènes DMI1, DMI2 et DMI3 sont également incapables d’établir une interaction symbiotique avec les champignons mycorhiziens à arbuscules, suggérant l’existence de voies de signalisation communes intervenant dans la mise en place des deux symbioses. Récemment, les gènes DMI1, DMI2, DMI3 NFP, NSP1 et NSP2 et leurs orthologues dans d’autres légumineuses ont été clonés. DMI1 code une protéine membranaire présentant une homologie faible avec un canal cationique, DMI2 un récepteur kinase à domaine extracellulaire LRR (leucine rich repeat), DMI3 une protéine kinase calcium- et calmoduline-dépendante, NFP un récepteur kinase à domaine extracellulaire présentant des motifs LysM (lysin motif) connus pour interagir avec les glycanes, NSP1 et NSP2 des facteurs de transcription de la famille GRAS (pour revue, voir [8]).
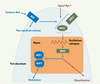 |
Figure 2. Modèle hypothétique des voies de signalisation symbiotiques Nod et Myc chez M. truncatula. NFP : récepteur kinase à domaines LysM ; DMI1 : canal cationique présomptif ; DMI2 : récepteur kinase à domaines LRR ; DMI3 : protéine kinase calcium- et calmoduline-dépendante ; NSP1, NSP2 : facteurs de transcription. |
Le phénotype du mutant nfp (absence totale de réponse aux facteurs Nod) et la présence, dans le domaine extracellulaire de la protéine, de motifs compatibles avec la fonction biochimique de reconnaissance du squelette oligosaccharidique des facteurs Nod, font de NFP le récepteur présomptif des facteurs Nod. Un autre gène, LYK3, contrôlant l’infection de la plante-hôte, et récemment identifié, est également prédit pour coder un récepteur kinase à domaine LysM (LysM-RLK), suggérant des mécanismes de perception complexes à différentes étapes de l’interaction symbiotique. Si la fonction biochimique de DMI1 et DMI2 n’est pas encore connue, le fait que les mutants dmi1 et dmi2 soient affectés au niveau des oscillations calciques indique que DMI1 et DMI2 interviennent dans leur production.
Le décodage des oscillations calciques
Le positionnement de DMI3 en aval des oscillations calciques et le fait que le mutant correspondant soit affecté dans les étapes ultérieures de signalisation, suggèrent fortement que cette protéine assure le décodage des oscillations. DMI3 est une protéine kinase calcium- et calmoduline-dépendante (CCaMK) qui possède un domaine kinase, un domaine de liaison à la calmoduline homologue de celui de la CaMKII des animaux, un domaine présentant une homologie avec la visinine, une calciprotéine neuronale, qui comporte 3 motifs EF-hands de liaison au Ca2+ [9]. Comme la CaMKII, la CCaMK de M. truncatula pourrait percevoir la fréquence des oscillations calciques. Cependant, son mécanisme d’action reste à élucider et notamment les rôles respectifs des domaines visinine et de liaison à la calmoduline dans la perception des variations calciques et l’activation de l’enzyme. En outre, sa localisation nucléaire laisse entrevoir un rôle de cet organite dans la production des oscillations calciques.
En raison de sa présence en un seul exemplaire dans le génome de M. truncatula et de son intervention dans l’établissement de la symbiose mycorhizienne, la CCaMK pourrait assurer un rôle d’aiguillage dans le routage des signaux associés aux deux types de symbiose. Cette hypothèse, séduisante, suppose que l’interaction avec les champignons mycorhiziens se traduise par la production d’une signature calcique différente (en terme de fréquence et/ou d’amplitude des oscillations) de celle associée à la voie Nod, qui serait également décodée par la CCaMK. L’identification d’un facteur Myc, molécule signal équivalente du facteur Nod, ou la détection d’oscillations calciques associées à la mycorhization constitueraient des avancées importantes permettant de mettre à l’épreuve cette hypothèse. Cependant, le fait qu’un gène de CCaMK de riz soit capable de restaurer partiellement l’aptitude à noduler d’un mutant dmi3 de M. truncatula indique que les oscillations calciques induites par les facteurs Nod ne constituent pas une signature calcique spécifique, que seules les légumineuses seraient capables d’interpréter [10].
Conclusions
L’approche génétique a permis d’identifier des gènes clés intervenant dans la voie de signalisation Nod. Il devient maintenant possible d’étudier cette voie d’un point de vue fonctionnel, notamment en relation avec la signalisation calcique. Ainsi, les champs de recherche à explorer concernent notamment les rôles de DMI1 et DMI2 dans la production des oscillations calciques et le rôle de DMI3 dans le décodage de ce signal. Par ailleurs, l’existence de deux réponses calciques distinctes, nécessitant, pour leur induction, des concentrations différentes en facteurs Nod suggère l’existence de plusieurs récepteurs ou d’un système de perceptions multi-composantes présentant des affinités ou des mécanismes d’activation différents.
Références
- Dénarié J, Debellé F, Promé JC. Rhizobium lipo-chitooligosaccharide nodulation factors: signaling molecules mediating recognition and morphogenesis. Annu Rev Biochem 1996; 65 : 503–35. [Google Scholar]
- Cullimore JV, Ranjeva R, Bono JJ. Perception of lipo-chitooligosaccharidic Nod factors in legumes. Trends Plant Sci 2001; 6 : 24–30. [Google Scholar]
- Oldroyd GE, Downie JA. Calcium, kinases and nodulation signalling in legumes. Nat Rev Mol Cell Biol 2004; 5 : 566–76. [Google Scholar]
- Pingret JL, Journet EP, Barker DG. Rhizobium Nod factor signaling. Evidence for a G protein-mediated transduction mechanism. Plant Cell 1998; 10 : 659–72. [Google Scholar]
- Engstrom EM, Ehrhardt DW, Mitra RM, Long SR. Pharmacological analysis of Nod factor-induced calcium spiking in Medicago truncatula. Evidence for the requirement of type IIA calcium pumps and phosphoinositide signaling. Plant Physiol 2002; 128 : 1390–401 [Google Scholar]
- Shaw SL, Long SR. Nod factor elicits two separable calcium responses in Medicago truncatula root hair cells. Plant Physiol 2003; 131 : 976–84. [Google Scholar]
- Catoira R, Galera C, de Billy F, et al. Four genes of Medicago truncatula controlling components of a Nod factor transduction pathway. Plant Cell 2000; 12 : 1647–66. [Google Scholar]
- Stacey G, Libault M, Brechenmacher L, et al. Genetics and functional genomics of legume nodulation. Curr Opin Plant Biol 2006; 9 : 110–21. [Google Scholar]
- Levy J, Bres C, Geurts R, et al. A putative Ca2+ and calmodulin-dependent protein kinase required for bacterial and fungal symbioses. Science 2004; 303 : 1361–4. [Google Scholar]
- Godfroy O, Debellé F, Timmers T, Rosenberg C. A rice calcium- and calmodulin-dependent protein kinase restores nodulation to a legume mutant. Mol Plant-Microbe Interact 2006; 19 : 495–501. [Google Scholar]
© 2007 médecine/sciences - Inserm / SRMS
Liste des figures
 |
Figure 1. La symbiose Rhizobium /légumineuses : un dialogue moléculaire entre la plante et la bactérie. |
| Dans le texte | |
 |
Figure 2. Modèle hypothétique des voies de signalisation symbiotiques Nod et Myc chez M. truncatula. NFP : récepteur kinase à domaines LysM ; DMI1 : canal cationique présomptif ; DMI2 : récepteur kinase à domaines LRR ; DMI3 : protéine kinase calcium- et calmoduline-dépendante ; NSP1, NSP2 : facteurs de transcription. |
| Dans le texte | |
Current usage metrics show cumulative count of Article Views (full-text article views including HTML views, PDF and ePub downloads, according to the available data) and Abstracts Views on Vision4Press platform.
Data correspond to usage on the plateform after 2015. The current usage metrics is available 48-96 hours after online publication and is updated daily on week days.
Initial download of the metrics may take a while.




