Figure 1
Télécharger l'image originale
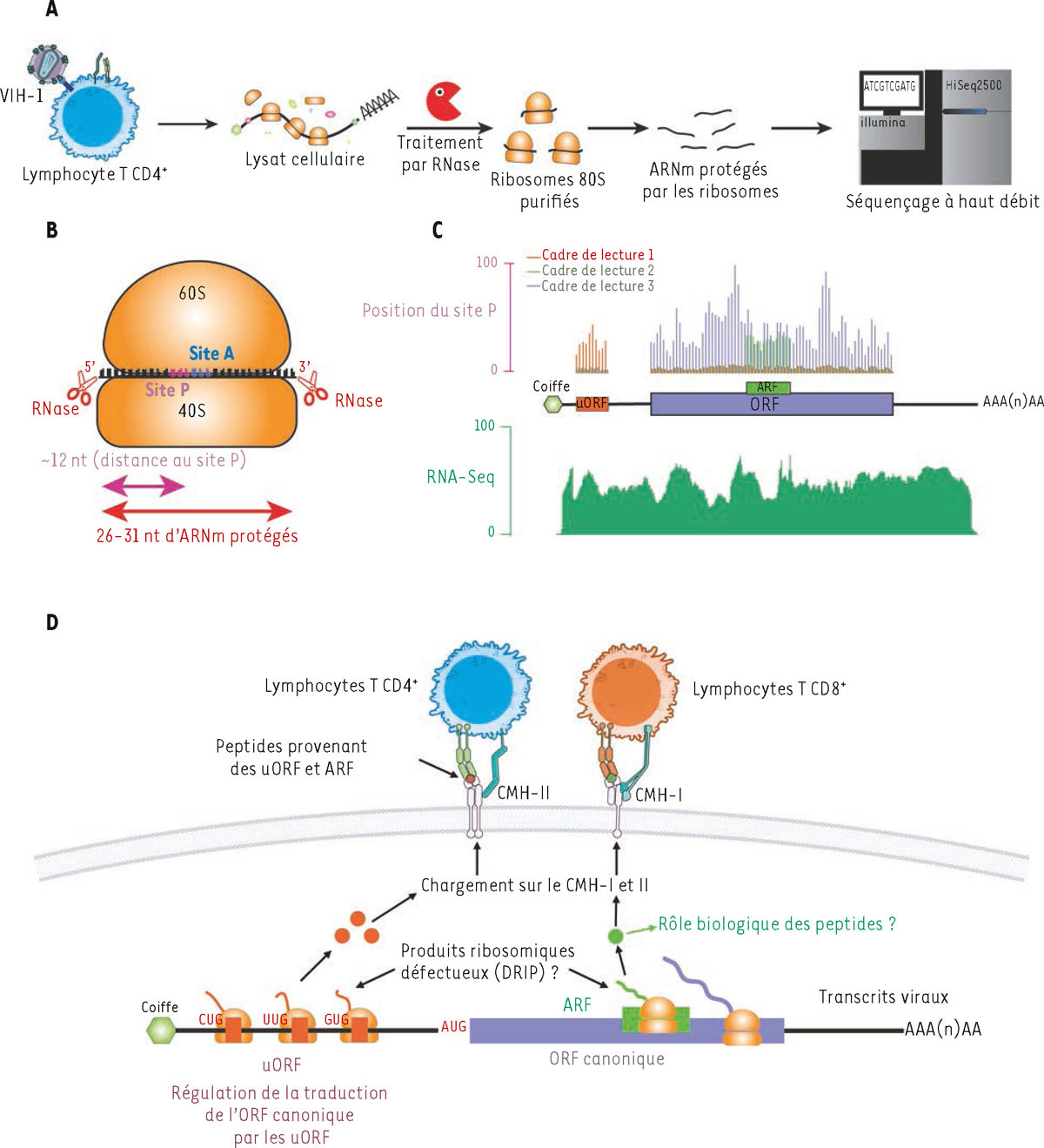
Analyse globale de la traduction des ARN messagers par profilage ribosomique (Ribo-Seq). A. Les lymphocytes T CD4+ infectés par le virus VIH-1 sont incubés avec des inhibiteurs de la traduction des ARN messagers (ARNm), comme le cycloheximide, afin de figer les ribosomes sur les ARNm. Les cellules sont ensuite lysées, et la fraction cytoplasmique, correspondant au compartiment cellulaire où a lieu la traduction des ARNm, est récupérée. Les lysats obtenus sont ensuite séparés en deux fractions. La première est utilisée pour extraire les ARNm et mesurer, par « séquençage massif en parallèle » (RNA-sequencing, RNA-Seq), le degré d’expression des gènes correspondants. La deuxième est incubée avec des ribonucléases (généralement la RNase I, qui clive l’ARN simple brin quelle que soit sa séquence nucléotidique) qui vont dégrader toutes les régions d’ARN accessibles à l’exception de celles qui sont associées aux protéines se liant à l’ARN et de celles associées aux ribosomes 80S. Les ribosomes étant plus denses et volumineux que les protéines libres et autres complexes ribonucléoprotéiques, ils peuvent être purifiés dans un gradient de sucrose, sur coussin de sucrose ou par chromatographie d’exclusion. Une fois les ribosomes 80S isolés, les fragments d’ARNm protégés sont récupérés, puis utilisés pour préparer des banques d’ADN complémentaire (ADNc) qui seront séquencées à haut débit. B. Les fragments d’ARNm protégés par le ribosome ont généralement une longueur comprise entre 26 et 31 nucléotides. La position du site P du ribosome (qui contient la chaîne polypeptidique associée au dernier acide aminé incorporé) peut être extrapolée en ajoutant un décalage d’environ 10 nucléotides en direction 3’ à partir de l’extrémité 5’ de la séquence d’ARNm protégée par le ribosome. On peut ainsi déterminer, pour chaque ribosome, son cadre de lecture de l’ARNm en cours de traduction. C. Une fois la position de chaque site P alignée sur le transcriptome cellulaire et viral, il est possible d’identifier, pour chaque transcrit, la séquence de codons « principale » ainsi que des séquences codantes « alternatives » (uORF, ARF, etc). D. En appliquant le profilage ribosomique aux cellules infectées par le VIH-1, les chercheurs ont pu identifier des évènements de traduction « non canonique », conduisant à la production de peptides viraux inconnus jusqu’alors. Certains de ces peptides viraux peuvent être chargés sur les molécules du complexe majeur d’histocompatibilité (CMH) pour être présentés, à la surface des cellules infectées ou de cellules présentatrices d’antigènes, aux lymphocytes T CD4+ et CD8+. Figure réalisée à l’aide de NIAID Visual & Medical Arts.
Current usage metrics show cumulative count of Article Views (full-text article views including HTML views, PDF and ePub downloads, according to the available data) and Abstracts Views on Vision4Press platform.
Data correspond to usage on the plateform after 2015. The current usage metrics is available 48-96 hours after online publication and is updated daily on week days.
Initial download of the metrics may take a while.




