| Issue |
Med Sci (Paris)
Volume 19, Number 8-9, Août-Septembre 2003
|
|
|---|---|---|
| Page(s) | 865 - 872 | |
| Section | M/S Revues : Dossier Technique | |
| DOI | https://doi.org/10.1051/medsci/20031989865 | |
| Published online | 15 August 2003 | |
Prix Nobel de chimie 2002
Spectrométrie de masse et résonance magnétique nucléaire
Nobel Prize 2002 for chemistry
Mass spectrometry and nuclear magnetic resonance
1
Laboratoire de Chimie Biologique Organique et Structurale, Universite Pierre et Marie Curie, Bâtiment 74, Porte 721, 4, place Jussieu, 75252 Paris Cedex 05, France
2
Muséum National d’Histoire Naturelle, 43, rue Cuvier, 75231 Paris Cedex 05, France
*
This email address is being protected from spambots. You need JavaScript enabled to view it.
Résumé
En 2002, le Prix Nobel de Chimie a été décerné à trois grands scientifiques, John B. Fenn et Koichi Tanaka pour la spectrométrie de masse et Kurt Wüthrich pour la résonance magnétique nucléaire. Il récompense ainsi les idées innovantes qui ont conduit à développer, à l’interface chimie-biologie, des méthodologies spectroscopiques majeures initialement introduites en chimie analytique. La découverte de nouvelles méthodes douces d’ionisation en spectrométrie de masse, et la conception d’une stratégie d’attributions séquentielles des signaux de résonance magnétique nucléaire de biopolymères, ont permis l’application de ces deux méthodologies puissantes et complémentaires à la détermination de structures de macromolécules du vivant, protéines, acides nucléiques (ADN, ARN) et polysaccharides, etc. Par l’élucidation de leurs édifices (structures planes et tridimensionnelles) et des mécanismes moléculaires régissant leurs interactions, ces travaux fournissent des clés précieuses pour la compréhension des mécanismes moléculaires du vivant.
Abstract
The Nobel Prize in Chemistry for 2002 has been awarded to two powerful spectroscopic methodologies through three valorous scientists, John Fenn and Koichi Tanaka, for mass spectrometry and Kurt Wüthrich for nuclear magnetic resonance. These techniques were previously known for their intensive use in chemical analysis. They are now developed at the chemistry/biology interface. Two new methods of soft ionization in mass spectrometry and a strategy of sequential assignment of nuclear magnetic resonance signals of biopolymers now allow the use of these powerful and complementary methodologies for the structural analysis of biological macromolecules, proteins, nucleic acids (DNA, RNA) and polysaccharides. Through the elucidation of their planar and three-dimensional structures and of the molecular mechanisms that govern their interactions, these techniques now may afford precious clues for understanding the molecular mechanisms of life.
© 2003 médecine/sciences - Inserm / SRMS
Trois grands scientifiques se partagent le Prix Nobel de Chimie 2002 : John B. Fenn (professeur à l’Université Virginia Commonwealth de Richmond, États-Unis), Koichi Tanaka (chercheur à la Société Shimadzu, Kyoto, Japon), et Kurt Wüthrich (professeur à l’Institut de Biologie Moléculaire et de Biophysique de Zurich, Suisse et Professeur invité au Scripps Research Institute de La Jolla, États-Unis). Le Prix Nobel récompense leur contribution déterminante au développement et à l’application de la spectrométrie de masse (pour les deux premiers) et de la résonance magnétique nucléaire (pour le troisième) à l’étude de macromolécules du vivant et de leurs interactions supramoléculaires. De plus, ce Prix Nobel met à l’honneur l’interface entre la physique, la chimie et la biologie. Il illustre l’apport d’une telle interdisciplinarité au domaine des sciences de la vie en fournissant des clés pour la résolution des questions fondamentales de la biologie. La spectrométrie de masse (SM) et la résonance magnétique nucléaire (RMN) font partie intégrante des approches analytiques de la chimie et de la biochimie dont certaines ont déjà été couronnées d’un Prix Nobel. Il s’agit de: (1) la micro-analyse organique (Fritz Pregl, Graz, Autriche, 1923); (2) la polarographie (Jaroslav Heyrovsky, Prague, Tchécoslovaquie, 1959); (3) l’électrophorèse (Arne Tiselius, Uppsala, Suède, 1948) et la chromatographie de partition (Archer J.P. Martin et Richard L.M. Synge, Bucksburn, Royaume-Unis, 1952). Ces méthodes spectrochimiques contribuent de façon complémentaire à la compréhension des mécanismes intimes régissant le fonctionnement des macromolécules du vivant au sein même de la cellule. Elles ont pour application l’introduction de nouveaux médicaments ou de méthodes diagnostiques rapides et puissantes.
Deux méthodes révolutionnaires d’analyse spectrochimique de structures des biomolécules
Depuis longtemps, la spectrométrie de masse et la RMN sont reconnues comme des outils complémentaires et incontournables pour élucider la structure de molécules organiques car elles donnent accès à la masse moléculaire et à l’enchaînement d’édifices moléculaires en précisant leur conformation et, dans certains cas, la configuration de sites chiraux. Elles offrent aujourd’hui beaucoup plus en s’adressant aux biopolymères naturels, protéines, oligonucléotides (ARN, ADN) ou polysaccharides: l’enchaînement des acides aminés, des nucléotides, ou des monosaccharides peut ainsi être déchiffré, brique par brique, et les interactions inter- et intramoléculaires caractérisées dans le cas d’associations supramoléculaires.
La première partie de ce Prix Nobel de Chimie 2002 reconnaît les avancées considérables apportées à la spectrométrie de masse, constamment en évolution, par l’introduction de nouvelles méthodes douces d’ionisation applicables aux biomolécules. Ces méthodes permettent l’ionisation de biomolécules fragiles et de haute masse moléculaire en évitant leur dégradation, par la production d’agrégats, lors du passage en phase gazeuse. Ainsi, dès le milieu des années 1980, John Fenn et Koichi Tanaka ont introduit de nouvelles méthodes de désorption-ionisation comme l’électronébulisation (electrospray ionization, ESI) et la désorption douce par laser (soft laser desorption, SLD). Ces méthodes ont contribué à divers niveaux à la description du génome, à l’exploration du protéome ainsi qu’à l’identification du métabolome (métabolites biosynthétisés par un organisme), incluant la possibilité de distinguer des conformations biomoléculaires.
La seconde moitié du Prix Nobel récompense la RMN, technique déjà bien connue des chimistes organiciens pour sa capacité de résoudre les problèmes de structure, de stéréochimie et de dynamique des molécules. Grâce à Kurt Wüthrich, cette méthode est devenue applicable à la biologie structurale, en permettant la résolution des structures spatiales des macromolécules biologiques en solution, et en particulier des protéines.
Questions sur la connaissance de l’infiniment petit en biologie : de la précision pour une meilleure compréhension des mécanismes intimes de la vie!
Tous les organismes vivants, bactéries, plantes et animaux, disposent des mêmes familles de macromolécules biologiques (édifices primaires associés à leurs conformations) responsables selon leurs structures des interactions moléculaires et des réactions à l’origine de la vie. Ces biomolécules sont de trois types: (1) les acides nucléiques (acide désoxyribonucléique, ADN et acide ribonucléique, ARN) qui mémorisent les informations codifiées permettant la programmation des cellules; (2) les protéines qui assurent les principales fonctions biologiques; (3) les polysaccharides qui, outre leur fonction de réserve énergétique, interviennent dans de nombreux processus de reconnaissance moléculaire. Ainsi, les déterminations structurales sont un passage obligé dont dépend la compréhension des mécanismes du vivant. Aujourd’hui, à l’ère de la génomique et de la protéomique, la connaissance des structures tridimensionnelles des protéines apparaît comme le maillon complémentaire qui permet de comprendre les mécanismes biomoléculaires intervenant dans leur fonctionnement.
Par ailleurs, l’apparition de nouvelles maladies dues à des anomalies de la structure spatiale de certaines protéines accroît encore la nécessité d’accéder à leurs structures tridimensionnelles. Ainsi en est-il de l’encéphalopathie spongiforme bovine (ESB) (→) qui implique vraisemblablement, comme agent infectieux transmissible entre espèces, une protéine qui devient pathogène lorsqu’elle adopte un repliement tridimensionnel incorrect (protéine prion). De même, certaines démences séniles, comme la maladie d’Alzheimer, sont également liées à des perturbations de la structure spatiale d’un fragment protéique normalement présent dans le cerveau sain, le peptide amyloïde (→→).
(→) m/s 2002, n° 1, p. 62 et n° 12,p. 1267
(→→) m/s 2002, n° 6-7, p. 717
Pour répondre aux questions posées, chimistes et biochimistes travaillent ensemble à élucider les structures dans l’espace de ces protéines afin de comprendre les mécanismes gouvernant leur fonctionnement et leurs interactions avec d’autres molécules partenaires. Les avancées apportées par les trois lauréats du Nobel de Chimie 2002 dans les deux grandes méthodes d’analyse que sont la spectrométrie de masse et la RMN donnent aujourd’hui aux chercheurs des moyens nouveaux, puissants et efficaces, pour atteindre les structures de biomolécules de plus en plus grosses et complexes et répondre ainsi aux attentes de la société.
Enfin, ces méthodes sont des outils diagnostiques de choix dans des domaines aussi variés que l’analyse sanitaire dans la filière agro-alimentaire, l’environnement et l’action sanitaire pour la détection de bactéries ou de virus et, enfin, la protection civile grâce à la détection d’agents biologiques pathogènes ou l’identification de toxines introduites lors d’actions terroristes. La sensibilité et l’efficacité de ces méthodes permettent de donner des réponses rapides.
Accès à la masse moléculaire et à la structure de biomolécules intactes en spectrométrie de masse
Une bien longue aventure partant de l’élément hydrogène pour arriver aux macromolécules biologiques!
La méthode est apparue dans sa forme la plus simple à la fin du XIXe siècle (Sir J.J. Thomson, 1906). Elle a permis la mesure de la masse atomique de l’hydrogène, l’élément le plus simple (W. Aston, 1922), et la découverte d’isotopes comme le deutérium (H. Hurey, 1934). L’étude structurale d’une molécule par spectrométrie de masse passe par une étape incontournable qui est son ionisation: seules les formes ionisées peuvent être séparées et analysées selon leur rapport masse/charge à l’aide d’un champ électrique, variable ou non selon le type d’analyseur. Cette étape fait éventuellement suite à une séparation des molécules par chromatographie en phase gazeuse ou liquide, s’il s’agit d’un mélange. La production des ions en phase gazeuse implique, au préalable, l’évaporation de l’échantillon dans le vide. Si cette approche est adéquate pour les molécules organiques qui sont des systèmes volatiles, il n’en est pas de même pour les biomolécules. En fait, celles-ci étant généralement très polaires et thermiquement fragiles, leur évaporation est impossible sans les dégrader par pyrolyse: comment chauffer du sucre pour le faire passer en phase gazeuse sans en faire du caramel ? Ce point constituait une limite de la spectrométrie de masse qui a été franchie durant la période 1975-1985. En effet, différents modes de désorption/ionisation sous vide ont été introduits comme alternatives au cours de cette décennie. Il s’agit principalement de la désorption par champs (FD, field desorption, Beckey, 1968), trop souvent oubliée mais à l’origine des autres méthodes de désorption, et du bombardement par particules rapides d’une solution de biomolécule dans une matrice, utilisant comme projectiles des atomes rapides dans le cas du bombardement par atomes rapides (FAB, fast atom bombardment, M. Barber, 1980) ou des ions (LSIMS, liquid secondary ion mass spectrometry, Benhingoven, 1975). C’est également à cette époque que la désorption par impulsion de rayon laser infra-rouge apparaît (F.Hillenkamp et R.J. Cotter). Il s’agit du premier pas vers les méthodes de désorption douce par laser utilisant le mode ultraviolet et une matrice (SLD, soft laser desorption) et la désorption/ionisation laser assistée par matrice (MALDI, matrix-assisted laser desorption ionization). Les premiers spectres de masse de l’insuline et du lysozyme de jaune d’oeuf présentant des ions quasi moléculaires ont alors pu être enregistrés. Des stratégies de détermination de séquences protéiques à l’échelle de la nanomole se sont développées par le FAB comme par exemple pour l’hémoglobine. La spectrométrie de masse en tandem SM/SM (F. McLafferty, 1969), qui conduit à des fragmentations sélectives à partir d’un ion précurseur choisi, a constitué la dernière étape permettant à cette méthode d’être dédiée à part entière à la biologie. Elle a ainsi été un outil de choix pour mettre en évidence les premières modifications post-traductionnelles de protéines. Les efforts grandissants d’autres groupes de recherche dans le domaine de l’électrohydrodynamique, pour la production d’aérosols chargés ou non, ont donné accès aux premiers systèmes de couplage entre la chromatographie liquide et la spectrométrie de masse (CL/SM). Dans ce cas, l’ionisation des aérosols par réactions ion-molécule après évaporation est induite par une décharge électrique sous pression atmosphérique pour de petites molécules organiques (APCI [atmospheric pessure chemical ionization]). La production d’aérosols chargés sous pression atmosphérique a ouvert la voie à la découverte du mode électronébulisation (ESI). Ainsi, la découverte de l’ESI par J.B. Fenn et du SLD par K. Tanaka, technologies révolutionnaires dans le domaine de l’analyse de macromolécules du vivant, résulte de successions d’innovations technologiques mises en route dès 1965.
Un principe fondé sur la désorption d’agrégats et leur désolvatation
Le lien entre les deux méthodes, SLD [1] et ESI [2], trouve son origine dans le principe même des processus de désorption (Figure 1). Toutes deux conduisent à des espèces quasi microscopiques, les agrégats, mais qui résultent de conditions différentes utilisant des gouttelettes chargées formées sous un champ électrique à partir de nébulisation pour l’ESI ou un panache de matière excitée engendré par ablation laser d’une surface où est déposée une matrice pour le SLD. Ces agrégats sont constitués d’un grand nombre de molécules de solvant en mode ESI ou de matrice pour le SLD. Ils stabilisent une (ou plusieurs) biomolécule(s) multichargée(s) selon leur taille et leur forme. Par le jeu de transferts d’énergie, une cascade de désolvatations conduit à la libération d’ions quasi moléculaires désolvatés, avec le minimum d’énergie interne. Ces étapes étant très rapides (de l’ordre de la microseconde), le processus de destruction moléculaire par pyrolyse se trouve limité dans cette période d’ionisation. Une méthode proche du SLD, le MALDI s’en distingue essentiellement par la nature de la matrice utilisée, poudre de cobalt ultrafine et colloïdes dans du glycérol: pour la première, et matrices organique pour la seconde (Figure 1).
 |
Figure 1. Principe des processus de désorption/ionisation de grosses biomolécules. A. En mode ESI (electrospray ionization), un aérosol formé à partir d’une solution est soumis à un puissant champ électrique sous pression atmosphérique pour conduire à des micro-gouttelettes fortement chargées (5+, 6+, 7+). De celles-ci, un processus d’« évaporation ionique » produit des agrégats chargés de faible énergie, libérant des biomolécules multi-chargées. B. En mode SLD (soft laser desorption), en revanche, après l’impact du rayon laser, de gros agrégats constitués de matrices neutres, mais excitées, sont produits par ablation de la surface. Lors de processus de désolvatation en cascade, ces agrégats donnent principalement des macromolécules « simplement chargées » (+, 2+). Déconvolution: transformation mathématique d’un ensemble des signaux d’états m/z, de charge z (n = z), différents (n = n protons ajoutés), tel que m/z = (M + n)/n en un signal M qui correspond à la masse moléculaire de la macrobiomolécule. Le chronomètre représente une image de la mesure du temps de vol des ions selon leur vitesse (les plus gros étant les plus lents au contraire des plus légers qui seront les plus rapides). L’ensemble des ions donne une énergie cinétique constante pour une valeur de z donnée (d’après ChemChannels.com-the Nobel Prize in Chemistry). |
Caractéristiques et limites des analyses
En général, les ions produits sous ESI [2] emportent une plus grande distribution de charges qu’en MALDI [1]. Cette distribution peut être contrôlée et permet de calculer avec précision les masses moléculaires. L’analyse des ions quasi moléculaires donne accès : (1) aux masses moléculaires évoluant de quelques milliers à plusieurs millions d’unités u (u=g/6.1023, le gramme divisé par le nombre d’Avogadro) avec une précision évoluant de 10−1 % à 10−4 % d’erreur selon la masse et l’analyseur; et (2) à la stoechiométrie dans le cas de systèmes non covalents. Les analyses sont possibles de la femtomole à la picomole d’échantillon purifié ou d’un mélange de peptides fournis par digestion enzymatique d’une protéine. L’analyse de plus faibles quantités par la technique nanospray est possible. Le temps d’analyse peut être très court (inférieur à la minute), ce qui permet aux centres de génotypage et aux plates-formes protéomiques de travailler sous de très hauts débits (plusieurs milliers d’analyses par jour) à l’aide de robots. La détermination de séquences de protéines connues est alors réalisée par interrogation de banques de données.
John B. Fenn et l’electrospray
Expérimentateur passionné, entouré de ses étudiants (M.Yamashita, C.M. Whitehouse et M. Mann), John Fenn a découvert l’electrospray à plus de 65 ans [2]. Ce résultat est l’aboutissement d’un long travail original sur les brouillards et les aérosols soumis à des champs électriques intenses. En fait, le principe en avait déjà été envisagé en 1968 par M. Dole, lors d’études sur les faisceaux de gros ions moléculaires désolvatés par des gaz inertes. C’est en utilisant un gaz desséchant à contrecourant (méthode également employée durant la même période dans un laboratoire russe), que John B. Fenn a pu, en 1984, observer des ions produits sous pression atmosphérique. Puis, il a étudié l’ionisation de polyéthylène glycols de très hautes masses moléculaires (au-delà du million d’unités) et portant plus de mille charges positives. Enfin, il a appliqué sa méthode aux molécules de taille moyenne (peptides et polysaccharides), puis aux protéines. Après multi-ionisation à partir de gouttelettes chargées, la protéine est libérée à l’état gazeux après désolvatation et, ce qui est tout particulièrement intéressant, en conservant une mémoire de sa conformation initiale en solution. Le processus conduit à la formation d’une multiplicité d’ions portant un nombre variable de charges. John B. Fenn a eu la clairvoyance de considérer que la complexité de ces spectres était en fait un avantage, car la précision des mesures en était accrue. Il a décrit le secret de la méthode dans sa théorie des ions multichargés en 1987. Aujourd’hui, à 86 ans, plus que jamais passionné par les problèmes posés par la biologie, il contribue toujours activement à l’effort collectif visant à comprendre les mécanismes intimes de ce mode de désorption. De cette technique, les modes ion-spray et nanospray ont été développés, permettant l’étude de mélanges de plus en plus complexes et la détection de quantités de matière toujours plus faibles (de l’ordre de la zemptomole, soit 10−21 mole).
Koichi Tanaka et la désorption laser douce
C’est au cours d’une conférence que K. Tanaka, employé par la société Shimadzu, alors âgé de 28 ans, présenta en 1987 l’application de la SLD aux grosses protéines intactes comme le cytochrome C, le chymotrypsinogène et la carboxypeptidase A. Selon cette méthode, ces protéines, de masses moléculaires comprises entre 12000 et 35000 u, sont « désorbées » intactes sous forme d’ions simplement et doublement chargés. L’idée originale développée par K. Tanaka a consisté à employer, en présence d’une matrice constituée de colloïdes dispersés dans du glycérol, un laser à azote dont la longueur d’onde de 330 nm n’était pas absorbée par les résidus aromatiques des protéines [1]. Il faut souligner que la même année, la désorption/ionisation assistée par matrice (MALDI) était introduite par F.Hillenkamp et M. Karas [3], qui utilisaient un laser à 266 nm associé à une matrice d’acide nicotinique. Cette méthode a permis la désorption de protéines de masses moléculaires supérieures à 10000 u. C’est en fait cette dernière méthode qui a été développée et est aujourd’hui la plus utilisée. Elle a même fait oublier la SLD, tout comme la désorption par laser qui l’avait précédée. Alors qui devait être primé? Ce n’est ici ni le moment ni le lieu pour en débattre!
Les développements et l’avenir du MALDI
Aujourd’hui, l’innovation se poursuit dans ce domaine et permet d’introduire de nouvelles techniques comme: (1) le DIOS (desorption/ionization on porous silicon) pour l’étude de biomolécules de petite taille (de 150 à 2000 u); (2) le SALDI (surface-activated laser desorption ionization) qui utilise le graphite comme surface; (3) le SELDI (surface-enhanced laser desorption ionization) caractérisé par l’emploi de cibles où sont fixées des anticorps spécifiques d’une protéine (ou d’une famille de protéines) permettant sa purification à partir du milieu naturel (plasma, urines, etc.) et sa désorption par impact laser. Dans le domaine du MALDI, différents développements sont apparus: (1) le couplage CL-MALDI qui est cependant resté sans succès bien qu’amélioré par l’emploi d’aérosols; (2) l’AP-MALDI (atmospheric pressure-MALDI) qui conduit à des espèces ionique, plus stables par relaxation et à une très grande sensibilité. Son développement sera vraisemblablement déterminant pour le mode CL/MALDI. Mais, à ce jour, la plus belle application est sans conteste l’imagerie moléculaire par MALDI qui permet l’étude de peptides, de protéines et d’acides nucléiques directement sur des coupes de biopsies ou de tissus, et fournit ainsi de véritables cartes moléculaires des échantillons.
La résonance magnétique nucléaire des macromolécules biologiques en solution : un accès à leur structure tridimensionnelle dans des conditions proches du vivant
Vis-à-vis des questions soulevées par une protéine et son rôle dans l’organisme, l’apport de la RMN consiste à définir sa topologie, c’est-à-dire l’organisation spatiale des atomes qui la composent. La radio-cristallographie aux rayons X était jusqu’alors la seule méthode capable d’apporter cette information et a d’ailleurs déjà été couronnée par le Prix Nobel de Chimie attribué à Max Perutz en 1962. Cependant, par les méthodes utilisant la RMN, la protéine peut être étudiée non plus à l’état cristallin, mais en solution, c’est-à-dire dans un état plus proche de son environnement naturel dans la cellule. De surcroît, la dynamique des différentes régions de la protéine en solution devient dès lors accessible, ouvrant des perspectives quant à la résolution des mécanismes intimes de son fonctionnement selon son environnement.
Le principe de base de la RMN repose sur les propriétés magnétiques de certains noyaux comme par exemple le proton (1H), le carbone (13C) et l’azote (15N), trois noyaux parmi les plus représentés dans les macromolécules du vivant. Lorsqu’ils sont placés dans un champ magnétique intense, ces noyaux sont capables, via ce que l’on nomme leur spin, d’absorber de l’énergie et d’entrer en résonance. Plus encore, leur fréquence de résonance ne dépend pas uniquement de la fréquence du champ magnétique, mais aussi de leur environnement chimique. De surcroît, les spins nucléaires des différents noyaux d’une molécule (comme par exemple les protons) interfèrent, engendrant des structures fines interprétables en termes structuraux. Ces deux paramètres, couramment connus respectivement sous les noms de « déplacement chimique » et de « couplage scalaire » sont à la base de l’utilisation de la RMN pour établir la structure des molécules.
Ce n’est pas la première fois que la RMN est récompensée par un Prix Nobel. En effet, c’est en 1952 que Félix Bloch et Edward Purcell (Universités de Stanford et d’Harvard aux États-Unis) se sont vu remettre le Prix Nobel de Physique pour la mise en évidence des concepts de base à l’origine des méthodes modernes de RMN, puis, en 1991, que le Prix Nobel de Chimie a été décerné à Richard Ernst pour sa contribution au développement de méthodes de RMN à haute résolution, permettant d’optimiser l’analyse structurale de molécules organiques de complexité croissante (→).
(→) m/s 1991, n° 9, p. 987
Cependant, si la méthode s’appliquait efficacement aux molécules organiques de petite taille, elle devenait inutilisable pour les molécules de taille et de complexité plus grandes, en raison de la forte superposition des signaux et de l’incapacité de les attribuer aux différents atomes de la macromolécule.
La RMN des macromolécules biologiques en solution et Kurt Wüthrich
De nationalité suisse, Kurt Wüthrich est né le 4 octobre 1938 à Aarberg en Suisse. Il a obtenu un Diplôme de Docteur en Chimie inorganique de l’Université de Bâle (Suisse) en 1964 et est, depuis 1980, Professeur de Biophysique à l’École Polytechnique Fédérale de Zurich (Suisse) où il dirige le groupe de RMN. Titulaire à ce jour de 621 publications scientifiques dans des revues internationales, il a très tôt orienté ses travaux vers les macromolécules biologiques. Dès 1967, il se consacrait à l’étude par RMN 1H des protéines de mammifères, hémoprotéines et cytochromes. Tout en développant la méthodologie d’analyse structurale de peptides par RMN du 1H et du 13C, c’est à travers l’étude des propriétés conformationnelles d’une protéine de 56 acides aminés, un inhibiteur protéique de trypsine, le BPTI (bovine pancreatic trypsin inhibitor), que K. Wüthrich mis en route entre 1975 et 1985 les premiers travaux qui lui valent aujourd’hui ce Prix Nobel. Il développa ainsi une méthodologie qui a conduit pour la première fois en 1985 à la résolution de la structure tridimensionnelle d’une protéine en solution à partir de données de RMN [4].
Très largement employée par l’ensemble de la communauté scientifique internationale, appliquant la RMN à l’analyse des structures tridimensionnelles des macromolécules biologiques en solution, cette méthodologie utilise les techniques de RMN multidimensionnelles qui permettent de surmonter la difficulté d’interprétation de nombreux signaux superposés, propre aux polymères et aux biopolymères. Elle consiste dans un premier temps à apparier systématiquement un signal du spectre de RMN à un atome de la molécule (1H par exemple). Cette méthode nommée « attributions séquentielles » (Figure 2) utilisait initialement des expériences de RMN à deux dimensions homonucléaires utilisant le proton et portant divers acronymes (COSY, TOCSY, NOESY…). Elle a ensuite été étendue aux hétéronoyaux, 13C et 15N (HSQC, HMBC) et, par le biais de molécules enrichies en ces noyaux d’intérêt, a mis en jeu des expériences de triple résonance (HN[CO]CA, HN[COCA]CB…). Cette méthodologie est à l’origine de toutes les études structurales de macromolécules par RMN. Il est ensuite possible d’établir des relations de distances inter-protoniques, via un phénomène nommé « effet Overhauser nucléaire » (NOE) dont l’intensité reflète la proximité entre deux protons, dès lors qu’ils sont distants de moins de 5 Å. Des angles de torsion du squelette de la protéine peuvent également être déduits des paramètres RMN mesurés. Ces distances et ces angles sont alors utilisés dans des programmes de calcul, comme ceux qui ont été élaborés par K. Wüthrich et ses collaborateurs, en particulier Peter Güntert, pour calculer et reconstruire la structure tridimensionnelle de la macromolécule.
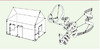 |
Figure 2. Structures tridimensionnelles. De même qu’il faut connaître toutes les dimensions d’une maison pour construire son image tridimensionnelle, en déterminant un grand nombre de courtes distances inter-atomiques dans une protéine, il est possible de créer son image, c’est-à-dire sa structure tridimensionnelle (d’après ChemChannels.com-the Nobel Prize in Chemistry). |
Il faut bien sûr souligner que les progrès méthodologiques fondamentaux établis par K. Wüthrich sont indissociables des avancées technologiques qui se sont produites dans le même temps, depuis les aimants supraconducteurs qui ont permis le développement de la RMN à haut champ (400 à 900 MHz) jusqu’aux progrès réalisés dans les nouvelles générations de calculateurs et de programmes de calcul scientifique. Ces développements parallèles ont contribué à accroître la taille des macromolécules dont les structures étaient accessibles. Des avancées constantes dans ce domaine permettent aujourd’hui d’accéder à la structure tridimensionnelle de protéines en solution de plus de 100 kDa.
Les résultats majeurs de Kurt Wüthrich
Aujourd’hui, 15 à 20 % des structures des milliers de protéines dont l’existence est connue ont été établies selon cette méthodologie. K. Wüthrich et son groupe ont ainsi élucidé les structures de plusieurs métalloprotéines, d’un inhibiteur protéique de l’α-amylase, le tendamistat, de protéines chaperons qui assurent dans les cellules la mise en place des structures tridimensionnelles d’enzymes et de protéines, de protéines membranaires de bactéries comme Escherichia coli ou bien encore de la neurotoxine du serpent Mamba noir. Il a également appliqué sa méthode aux acides nucléiques et résolu les structures tridimensionnelles de complexes résultant d’interactions moléculaires entre deux macromolécules. Ainsi, en 1991, la résolution de la structure du complexe protéique ciclosporine A/cyclophilline a été déterminante pour la compréhension du mécanisme d’action de l’un des immunosuppresseurs majeurs de notre époque, la ciclosporine, dont l’utilisation a révolutionné les greffes d’organes. Mais c’est incontestablement la structure de la protéine prion de souris, résolue en 1997 et suivie de très près par celle des prions humains et bovins en 2000, qui lui auront valu le plus grand succès [5].
À ces résultats marquants s’ajoutent de nombreux travaux purement méthodologiques concernant la RMN multidimensionnelle des principaux noyaux observables en RMN et présents dans les biomolécules (1H, 13C et 15N). Ainsi, K.Wüthrich et son groupe ont contribué, parallèlement à d’autres équipes également illustres (G. Bodenhausen, A.Gronenborn, J. Prestegard, G. Wagner, pour n’en citer que quelques-unes), à l’évolution des théories de la RMN et à l’introduction de nouveaux concepts contribuant au développement de la RMN multidimensionnelle. Ses communications ont marqué le cours et l’évolution des méthodes RMN entre 1967 et le XXIe siècle, rendant exemplaire la carrière de K. Wüthrich dont les travaux associent, en parfaite harmonie, théorie et applications.
Les développements récents de la RMN des macromolécules biologiques
Si les avancées apportées par K. Wüthrich dès 1970 ont été déterminantes pour l’analyse des structures tridimensionnelles des macromolécules biologiques en solution, il n’en reste pas moins que des développements récents liés à l’émergence de nouveaux concepts, auxquels K. Wüthrich contribue également, concourrent déjà à faire évoluer cette méthodologie fondamentale. Ainsi, la mesure des couplages dipolaires résiduels dans des milieux orientés permet de définir l’orientation des vecteurs des liaisons inter-atomiques. La détection de couplages à travers les liaisons hydrogène, interactions faibles stabilisant les structures des macromolécules, en est un autre exemple. Ces paramètres conduisent à de nouvelles données structurales, indépendantes des distances interprotoniques et des angles dièdres. À partir de données de relaxation hétéronucléaire, des études de dynamique moléculaire sont capables de désigner les régions d’une protéine associées à une plus forte mobilité. De telles approches sont exploitées pour repousser toujours plus loin les limites des méthodes utilisant la RMN au regard de la complexité des macromolécules, seules ou en interaction. Ainsi, les techniques TROSY ou CRINEPT récemment développées dans le groupe de K. Wüthrich permettent-elles d’aborder les structures de complexes protéiques dont la masse atteint 900 kDa.
Le Prix Nobel de Chimie 2002 et ses perspectives
La découverte faite par les Prix Nobel 2002 a des applications dans un très vaste ensemble de champs disciplinaires, allant de la physique et de la chimie analytique à la biologie, en passant par la pharmacologie et la médecine. Ces découvertes sont celles d’expérimentateurs et de créateurs qui ont introduit de nouvelles méthodes mais ont aussi modifié des techniques d’analyse existantes, et ceci tout en restant en prise directe avec la recherche fondamentale. Leur réussite est en particulier liée au fait qu’ils ont su intégrer un ensemble de connaissances dispersées dans un grand nombre de domaines. C’est assurément, pour tous les chercheurs et les enseignants qui pratiquent et diffusent ces méthodes, un honneur et une très grande satisfaction de voir aujourd’hui leurs applications fondamentales en biologie recevoir l’une des plus grandes récompenses de la profession. Mais au-delà, ce Prix devrait susciter un grand enthousiasme de la part des étudiants et des doctorants et les inciter à s’engager dans cette voie qui associe les mondes de la physique, de la chimie et de la biologie pour poursuivre et développer cette chaîne de découvertes, que ce soit dans l’ombre ou sous les feux du succès. Pour le siècle qui débute, la réponse aux grandes questions posées par la biologie se trouve bien à l’interface entre ces grandes et indissociables disciplines.
Références
- Tanaka K, Waki H, Ido Y, Akita S, Yoshida Y, Yoshida T. Protein and polymer analysis up to m/z 100,000 daltons by laser ionization time-offlight mass spectrometry. Rapid Comm Mass Spectrom 1988; 2: 151–3. [Google Scholar]
- Fenn JB, Mann M, Meng CK, Wong SF, Whitehouse CM. Electrospray ionization for mass spectrometry of large biomolecules. Science 1989; 246: 64–71. [Google Scholar]
- Karas, M, Hillenkamp F. Laser desorption ionization of proteins with molecular masses exceeding 10,000 daltons. Anal Chem 1988; 60: 2299–301. [Google Scholar]
- Wüthrich K. NMR of proteins and nucleic acids. New York: John Wiley and Sons, 1986. [Google Scholar]
- Lopez Garcia F, Zahn R, Riek R, Wüthrich K. NMR structure of the bovine prion protein. Proc Natl Acad Sci USA 2000; 97: 8334–39. [Google Scholar]
Liste des figures
 |
Figure 1. Principe des processus de désorption/ionisation de grosses biomolécules. A. En mode ESI (electrospray ionization), un aérosol formé à partir d’une solution est soumis à un puissant champ électrique sous pression atmosphérique pour conduire à des micro-gouttelettes fortement chargées (5+, 6+, 7+). De celles-ci, un processus d’« évaporation ionique » produit des agrégats chargés de faible énergie, libérant des biomolécules multi-chargées. B. En mode SLD (soft laser desorption), en revanche, après l’impact du rayon laser, de gros agrégats constitués de matrices neutres, mais excitées, sont produits par ablation de la surface. Lors de processus de désolvatation en cascade, ces agrégats donnent principalement des macromolécules « simplement chargées » (+, 2+). Déconvolution: transformation mathématique d’un ensemble des signaux d’états m/z, de charge z (n = z), différents (n = n protons ajoutés), tel que m/z = (M + n)/n en un signal M qui correspond à la masse moléculaire de la macrobiomolécule. Le chronomètre représente une image de la mesure du temps de vol des ions selon leur vitesse (les plus gros étant les plus lents au contraire des plus légers qui seront les plus rapides). L’ensemble des ions donne une énergie cinétique constante pour une valeur de z donnée (d’après ChemChannels.com-the Nobel Prize in Chemistry). |
| Dans le texte | |
 |
Figure 2. Structures tridimensionnelles. De même qu’il faut connaître toutes les dimensions d’une maison pour construire son image tridimensionnelle, en déterminant un grand nombre de courtes distances inter-atomiques dans une protéine, il est possible de créer son image, c’est-à-dire sa structure tridimensionnelle (d’après ChemChannels.com-the Nobel Prize in Chemistry). |
| Dans le texte | |
Current usage metrics show cumulative count of Article Views (full-text article views including HTML views, PDF and ePub downloads, according to the available data) and Abstracts Views on Vision4Press platform.
Data correspond to usage on the plateform after 2015. The current usage metrics is available 48-96 hours after online publication and is updated daily on week days.
Initial download of the metrics may take a while.




